La genética evolutiva humana estudia en qué se diferencia un genoma humano de otro genoma humano, el pasado evolutivo que dio origen al genoma humano y sus efectos actuales. Las diferencias entre genomas tienen implicaciones y aplicaciones antropológicas , médicas , históricas y forenses . Los datos genéticos pueden proporcionar importantes conocimientos sobre la evolución humana .
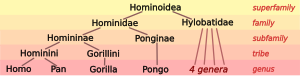
Los biólogos clasifican a los humanos , junto con algunas otras especies , como grandes simios (especies de la familia Hominidae ). Los homínidos vivos incluyen dos especies distintas de chimpancé (el bonobo , Pan paniscus , y el chimpancé , Pan troglodytes ), dos especies de gorila (el gorila occidental , Gorilla gorilla , y el gorila oriental , Gorilla graueri ), y dos especies de orangután. (el orangután de Borneo , Pongo pygmaeus , y el orangután de Sumatra , Pongo abelii ). Los grandes simios de la familia Hylobatidae de gibones forman la superfamilia Hominoidea de simios .
Los simios, a su vez, pertenecen al orden de los primates (>400 especies), junto con los monos del Viejo Mundo , los monos del Nuevo Mundo y otros. Los datos tanto del ADN mitocondrial (ADNmt) como del ADN nuclear (ADNn) indican que los primates pertenecen al grupo de Euarchontoglires , junto con Rodentia , Lagomorpha , Dermoptera y Scandentia . [1] Esto está respaldado además por elementos nucleares cortos intercalados (SINE) similares a Alu que se han encontrado solo en miembros de los Euarchontoglires. [2]
Un árbol filogenético generalmente se deriva de secuencias de ADN o proteínas de poblaciones. A menudo, el ADN mitocondrial o las secuencias del cromosoma Y se utilizan para estudiar la demografía humana antigua. Estas fuentes de ADN de locus único no se recombinan y casi siempre se heredan de un solo progenitor, con sólo una excepción conocida en el ADNmt. [3] Los individuos de regiones geográficas más cercanas generalmente tienden a ser más similares que los individuos de regiones más lejanas. La distancia en un árbol filogenético se puede utilizar aproximadamente para indicar:
La separación de los humanos de sus parientes más cercanos, los simios africanos no humanos (chimpancés y gorilas), se ha estudiado ampliamente durante más de un siglo. Se han abordado cinco cuestiones principales:
Como se mencionó anteriormente, diferentes partes del genoma muestran diferentes divergencias de secuencia entre diferentes hominoides . También se ha demostrado que la divergencia de secuencia entre el ADN de humanos y chimpancés varía mucho. Por ejemplo, la divergencia de secuencia varía entre 0% y 2,66% entre regiones genómicas no codificantes y no repetitivas de humanos y chimpancés. [8] El porcentaje de nucleótidos en el genoma humano (hg38) que tenían coincidencias exactas uno a uno en el genoma del chimpancé (pantro6) fue del 84,38%. Además, los árboles genéticos, generados mediante análisis comparativos de segmentos de ADN, no siempre se ajustan al árbol de especies. Resumiendo:
El tiempo de divergencia entre los humanos y otros simios es de gran interés. Uno de los primeros estudios moleculares, publicado en 1967, midió distancias inmunológicas (ID) entre diferentes primates. [10] Básicamente, el estudio midió la fuerza de la respuesta inmunológica que un antígeno de una especie (albúmina humana) induce en el sistema inmunológico de otra especie (humano, chimpancé, gorila y monos del Viejo Mundo ). Las especies estrechamente relacionadas deberían tener antígenos similares y, por tanto, una respuesta inmunológica más débil a los antígenos de cada una. La respuesta inmunológica de una especie a sus propios antígenos (por ejemplo, de humano a humano) se estableció en 1.
Se determinó que la identificación entre humanos y gorilas era 1,09, y entre humanos y chimpancés era 1,14. Sin embargo, la distancia a seis monos diferentes del Viejo Mundo fue en promedio 2,46, lo que indica que los simios africanos están más estrechamente relacionados con los humanos que con los monos. Los autores consideran que el tiempo de divergencia entre los monos del Viejo Mundo y los hominoides fue hace 30 millones de años (MYA), basándose en datos fósiles, y se consideró que la distancia inmunológica crecía a un ritmo constante. Llegaron a la conclusión de que el tiempo de divergencia entre los humanos y los simios africanos es de aproximadamente ~5 millones de años. Ese fue un resultado sorprendente. La mayoría de los científicos de esa época pensaban que los humanos y los grandes simios divergieron mucho antes (>15 millones de años).
El gorila estaba, en términos de identidad, más cerca de los humanos que de los chimpancés; sin embargo, la diferencia fue tan leve que la tricotomía no pudo resolverse con certeza. Estudios posteriores basados en la genética molecular lograron resolver la tricotomía: los chimpancés están filogenéticamente más cerca de los humanos que de los gorilas. Sin embargo, algunos tiempos de divergencia estimados posteriormente (utilizando métodos mucho más sofisticados en genética molecular) no difieren sustancialmente de la primera estimación de 1967, pero un artículo reciente [11] lo sitúa entre 11 y 14 millones de años.

Los métodos actuales para determinar los tiempos de divergencia utilizan alineamientos de secuencias de ADN y relojes moleculares . Por lo general, el reloj molecular se calibra suponiendo que el orangután se separó de los simios africanos (incluidos los humanos) hace 12 a 16 millones de años. Algunos estudios también incluyen algunos monos del viejo mundo y establecen el tiempo de divergencia entre ellos y los hominoides en 25-30 millones de años. Ambos puntos de calibración se basan en muy pocos datos fósiles y han sido criticados. [12]
Si se revisan estas fechas, los tiempos de divergencia estimados a partir de datos moleculares también cambiarán. Sin embargo, es poco probable que cambien los tiempos de divergencia relativa. Incluso si no podemos determinar exactamente los tiempos de divergencia absoluta, podemos estar bastante seguros de que el tiempo de divergencia entre chimpancés y humanos es aproximadamente seis veces más corto que entre chimpancés (o humanos) y monos.
Un estudio (Takahata et al. , 1995) utilizó 15 secuencias de ADN de diferentes regiones del genoma de humanos y chimpancés y 7 secuencias de ADN de humanos, chimpancés y gorilas . [13] Determinaron que los chimpancés están más estrechamente relacionados con los humanos que los gorilas. Utilizando varios métodos estadísticos, estimaron que el tiempo de divergencia entre humanos y chimpancés era de 4,7 millones de años y el tiempo de divergencia entre gorilas y humanos (y chimpancés) de 7,2 millones de años.
Además, estimaron que el tamaño efectivo de la población del ancestro común de los humanos y los chimpancés era de ~100.000. Esto fue algo sorprendente, ya que se estima que el tamaño efectivo de la población humana actual es de sólo ~10.000. De ser cierto, eso significa que el linaje humano habría experimentado una inmensa disminución del tamaño efectivo de su población (y por tanto de su diversidad genética) en su evolución. (ver teoría de la catástrofe de Toba )

Otro estudio (Chen y Li, 2001) secuenció 53 segmentos de ADN intergénicos no repetitivos de humanos, chimpancés , gorilas y orangutanes . [8] Cuando las secuencias de ADN se concatenaron en una sola secuencia larga, el árbol de unión de vecinos generado apoyó al clado Homo - Pan con un 100% de arranque (es decir, los humanos y los chimpancés son las especies relacionadas más cercanas de las cuatro). Cuando tres especies están bastante relacionadas entre sí (como humanos, chimpancés y gorilas), los árboles obtenidos a partir de los datos de la secuencia de ADN pueden no ser congruentes con el árbol que representa la especiación (árbol de especies).
Cuanto más corto es el lapso de tiempo internodal (TIN ) , más comunes son los árboles de genes incongruentes. El tamaño efectivo de la población (N e ) de la población internodal determina cuánto tiempo se conservan los linajes genéticos en la población. Un tamaño de población efectivo más alto provoca árboles genéticos más incongruentes. Por lo tanto, si se conoce el lapso de tiempo internodal, se puede calcular el tamaño poblacional efectivo ancestral del ancestro común de los humanos y los chimpancés.
Cuando cada segmento se analizó individualmente, 31 apoyaron el clado Homo - Pan , 10 apoyaron el clado Homo - Gorilla y 12 apoyaron el clado Pan - Gorilla . Utilizando el reloj molecular, los autores estimaron que los gorilas se dividieron primero entre 6,2 y 8,4 millones de años y los chimpancés y los humanos se separaron entre 1,6 y 2,2 millones de años después (lapso de tiempo internodal), entre 4,6 y 6,2 millones de años. El lapso de tiempo internodal es útil para estimar el tamaño poblacional efectivo ancestral del ancestro común de humanos y chimpancés.
Un análisis parsimonioso reveló que 24 loci apoyaban al clado Homo - Pan , 7 apoyaban al clado Homo - Gorilla , 2 apoyaban al clado Pan - Gorilla y 20 no daban resolución. Además, tomaron 35 loci codificantes de proteínas de bases de datos. De estos, 12 apoyaron al clado Homo - Pan , 3 al clado Homo - Gorilla , 4 al clado Pan - Gorilla y 16 no dieron ninguna resolución. Por lo tanto, sólo ~70% de los 52 loci que dieron una resolución (33 intergénicos, 19 codificantes de proteínas) apoyan el árbol de especies "correcto". A partir de la fracción de loci que no sustentaban la especie de árbol y el período internodal que estimaron anteriormente, se estimó que la población efectiva del ancestro común de los humanos y los chimpancés era de ~52 000 a 96 000. Este valor no es tan alto como la del primer estudio (Takahata), pero aún es mucho mayor que el tamaño efectivo de la población humana actual.
Un tercer estudio (Yang, 2002) utilizó el mismo conjunto de datos que Chen y Li, pero estimó la población efectiva ancestral de "sólo" ~12.000 a 21.000, utilizando un método estadístico diferente. [14]
Las secuencias alineables dentro de los genomas de humanos y chimpancés difieren en aproximadamente 35 millones de sustituciones de un solo nucleótido. Además, alrededor del 3% de los genomas completos se diferencian por eliminaciones, inserciones y duplicaciones. [15]
Dado que la tasa de mutación es relativamente constante, aproximadamente la mitad de estos cambios ocurrieron en el linaje humano. Sólo una fracción muy pequeña de esas diferencias fijas dio lugar a los diferentes fenotipos de humanos y chimpancés y encontrarlas es un gran desafío. La gran mayoría de las diferencias son neutrales y no afectan el fenotipo . [ cita necesaria ]
La evolución molecular puede actuar de diferentes maneras, a través de la evolución de proteínas, la pérdida de genes, la regulación diferencial de genes y la evolución del ARN. Se cree que todos jugaron algún papel en la evolución humana.
Muchas mutaciones diferentes pueden inactivar un gen, pero pocas cambiarán su función de una manera específica. Por lo tanto, las mutaciones de inactivación estarán fácilmente disponibles para que la selección actúe sobre ellas. Por tanto, la pérdida de genes podría ser un mecanismo común de adaptación evolutiva (la hipótesis de "menos es más"). [dieciséis]
80 genes se perdieron en el linaje humano tras la separación del último ancestro común con el chimpancé. 36 de ellos eran para receptores olfativos . Los genes implicados en la quimiorrecepción y la respuesta inmune están sobrerrepresentados. [17] Otro estudio estimó que se habían perdido 86 genes. [18]
Un gen para la queratina capilar tipo I se perdió en el linaje humano. Las queratinas son un componente importante de los cabellos. Los seres humanos todavía tienen nueve genes funcionales de queratina capilar tipo I, pero la pérdida de ese gen en particular puede haber causado el adelgazamiento del cabello corporal humano. Basado en el supuesto de un reloj molecular constante, el estudio predice que la pérdida de genes ocurrió relativamente recientemente en la evolución humana, hace menos de 240.000 años, pero tanto la secuencia de Vindija Neandertal como la de Denisovan de alta cobertura contienen los mismos codones de parada prematuros que los modernos. humanos y, por tanto, la datación debería ser superior a hace 750.000 años. [19]
Stedman et al. (2004) afirmaron que la pérdida del gen sarcomérico de miosina MYH16 en el linaje humano condujo a músculos masticatorios más pequeños . Estimaron que la mutación que condujo a la inactivación (una deleción de dos pares de bases) ocurrió hace 2,4 millones de años, antes de la aparición del Homo ergaster /erectus en África. El período que siguió estuvo marcado por un fuerte aumento en la capacidad craneal , lo que promovió la especulación de que la pérdida del gen pudo haber eliminado una limitación evolutiva sobre el tamaño del cerebro en el género Homo . [20]
Otra estimación de la pérdida del gen MYH16 es hace 5,3 millones de años, mucho antes de que apareciera el Homo . [21]
Las duplicaciones segmentarias (SD o LCR ) han desempeñado un papel en la creación de nuevos genes de primates y en la configuración de la variación genética humana.
Cuando se comparó el genoma humano con los genomas de cinco especies de primates de comparación, incluidos el chimpancé , el gorila , el orangután , el gibón y el macaco, se descubrió que hay aproximadamente 20.000 inserciones específicas de humanos que se cree que son reguladoras. Si bien la mayoría de las inserciones parecen ser neutrales en términos de aptitud física, se ha identificado una pequeña cantidad en genes seleccionados positivamente que muestran asociaciones con fenotipos neuronales y algunos se relacionan con fenotipos relacionados con la percepción dental y sensorial. Estos hallazgos apuntan al papel aparentemente importante de las inserciones específicas de humanos en la reciente evolución de los humanos. [22]
Las regiones aceleradas humanas son áreas del genoma que difieren entre humanos y chimpancés en mayor medida de lo que puede explicarse por la deriva genética a lo largo del tiempo desde que las dos especies compartieron un ancestro común. Estas regiones muestran signos de estar sujetas a la selección natural, lo que lleva a la evolución de rasgos claramente humanos. Dos ejemplos son HAR1F , que se cree que está relacionado con el desarrollo del cerebro, y HAR2 (también conocido como HACNS1 ), que puede haber desempeñado un papel en el desarrollo del pulgar oponible .
También se ha planteado la hipótesis de que gran parte de la diferencia entre humanos y chimpancés es atribuible a la regulación de la expresión genética más que a diferencias en los genes mismos. Los análisis de secuencias no codificantes conservadas , que a menudo contienen regiones reguladoras funcionales y, por tanto, seleccionadas positivamente, abordan esta posibilidad. [23]
Cuando se publicó el borrador de la secuencia del genoma del chimpancé común ( Pan troglodytes ) en el verano de 2005, se secuenciaron y ensamblaron 2.400 millones de bases (de ~3.160 millones de bases) lo suficientemente bien como para compararlas con el genoma humano. [15] El 1,23% de estos secuenciados difirieron por sustituciones de una sola base. De esto, se pensaba que el 1,06% o menos representaba diferencias fijas entre las especies, y el resto eran sitios variantes en humanos o chimpancés. Otro tipo de diferencia, llamado indeles (inserciones/eliminaciones) representó muchas menos diferencias (15% más), pero contribuyó con ~1,5% de la secuencia única de cada genoma, ya que cada inserción o eliminación puede involucrar desde una base hasta millones de bases. [15]
Un artículo complementario examinó las duplicaciones segmentarias en los dos genomas, [24] cuya inserción y eliminación en el genoma representan gran parte de la secuencia indel. Descubrieron que un total del 2,7% de la secuencia eucromática se había duplicado diferencialmente en uno u otro linaje.
La secuencia de divergencia tiene generalmente el siguiente patrón: Humano-Chimpancé < Humano-Gorila << Humano-Orangután, destacando el estrecho parentesco entre los humanos y los simios africanos. Los elementos Alu divergen rápidamente debido a su alta frecuencia de dinucleótidos CpG que mutan aproximadamente 10 veces más a menudo que el nucleótido promedio en el genoma. La tasa de mutación es mayor en la línea germinal masculina , por lo que la divergencia en el cromosoma Y —que se hereda únicamente del padre— es mayor que en los autosomas . El cromosoma X se hereda dos veces más a través de la línea germinal femenina que a través de la línea germinal masculina y, por lo tanto, muestra una divergencia de secuencia ligeramente menor. La divergencia de secuencia de la región Xq13.3 es sorprendentemente baja entre humanos y chimpancés. [25]
Las mutaciones que alteran la secuencia de aminoácidos de las proteínas (K a ) son las menos comunes. De hecho, ~29% de todas las proteínas ortólogas son idénticas entre humanos y chimpancés. La proteína típica se diferencia sólo en dos aminoácidos. [15] Las medidas de divergencia de secuencia que se muestran en la tabla solo tienen en cuenta las diferencias de sustitución, por ejemplo de una A ( adenina ) a una G ( guanina ). Sin embargo, las secuencias de ADN también pueden diferir mediante inserciones y eliminaciones ( indeles ) de bases. Por lo general, estos se eliminan de las alineaciones antes de realizar el cálculo de la divergencia de secuencia.
Un grupo internacional de científicos completó un borrador de secuencia del genoma neandertal en mayo de 2010. Los resultados indican cierta reproducción entre los humanos modernos ( Homo sapiens ) y los neandertales ( Homo neanderthalensis ) , ya que los genomas de los humanos no africanos tienen entre un 1% y un 4% más. en común con los neandertales que los genomas de los africanos subsaharianos. Los neandertales y la mayoría de los humanos modernos comparten una variante intolerante a la lactosa del gen de la lactasa que codifica una enzima que es incapaz de descomponer la lactosa en la leche después del destete. Los humanos modernos y los neandertales también comparten la variante del gen FOXP2 asociada con el desarrollo del cerebro y con el habla en los humanos modernos, lo que indica que los neandertales podrían haber podido hablar. Los chimpancés tienen dos diferencias de aminoácidos en FOXP2 en comparación con el FOXP2 humano y neandertal. [26] [27] [28]
Se cree que el Homo sapiens surgió hace unos 300.000 años. Se dispersó por África y, hace 70.000 años, por Eurasia y Oceanía. Un estudio de 2009 identificó 14 "grupos de población ancestrales", siendo el más remoto el pueblo san del sur de África. [29] [30]
Con su rápida expansión por diferentes zonas climáticas, y especialmente con la disponibilidad de nuevas fuentes de alimentos con la domesticación del ganado y el desarrollo de la agricultura , las poblaciones humanas han estado expuestas a importantes presiones selectivas desde su dispersión. Por ejemplo, se cree que los antepasados de los asiáticos orientales se sometieron a procesos de selección para varios alelos, incluidas variantes de los genes EDAR , ADH1B , ABCC1 y ALDH2 .
Los tipos de ADH1B del este de Asia en particular están asociados con la domesticación del arroz y, por lo tanto, habrían surgido después del desarrollo del cultivo de arroz hace aproximadamente 10.000 años. [31] Varios rasgos fenotípicos característicos de los asiáticos orientales se deben a una única mutación del gen EDAR , que data de c. Hace 35.000 años. [32]
En 2017 [update], la base de datos de polimorfismo de nucleótido único ( dbSNP ), que enumera SNP y otras variantes, enumeró un total de 324 millones de variantes encontradas en genomas humanos secuenciados. [33] La diversidad de nucleótidos , la proporción promedio de nucleótidos que difieren entre dos individuos, se estima entre 0,1% y 0,4% para los humanos contemporáneos (en comparación con el 2% entre humanos y chimpancés). [34] [35] Esto corresponde a diferencias genómicas en unos pocos millones de sitios; El Proyecto 1000 Genomas encontró de manera similar que "un genoma [individual] típico difiere del genoma humano de referencia en 4,1 millones a 5,0 millones de sitios... afectando 20 millones de bases de secuencia". [36]
En febrero de 2019, los científicos descubrieron evidencia, basada en estudios genéticos que utilizan inteligencia artificial (IA), que sugieren la existencia de una especie ancestral humana desconocida, no neandertal , denisovana o híbrida humana (como Denny (hominino híbrido) ), en el genoma de humanos modernos . [37] [38]
En marzo de 2019, científicos chinos informaron que habían insertado el gen MCPH1 relacionado con el cerebro humano en monos rhesus de laboratorio , lo que resultó en que los monos transgénicos tuvieran un mejor desempeño y respondieran más rápido en "pruebas de memoria a corto plazo que involucraban combinar colores y formas", en comparación con los controles no transgénicos. monos, según los investigadores. [39] [40]
En mayo de 2023, los científicos informaron, basándose en estudios genéticos, de una vía de evolución humana más complicada de lo que se creía anteriormente. Según los estudios, los humanos evolucionaron en diferentes lugares y épocas de África, en lugar de un único lugar y período de tiempo. [41] [42]
El 31 de agosto de 2023, los investigadores informaron, basándose en estudios genéticos, que se produjo un cuello de botella en la población de ancestros humanos "hace alrededor de 930.000 y 813.000 años... duró unos 117.000 años y llevó a los ancestros humanos al borde de la extinción". [43] [44]
{{cite journal}}: CS1 maint: numeric names: authors list (link)