El diseño de fármacos , a menudo denominado diseño racional de fármacos o simplemente diseño racional , es el proceso inventivo de encontrar nuevos medicamentos basándose en el conocimiento de un objetivo biológico . [1] El fármaco suele ser una pequeña molécula orgánica que activa o inhibe la función de una biomolécula como una proteína , lo que a su vez resulta en un beneficio terapéutico para el paciente . En el sentido más básico, el diseño de fármacos implica el diseño de moléculas que sean complementarias en forma y carga con respecto al objetivo biomolecular con el que interactúan y, por lo tanto, se unirán a él. El diseño de fármacos se basa con frecuencia, pero no necesariamente, en técnicas de modelado por computadora . [2] Este tipo de modelado a veces se denomina diseño de fármacos asistido por computadora . Finalmente, el diseño de fármacos que se basa en el conocimiento de la estructura tridimensional de la diana biomolecular se conoce como diseño de fármacos basado en la estructura . [2] Además de las moléculas pequeñas, los productos biofarmacéuticos , incluidos los péptidos [3] [4] y especialmente los anticuerpos terapéuticos, son una clase de fármacos cada vez más importante y también se han desarrollado métodos computacionales para mejorar la afinidad, la selectividad y la estabilidad de estas terapias basadas en proteínas. desarrollado. [5]
La frase "diseño de fármaco" es similar al diseño de ligando (es decir, diseño de una molécula que se unirá firmemente a su objetivo). [6] Aunque las técnicas de diseño para la predicción de la afinidad de unión son razonablemente exitosas, hay muchas otras propiedades, como la biodisponibilidad , la vida media metabólica y los efectos secundarios , que primero deben optimizarse antes de que un ligando pueda convertirse en un fármaco seguro y eficaz. Estas otras características suelen ser difíciles de predecir con técnicas de diseño racional.
Debido a las altas tasas de deserción, especialmente durante las fases clínicas del desarrollo de fármacos , se está centrando más atención en las primeras etapas del proceso de diseño de fármacos en la selección de fármacos candidatos cuyas propiedades fisicoquímicas se predice que darán como resultado menos complicaciones durante el desarrollo y, por lo tanto, es más probable que conduzcan a una aprobación. , fármaco comercializado. [7] Además, los experimentos in vitro complementados con métodos de computación se utilizan cada vez más en el descubrimiento temprano de fármacos para seleccionar compuestos con ADME (absorción, distribución, metabolismo y excreción) y perfiles toxicológicos más favorables. [8]
Una diana biomolecular (más comúnmente una proteína o un ácido nucleico ) es una molécula clave involucrada en una vía metabólica o de señalización particular que está asociada con una enfermedad o patología específica o con la infectividad o supervivencia de un patógeno microbiano . Los posibles objetivos farmacológicos no necesariamente causan enfermedades, pero, por definición, deben modificarlas. [9] En algunos casos, se diseñarán moléculas pequeñas para mejorar o inhibir la función objetivo en la vía de modificación de la enfermedad específica. Se diseñarán moléculas pequeñas (por ejemplo, agonistas , antagonistas , agonistas inversos o moduladores de receptores ; activadores o inhibidores de enzimas; o abridores o bloqueadores de canales iónicos ) [10] que sean complementarias al sitio de unión del objetivo. [11] Las moléculas pequeñas (medicamentos) se pueden diseñar de manera que no afecten a otras moléculas importantes "fuera del objetivo" (a menudo denominadas antiobjetivos ), ya que las interacciones farmacológicas con moléculas fuera del objetivo pueden provocar efectos secundarios indeseables . [12] Debido a las similitudes en los sitios de unión, los objetivos estrechamente relacionados identificados mediante homología de secuencia tienen la mayor probabilidad de reactividad cruzada y, por lo tanto, el mayor potencial de efectos secundarios.
Por lo general, los medicamentos son pequeñas moléculas orgánicas producidas mediante síntesis química, pero los medicamentos basados en biopolímeros (también conocidos como biofarmacéuticos ) producidos mediante procesos biológicos son cada vez más comunes. [13] Además, las tecnologías de silenciamiento de genes basadas en ARNm pueden tener aplicaciones terapéuticas. [14] Por ejemplo, las nanomedicinas basadas en ARNm pueden agilizar y acelerar el proceso de desarrollo de fármacos, permitiendo la expresión transitoria y localizada de moléculas inmunoestimulantes. [15] El ARNm transcrito in vitro (IVT) permite la entrega a varios tipos de células accesibles a través de la sangre o vías alternativas. El uso de ARNm de IVT sirve para transmitir información genética específica a las células de una persona, con el objetivo principal de prevenir o alterar una enfermedad en particular. [dieciséis]
El descubrimiento de fármacos fenotípicos es un método tradicional de descubrimiento de fármacos, también conocido como farmacología avanzada o farmacología clásica. Utiliza el proceso de detección fenotípica en colecciones de pequeñas moléculas sintéticas, productos naturales o extractos dentro de bibliotecas químicas para identificar sustancias que exhiben efectos terapéuticos beneficiosos. Este método consiste en descubrir primero la actividad funcional in vivo o in vitro de los fármacos (como extractos de fármacos o productos naturales) y luego realizar la identificación del objetivo. El descubrimiento fenotípico utiliza un enfoque práctico e independiente del objetivo para generar pistas iniciales, con el objetivo de descubrir compuestos farmacológicamente activos y terapias que operen a través de nuevos mecanismos farmacológicos. [17] Este método permite la exploración de fenotipos de enfermedades para encontrar tratamientos potenciales para afecciones con orígenes desconocidos, complejos o multifactoriales, donde la comprensión de los objetivos moleculares es insuficiente para una intervención eficaz. [18]
El diseño racional de fármacos (también llamado farmacología inversa ) comienza con la hipótesis de que la modulación de un objetivo biológico específico puede tener valor terapéutico. Para seleccionar una biomolécula como objetivo de un fármaco, se requieren dos datos esenciales. La primera es la evidencia de que la modulación del objetivo modificará la enfermedad. Este conocimiento puede provenir, por ejemplo, de estudios de vinculación de enfermedades que muestran una asociación entre mutaciones en el objetivo biológico y ciertos estados patológicos. [19] La segunda es que el objetivo es capaz de unirse a una molécula pequeña y que su actividad puede ser modulada por la molécula pequeña. [20]
Una vez que se ha identificado una diana adecuada, la diana normalmente se clona , se produce y se purifica . La proteína purificada se utiliza luego para establecer un ensayo de detección . Además, se puede determinar la estructura tridimensional del objetivo.
La búsqueda de moléculas pequeñas que se unan al objetivo se inicia mediante la selección de bibliotecas de posibles compuestos farmacológicos. Esto se puede hacer utilizando el ensayo de detección (una "pantalla húmeda"). Además, si se dispone de la estructura del objetivo, se podrá realizar un cribado virtual de los fármacos candidatos. Idealmente, los compuestos farmacológicos candidatos deberían ser " similares a los fármacos ", es decir, deberían poseer propiedades que se predice que conduzcan a una biodisponibilidad oral , una estabilidad química y metabólica adecuada y efectos tóxicos mínimos. [21] Hay varios métodos disponibles para estimar la semejanza con los medicamentos, como la regla de cinco de Lipinski , y una variedad de métodos de puntuación, como la eficiencia lipófila . [22] En la literatura científica también se han propuesto varios métodos para predecir el metabolismo de los fármacos. [23]
Debido a la gran cantidad de propiedades de los fármacos que deben optimizarse simultáneamente durante el proceso de diseño, a veces se emplean técnicas de optimización multiobjetivo . [24] Finalmente, debido a las limitaciones de los métodos actuales para la predicción de la actividad, el diseño de fármacos todavía depende en gran medida de la casualidad [25] y la racionalidad limitada . [26]
El objetivo más fundamental en el diseño de fármacos es predecir si una molécula determinada se unirá a un objetivo y, de ser así, con qué fuerza. La mecánica molecular o la dinámica molecular se utiliza con mayor frecuencia para estimar la fuerza de la interacción intermolecular entre la molécula pequeña y su objetivo biológico. Estos métodos también se utilizan para predecir la conformación de la molécula pequeña y para modelar los cambios conformacionales en el objetivo que pueden ocurrir cuando la molécula pequeña se une a él. [3] [4] Los métodos semiempíricos de química cuántica ab initio o la teoría funcional de la densidad se utilizan a menudo para proporcionar parámetros optimizados para los cálculos de la mecánica molecular y también proporcionar una estimación de las propiedades electrónicas (potencial electrostático, polarizabilidad , etc.) del fármaco candidato que influirá en la afinidad de unión. [27]
También se pueden utilizar métodos de mecánica molecular para proporcionar una predicción semicuantitativa de la afinidad de unión. Además, se puede utilizar una función de puntuación basada en conocimientos para proporcionar estimaciones de afinidad vinculantes. Estos métodos utilizan regresión lineal , aprendizaje automático , redes neuronales u otras técnicas estadísticas para derivar ecuaciones de afinidad de unión predictivas ajustando afinidades experimentales a energías de interacción derivadas computacionalmente entre la molécula pequeña y el objetivo. [28] [29]
Idealmente, el método computacional será capaz de predecir la afinidad antes de que se sintetice un compuesto y, por lo tanto, en teoría solo es necesario sintetizar un compuesto, lo que ahorrará una enorme cantidad de tiempo y costos. La realidad es que los métodos computacionales actuales son imperfectos y proporcionan, en el mejor de los casos, sólo estimaciones de afinidad cualitativamente precisas. En la práctica, se requieren varias iteraciones de diseño, síntesis y pruebas antes de descubrir un fármaco óptimo. Los métodos computacionales han acelerado el descubrimiento al reducir el número de iteraciones necesarias y, a menudo, han proporcionado estructuras novedosas. [30] [31]
El diseño de fármacos asistido por computadora se puede utilizar en cualquiera de las siguientes etapas del descubrimiento de fármacos:

Para superar la predicción insuficiente de la afinidad de unión calculada mediante funciones de puntuación recientes, se utilizan para el análisis la interacción proteína-ligando y la información de la estructura 3D del compuesto. Para el diseño de fármacos basado en la estructura, se han desarrollado varios análisis posteriores a la selección centrados en la interacción proteína-ligando para mejorar el enriquecimiento y extraer eficazmente candidatos potenciales:
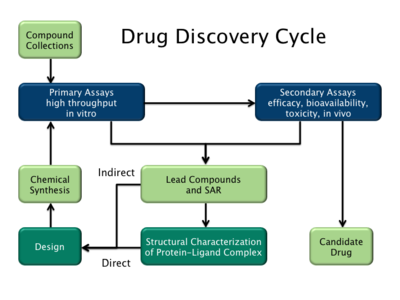
Hay dos tipos principales de diseño de fármacos. El primero se conoce como diseño de fármacos basado en ligandos y el segundo, diseño de fármacos basado en estructuras. [2]
El diseño de fármacos basado en ligandos (o diseño indirecto de fármacos ) se basa en el conocimiento de otras moléculas que se unen al objetivo biológico de interés. Estas otras moléculas se pueden utilizar para derivar un modelo de farmacóforo que defina las características estructurales mínimas necesarias que debe poseer una molécula para unirse al objetivo. [36] Se puede construir un modelo del objetivo biológico basándose en el conocimiento de lo que se une a él y este modelo, a su vez, se puede utilizar para diseñar nuevas entidades moleculares que interactúen con el objetivo. Alternativamente, se puede derivar una relación cuantitativa estructura-actividad (QSAR), en la que se puede derivar una correlación entre las propiedades calculadas de las moléculas y su actividad biológica determinada experimentalmente. Estas relaciones QSAR, a su vez, pueden usarse para predecir la actividad de nuevos análogos. [37]
El diseño de fármacos basado en la estructura (o diseño directo de fármacos ) se basa en el conocimiento de la estructura tridimensional del objetivo biológico obtenido mediante métodos como la cristalografía de rayos X o la espectroscopia de RMN . [38] Si no se dispone de una estructura experimental de un objetivo, es posible crear un modelo de homología del objetivo basado en la estructura experimental de una proteína relacionada. Utilizando la estructura del objetivo biológico, se pueden diseñar fármacos candidatos que se predice que se unirán con alta afinidad y selectividad al objetivo utilizando gráficos interactivos y la intuición de un químico medicinal . Alternativamente, se pueden utilizar varios procedimientos computacionales automatizados para sugerir nuevos fármacos candidatos. [39]
Los métodos actuales para el diseño de fármacos basados en estructuras se pueden dividir aproximadamente en tres categorías principales. [40] El primer método es la identificación de nuevos ligandos para un receptor determinado mediante la búsqueda en grandes bases de datos de estructuras 3D de moléculas pequeñas para encontrar aquellas que se ajusten al bolsillo de unión del receptor utilizando programas rápidos de acoplamiento aproximado . Este método se conoce como cribado virtual .
Una segunda categoría es el diseño de novo de nuevos ligandos. En este método, las moléculas de ligando se construyen dentro de las limitaciones del bolsillo de unión ensamblando piezas pequeñas de manera gradual. Estas piezas pueden ser átomos individuales o fragmentos moleculares. La ventaja clave de este método es que se pueden sugerir estructuras novedosas, que no están contenidas en ninguna base de datos. [41] [42] [43] Un tercer método es la optimización de ligandos conocidos mediante la evaluación de análogos propuestos dentro de la cavidad de unión. [40]
La identificación del sitio de unión es el primer paso en el diseño basado en estructuras. [20] [44] Si la estructura de la diana o de un homólogo suficientemente similar se determina en presencia de un ligando unido, entonces el ligando debe ser observable en la estructura, en cuyo caso la ubicación del sitio de unión es trivial. Sin embargo, puede haber sitios de unión alostéricos desocupados que puedan ser de interés. Además, puede ser que solo estén disponibles estructuras de apoproteína (proteína sin ligando) y la identificación confiable de sitios desocupados que tienen el potencial de unirse a ligandos con alta afinidad no sea trivial. En resumen, la identificación del sitio de unión generalmente se basa en la identificación de superficies cóncavas en la proteína que pueden acomodar moléculas del tamaño de un fármaco que también poseen "puntos calientes" apropiados ( superficies hidrófobas , sitios de enlace de hidrógeno , etc.) que impulsan la unión del ligando. [20] [44]
El diseño de fármacos basado en la estructura intenta utilizar la estructura de las proteínas como base para diseñar nuevos ligandos aplicando los principios del reconocimiento molecular . Generalmente es deseable la unión selectiva de alta afinidad al objetivo, ya que conduce a fármacos más eficaces con menos efectos secundarios. Por tanto, uno de los principios más importantes para diseñar u obtener nuevos ligandos potenciales es predecir la afinidad de unión de un determinado ligando a su objetivo (y a sus antiobjetivos conocidos ) y utilizar la afinidad predicha como criterio de selección. [45]
Böhm desarrolló una de las primeras funciones de puntuación empírica de propósito general para describir la energía de unión de los ligandos a los receptores. [46] [47] Esta función de puntuación empírica tomó la forma:
dónde:
Una ecuación "maestra" termodinámica más general es la siguiente: [48]
dónde:
La idea básica es que la energía libre de enlace general se puede descomponer en componentes independientes que se sabe que son importantes para el proceso de enlace. Cada componente refleja un cierto tipo de alteración de la energía libre durante el proceso de unión entre un ligando y su receptor objetivo. La ecuación maestra es la combinación lineal de estos componentes. Según la ecuación de energía libre de Gibbs, se construyó la relación entre la constante de equilibrio de disociación, Kd, y los componentes de la energía libre .
Se utilizan varios métodos computacionales para estimar cada uno de los componentes de la ecuación maestra. Por ejemplo, el cambio en el área de la superficie polar tras la unión del ligando se puede utilizar para estimar la energía de desolvatación. El número de enlaces giratorios congelados tras la unión del ligando es proporcional al término de movimiento. La energía configuracional o de deformación se puede estimar mediante cálculos de mecánica molecular . Finalmente, la energía de interacción se puede estimar utilizando métodos como el cambio en la superficie no polar, los potenciales de fuerza media derivados estadísticamente , el número de enlaces de hidrógeno formados, etc. En la práctica, los componentes de la ecuación maestra se ajustan a los datos experimentales utilizando múltiples regresión lineal. Esto se puede hacer con un conjunto de entrenamiento diverso que incluya muchos tipos de ligandos y receptores para producir un modelo "global" menos preciso pero más general o un conjunto más restringido de ligandos y receptores para producir un modelo "local" más preciso pero menos general. [49]
Un ejemplo particular de diseño racional de fármacos implica el uso de información tridimensional sobre biomoléculas obtenida a partir de técnicas como la cristalografía de rayos X y la espectroscopia de RMN. El diseño de fármacos asistido por ordenador, en particular, se vuelve mucho más manejable cuando existe una estructura de alta resolución de una proteína objetivo unida a un ligando potente. Este enfoque para el descubrimiento de fármacos a veces se denomina diseño de fármacos basado en estructuras. El primer ejemplo inequívoco de la aplicación del diseño de un fármaco basado en la estructura que condujo a un fármaco aprobado es el inhibidor de la anhidrasa carbónica dorzolamida , que fue aprobado en 1995. [50] [51]
Otro estudio de caso sobre diseño racional de fármacos es el imatinib , un inhibidor de la tirosina quinasa diseñado específicamente para la proteína de fusión bcr-abl que es característica de las leucemias con cromosoma Filadelfia positivo ( leucemia mielógena crónica y ocasionalmente leucemia linfocítica aguda ). Imatinib es sustancialmente diferente de los medicamentos anteriores para el cáncer , ya que la mayoría de los agentes de quimioterapia simplemente se dirigen a las células que se dividen rápidamente, sin diferenciar entre células cancerosas y otros tejidos. [52]
Ejemplos adicionales incluyen:
Los tipos de detección de drogas incluyen detección fenotípica , detección de alto rendimiento y detección virtual . La detección fenotípica se caracteriza por el proceso de detección de fármacos utilizando modelos de enfermedades celulares o animales para identificar compuestos que alteran el fenotipo y producen efectos beneficiosos relacionados con la enfermedad. [54] [55] Las tecnologías emergentes en detección de alto rendimiento mejoran sustancialmente la velocidad de procesamiento y disminuyen el volumen de detección requerido. [56] La detección virtual se realiza por computadora, lo que permite detectar una gran cantidad de moléculas con un ciclo corto y de bajo costo. El cribado virtual utiliza una variedad de métodos computacionales que permiten a los químicos reducir extensas bibliotecas virtuales a tamaños más manejables. [57]
Se ha argumentado que la naturaleza altamente rígida y centrada del diseño racional de fármacos suprime la casualidad en el descubrimiento de fármacos. [58]