
Las proteínas de fusión o proteínas quiméricas (kī-ˈmir-ik) (literalmente, hechas de partes de diferentes fuentes) son proteínas creadas a través de la unión de dos o más genes que originalmente codificaron proteínas separadas. La traducción de este gen de fusión da como resultado uno o varios polipéptidos con propiedades funcionales derivadas de cada una de las proteínas originales. Las proteínas de fusión recombinantes se crean artificialmente mediante tecnología de ADN recombinante para su uso en investigación biológica o terapéutica . Quimérico o quimera generalmente designa proteínas híbridas hechas de polipéptidos que tienen diferentes funciones o patrones fisicoquímicos. Las proteínas mutantes quiméricas ocurren naturalmente cuando una mutación compleja , como una translocación cromosómica , duplicación en tándem o retrotransposición crea una nueva secuencia codificante que contiene partes de las secuencias codificantes de dos genes diferentes. Las proteínas de fusión naturales se encuentran comúnmente en células cancerosas, donde pueden funcionar como oncoproteínas . La proteína de fusión bcr-abl es un ejemplo bien conocido de proteína de fusión oncogénica y se considera el principal impulsor oncogénico de la leucemia mielógena crónica .
Algunas proteínas de fusión combinan péptidos enteros y, por lo tanto, contienen todos los dominios funcionales de las proteínas originales. Sin embargo, otras proteínas de fusión, especialmente las que se producen de forma natural, combinan solo partes de secuencias codificantes y, por lo tanto, no mantienen las funciones originales de los genes parentales que las formaron.
Muchas fusiones de genes completos son completamente funcionales y aún pueden actuar para reemplazar los péptidos originales. Sin embargo, algunas experimentan interacciones entre las dos proteínas que pueden modificar sus funciones. Más allá de estos efectos, algunas fusiones de genes pueden causar cambios regulatorios que alteran cuándo y dónde actúan estos genes. En el caso de las fusiones de genes parciales , la combinación de diferentes sitios activos y dominios de unión tiene el potencial de dar como resultado nuevas proteínas con funciones novedosas.

La fusión de etiquetas fluorescentes a proteínas en una célula huésped es una técnica muy popular que se utiliza en la investigación experimental de células y biología para rastrear las interacciones de proteínas en tiempo real. La primera etiqueta fluorescente, la proteína fluorescente verde (GFP), se aisló de Aequorea victoria y todavía se utiliza con frecuencia en la investigación moderna. Las derivaciones más recientes incluyen proteínas fluorescentes fotoconvertibles (PCFP), que se aislaron por primera vez de Anthozoa . La PCFP más utilizada es la etiqueta fluorescente Kaede , pero el desarrollo de Kikume verde-rojo (KikGR) en 2005 ofrece una señal más brillante y una fotoconversión más eficiente. La ventaja de utilizar etiquetas fluorescentes PCFP es la capacidad de rastrear la interacción de vías bioquímicas superpuestas en tiempo real. La etiqueta cambiará de color de verde a rojo una vez que la proteína alcance un punto de interés en la vía, y la proteína de color alternativo se puede monitorear a lo largo de la duración de la vía. Esta técnica es especialmente útil cuando se estudian las vías de reciclaje del receptor acoplado a proteína G (GPCR). Los destinos de los receptores de proteína G reciclados pueden enviarse a la membrana plasmática para ser reciclados, marcados con una etiqueta fluorescente verde, o pueden enviarse a un lisosoma para su degradación, marcados con una etiqueta fluorescente roja. [1]
El objetivo de crear proteínas de fusión en el desarrollo de fármacos es transmitir las propiedades de cada una de las proteínas "progenitoras" a la proteína quimérica resultante. Actualmente existen varios fármacos con proteínas quiméricas disponibles para uso médico.
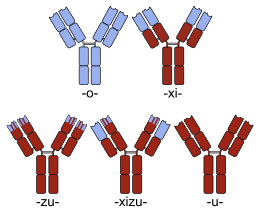
Muchos fármacos proteínicos quiméricos son anticuerpos monoclonales cuya especificidad para una molécula diana se desarrolló utilizando ratones y, por lo tanto, inicialmente eran anticuerpos "de ratón". Como proteínas no humanas, los anticuerpos de ratón tienden a provocar una reacción inmunitaria si se administran a humanos. El proceso de quimerización implica la ingeniería del reemplazo de segmentos de la molécula de anticuerpo que la distinguen de un anticuerpo humano. Por ejemplo, se pueden introducir dominios constantes humanos, eliminando así la mayoría de las porciones potencialmente inmunogénicas del fármaco sin alterar su especificidad para el objetivo terapéutico previsto. La nomenclatura de los anticuerpos indica este tipo de modificación insertando -xi- en el nombre común (p. ej., abci- xi -mab ). Si partes de los dominios variables también se reemplazan por porciones humanas, se obtienen anticuerpos humanizados . Aunque no son conceptualmente distintos de las quimeras, este tipo se indica utilizando -zu- como en dacli- zu -mab . Consulte la lista de anticuerpos monoclonales para obtener más ejemplos.
Además de los anticuerpos quiméricos y humanizados, existen otros usos farmacéuticos para la creación de construcciones quiméricas. Etanercept , por ejemplo, es un bloqueador del TNFα creado mediante la combinación de un receptor del factor de necrosis tumoral (TNFR) con el segmento Fc de inmunoglobulina G 1 . El TNFR proporciona especificidad para el objetivo del fármaco y se cree que el segmento Fc del anticuerpo añade estabilidad y capacidad de administración del fármaco. [2] Otras proteínas quiméricas utilizadas para aplicaciones terapéuticas incluyen:
Una proteína de fusión recombinante es una proteína creada mediante ingeniería genética de un gen de fusión. Esto generalmente implica eliminar el codón de terminación de una secuencia de ADNc que codifica la primera proteína y luego agregar la secuencia de ADNc de la segunda proteína en el marco de lectura mediante ligadura o PCR de extensión superpuesta . Luego, esa secuencia de ADN será expresada por una célula como una sola proteína. La proteína puede diseñarse para incluir la secuencia completa de ambas proteínas originales o solo una parte de una de ellas.
Si las dos entidades son proteínas, a menudo también se añaden péptidos enlazadores (o "espaciadores"), lo que hace más probable que las proteínas se plieguen de forma independiente y se comporten como se espera. Especialmente en el caso en que los enlazadores permiten la purificación de proteínas , los enlazadores en fusiones de proteínas o péptidos a veces se diseñan con sitios de escisión para proteasas o agentes químicos que permiten la liberación de las dos proteínas separadas. Esta técnica se utiliza a menudo para la identificación y purificación de proteínas, mediante la fusión de una proteína GST , un péptido FLAG o un péptido hexa-his (6xHis-tag), que se puede aislar mediante cromatografía de afinidad con resinas de níquel o cobalto. Las proteínas quiméricas di- o multiméricas se pueden fabricar a través de ingeniería genética mediante la fusión a las proteínas originales de dominios peptídicos que inducen la di- o multimerización artificial de proteínas (p. ej., cremalleras de estreptavidina o leucina ). Las proteínas de fusión también se pueden fabricar con toxinas o anticuerpos unidos a ellas para estudiar el desarrollo de enfermedades. Se estudió el promotor de la hidrogenasa, P SH , construyendo una fusión promotor P SH - gfp utilizando el gen reportero de la proteína fluorescente verde ( gfp) . [3]
Las nuevas tecnologías recombinantes han hecho posible mejorar el diseño de proteínas de fusión para su uso en campos tan diversos como la biodetección, las industrias papelera y alimentaria y los productos biofarmacéuticos. Las mejoras recientes han implicado la fusión de péptidos individuales o fragmentos de proteínas con regiones de proteínas existentes, como los extremos N y C , y se sabe que aumentan las siguientes propiedades: [4]
Las primeras aplicaciones del diseño de proteínas recombinantes se pueden documentar en el uso de etiquetas de péptidos individuales para la purificación de proteínas en cromatografía de afinidad . Desde entonces, se han desarrollado diversas técnicas de diseño de proteínas de fusión para aplicaciones tan diversas como las etiquetas de proteínas fluorescentes y los fármacos de proteínas de fusión recombinantes. Tres técnicas de diseño comúnmente utilizadas incluyen la fusión en tándem, la inserción de dominios y la conjugación postraduccional. [5]
Las proteínas de interés se conectan de manera sencilla de extremo a extremo mediante la fusión de los extremos N o C entre las proteínas. Esto proporciona una estructura de puente flexible que permite suficiente espacio entre los socios de fusión para garantizar un plegamiento adecuado . Sin embargo, los extremos N o C del péptido suelen ser componentes cruciales para obtener el patrón de plegamiento deseado para la proteína recombinante, lo que hace que la simple unión de dominios de extremo a extremo sea ineficaz en este caso. Por esta razón, a menudo se necesita un enlazador de proteínas para mantener la funcionalidad de los dominios proteicos de interés. [5]
Esta técnica implica la fusión de dominios proteicos consecutivos mediante la codificación de las estructuras deseadas en una única cadena polipeptídica, pero a veces puede requerir la inserción de un dominio dentro de otro dominio. Esta técnica suele considerarse más difícil de llevar a cabo que la fusión en tándem, debido a la dificultad de encontrar un sitio de ligación adecuado en el gen de interés. [5]
Esta técnica fusiona dominios proteicos después de la traducción ribosómica de las proteínas de interés, a diferencia de la fusión genética previa a la traducción utilizada en otras tecnologías recombinantes. [5]

Los ligadores de proteínas ayudan al diseño de proteínas de fusión al proporcionar un espaciado adecuado entre dominios, lo que favorece el plegamiento correcto de las proteínas en el caso de que las interacciones entre los extremos N y C sean cruciales para el plegamiento. Por lo general, los ligadores de proteínas permiten interacciones importantes entre dominios, refuerzan la estabilidad y reducen el impedimento estérico, lo que los hace preferidos para su uso en el diseño de proteínas de fusión incluso cuando los extremos N y C se pueden fusionar. Los tres tipos principales de ligadores son flexibles, rígidos y escindibles in vivo. [5] [6]
Los genes de fusión que se producen de forma natural se crean con mayor frecuencia cuando una translocación cromosómica reemplaza los exones terminales de un gen con exones intactos de un segundo gen. Esto crea un único gen que se puede transcribir , empalmar y traducir para producir una proteína de fusión funcional. Muchos oncogenes importantes que promueven el cáncer son genes de fusión producidos de esta manera.
Algunos ejemplos incluyen:
Los anticuerpos son proteínas de fusión producidas por recombinación V(D)J .
También hay ejemplos raros de polipéptidos naturales que parecen ser una fusión de dos módulos claramente definidos, en los que cada módulo muestra su actividad o función característica, independientemente del otro. Dos ejemplos principales son: la quimera doble PP2C en Plasmodium falciparum (el parásito de la malaria), en la que cada módulo PP2C exhibe actividad enzimática de la proteína fosfatasa 2C, [7] y las inmunofilinas de doble familia que se producen en varios organismos unicelulares (como los parásitos protozoarios y las flavobacterias ) y que contienen módulos de ciclofilina y chaperonas FKBP de longitud completa . [8] [9] El origen evolutivo de dicha quimera sigue sin estar claro.