El daño al ADN es una alteración en la estructura química del ADN , como una rotura en una hebra de ADN, una nucleobase que falta en la columna vertebral del ADN o una base químicamente cambiada como la 8-OHdG . El daño al ADN puede ocurrir de forma natural o a través de factores ambientales, pero es claramente diferente de la mutación , aunque ambos son tipos de error en el ADN . El daño del ADN es una estructura química anormal del ADN, mientras que una mutación es un cambio en la secuencia de pares de bases. Los daños en el ADN provocan cambios en la estructura del material genético e impiden que el mecanismo de replicación funcione y funcione correctamente. [1] La respuesta al daño del ADN (DDR) es una vía compleja de transducción de señales que reconoce cuándo el ADN está dañado e inicia la respuesta celular al daño. [2]
El daño y la mutación del ADN tienen diferentes consecuencias biológicas. Si bien la mayoría de los daños en el ADN pueden sufrir reparación , dicha reparación no es 100% eficiente. Los daños no reparados en el ADN se acumulan en células que no se replican, como las células del cerebro o los músculos de los mamíferos adultos, y pueden provocar el envejecimiento. [3] [4] [5] (Consulte también la teoría del envejecimiento del daño al ADN ). En las células en replicación, como las células que recubren el colon, se producen errores durante la replicación de daños pasados en la cadena plantilla de ADN o durante la reparación de daños en el ADN. Estos errores pueden dar lugar a mutaciones o alteraciones epigenéticas . [6] Ambos tipos de alteración pueden replicarse y transmitirse a generaciones celulares posteriores. Estas alteraciones pueden cambiar la función genética o la regulación de la expresión genética y posiblemente contribuir a la progresión al cáncer.
A lo largo del ciclo celular existen varios puntos de control para garantizar que la célula esté en buenas condiciones para progresar hacia la mitosis. Los tres puntos de control principales se encuentran en G1/s, G2/m y en el punto de control del conjunto del husillo que regula la progresión a través de la anafase. Los puntos de control G1 y G2 implican la exploración de ADN dañado. [7] Durante la fase S, la célula es más vulnerable al daño del ADN que cualquier otra parte del ciclo celular. El punto de control G2 comprueba el ADN dañado y la integridad de la replicación del ADN.
El daño al ADN que ocurre naturalmente puede ser el resultado de procesos metabólicos o hidrolíticos . El metabolismo libera compuestos que dañan el ADN, incluidas especies reactivas de oxígeno , especies reactivas de nitrógeno , especies reactivas de carbonilo , productos de peroxidación lipídica y agentes alquilantes , entre otros, mientras que la hidrólisis escinde los enlaces químicos en el ADN. [8] Los daños oxidativos del ADN que ocurren naturalmente surgen al menos 10.000 veces por célula por día en humanos y hasta 100.000 por célula por día en ratas [9] como se documenta a continuación.
El daño oxidativo del ADN puede producir más de 20 tipos de bases alteradas [10] [11] , así como roturas de una sola cadena. [12]
Otros tipos de daños endógenos en el ADN, que se detallan a continuación con sus frecuencias de aparición, incluyen depurinaciones , despirimidinas , roturas de doble cadena , O6-metilguaninas y desaminación de citosina .
El ADN también puede dañarse a través de factores ambientales. Agentes ambientales como la luz ultravioleta, la radiación ionizante y los productos químicos genotóxicos. Las bifurcaciones de replicación pueden detenerse debido a un ADN dañado y las roturas de doble cadena también son una forma de daño al ADN. [13]
La siguiente lista muestra algunas frecuencias con las que cada día surgen nuevos daños naturales en el ADN, debido a procesos celulares endógenos.
Otro daño endógeno importante al ADN es M1dG , abreviatura de (3-(2'-desoxi-beta-D-eritro-pentofuranosil)-pirimido[1,2-a]-purin-10(3H)-ona). La excreción en orina (que probablemente refleja la tasa de aparición) de M1dG puede ser hasta 1000 veces menor que la de 8-oxodG. [26] Sin embargo, una medida más importante puede ser el nivel de estado estacionario en el ADN, que refleja tanto la tasa de aparición como la tasa de reparación del ADN. El nivel en estado estacionario de M1dG es mayor que el de 8-oxodG. [27] Esto señala que algunos daños en el ADN producidos a un ritmo bajo pueden ser difíciles de reparar y permanecer en el ADN en un nivel alto en estado estable. Tanto M1dG [28] como 8-oxodG [29] son mutagénicos .
Los niveles de daños en el ADN en estado estacionario representan el equilibrio entre la formación y la reparación. Se han caracterizado más de 100 tipos de daño oxidativo del ADN, y el 8-oxodG constituye aproximadamente el 5% de los daños oxidativos en estado estacionario del ADN. [18] Helbock et al. [14] estimaron que había 24.000 aductos de ADN oxidativo en estado estacionario por célula en ratas jóvenes y 66.000 aductos por célula en ratas viejas. Esto refleja la acumulación de daño en el ADN con la edad. La acumulación de daño en el ADN con la edad se describe con más detalle en la teoría del envejecimiento del daño en el ADN .
Swenberg et al. [30] midieron cantidades promedio de daños seleccionados en el ADN endógeno en estado estacionario en células de mamíferos. Los siete daños más comunes que evaluaron se muestran en la Tabla 1.
Al evaluar los daños en estado estacionario en tejidos específicos de la rata, Nakamura y Swenberg [31] indicaron que el número de sitios abásicos variaba desde aproximadamente 50.000 por célula en el hígado, riñón y pulmón hasta aproximadamente 200.000 por célula en el cerebro.
Las proteínas que promueven el daño endógeno del ADN se identificaron en un artículo de 2019 como proteínas de "daño" del ADN (DDP). [32] Los mecanismos DDP se dividen en tres grupos:
Los homólogos humanos del DDP están sobrerrepresentados en los factores causantes del cáncer conocidos, y sus ARN en los tumores predicen una fuerte mutagénesis y un mal pronóstico. [32]
En presencia de daño en el ADN, la célula puede reparar el daño o inducir la muerte celular si el daño no se puede reparar.
En esta tabla se muestran los siete tipos principales de reparación del ADN y una vía de tolerancia al daño, las lesiones que abordan y la precisión de la reparación (o tolerancia). Para obtener una breve descripción de los pasos de la reparación, consulte Mecanismos de reparación del ADN o consulte cada vía individual.

El diagrama esquemático indica el papel de la reparación insuficiente del ADN en el envejecimiento y el cáncer, y el papel de la apoptosis en la prevención del cáncer. Un exceso de daño natural en el ADN, debido a deficiencias hereditarias, en particular las enzimas reparadoras del ADN, puede causar envejecimiento prematuro o un mayor riesgo de cáncer (consulte Trastorno por deficiencia de reparación del ADN ). Por otro lado, la capacidad de desencadenar la apoptosis en presencia de un exceso de daño en el ADN no reparado es fundamental para la prevención del cáncer. [42]
Las proteínas reparadoras del ADN a menudo se activan o inducen cuando el ADN ha sufrido daños. Sin embargo, el daño excesivo del ADN puede iniciar la apoptosis (es decir, la muerte celular programada) si el nivel de daño del ADN excede la capacidad de reparación. La apoptosis puede evitar que las células con exceso de daño en el ADN sufran mutagénesis y progresen hacia el cáncer. [43]
La inflamación suele ser causada por una infección, como por ejemplo con el virus de la hepatitis B (VHB), el virus de la hepatitis C (VHC) o el Helicobacter pylori . La inflamación crónica también es una característica central de la obesidad. [44] [45] [46] [47] Dicha inflamación causa daño oxidativo al ADN. Esto se debe a la inducción de especies reactivas de oxígeno (ROS) por varios mediadores inflamatorios intracelulares. [48] [49] [50] Las infecciones por VHB y VHC, en particular, causan aumentos de 10 000 y 100 000 veces en la producción intracelular de ROS, respectivamente. [51] Las ROS inducidas por inflamación que causan daño al ADN pueden desencadenar la apoptosis, [52] [53] pero también pueden causar cáncer si los procesos de reparación y apoptosis no son lo suficientemente protectores. [45]
Los ácidos biliares , almacenados en la vesícula biliar, se liberan en el intestino delgado en respuesta a la grasa de la dieta. Los niveles más altos de grasa provocan una mayor liberación. [54] Los ácidos biliares causan daño al ADN, incluido daño oxidativo del ADN, roturas de la doble hebra del ADN, aneuploidía y rotura cromosómica. [55] Los niveles normales altos del ácido biliar desoxicólico causan apoptosis en las células del colon humano, [56] pero también pueden provocar cáncer de colon si la reparación y las defensas apoptóticas son insuficientes. [57]
La apoptosis sirve como mecanismo de salvaguardia contra la tumorigénesis. [58] Previene el aumento de la mutagénesis que el exceso de daño en el ADN podría causar durante la replicación. [59]
Al menos 17 proteínas reparadoras del ADN, distribuidas en cinco vías de reparación del ADN, tienen una "doble función" en respuesta al daño del ADN. Con niveles moderados de daño al ADN, estas proteínas inician o contribuyen a la reparación del ADN. Sin embargo, cuando hay niveles excesivos de daño en el ADN, se desencadena la apoptosis. [43]
El empaquetamiento del ADN eucariota en cromatina es una barrera para todos los procesos basados en el ADN que requieren acción enzimática. Para la mayoría de los procesos de reparación del ADN, es necesario remodelar la cromatina . En los eucariotas, los complejos de remodelación de la cromatina dependientes de ATP y las enzimas modificadoras de histonas son dos factores que actúan para lograr este proceso de remodelación después de que se produce un daño en el ADN. [60] Generalmente siguen más pasos de reparación del ADN, que involucran múltiples enzimas. A continuación se describen algunas de las primeras respuestas al daño del ADN, con su calendario. Se presentan descripciones más completas de las vías de reparación del ADN en artículos que describen cada vía. Al menos 169 enzimas participan en las vías de reparación del ADN. [61]
Las bases oxidadas del ADN se producen en células tratadas con tinte Hoechst seguido de microirradiación con luz de 405 nm. [62] Estas bases oxidadas se pueden reparar mediante reparación por escisión de la base .
Cuando la luz de 405 nm se enfoca a lo largo de una línea estrecha dentro del núcleo de una célula, aproximadamente 2,5 segundos después de la irradiación, la enzima remodeladora de la cromatina Alc1 alcanza la mitad del reclutamiento máximo en la microlínea irradiada. [63] La línea de cromatina que se irradió luego se relaja y se expande de lado a lado durante los siguientes 60 segundos. [63]
A los 6 segundos de la irradiación con luz de 405 nm, se produce la mitad del reclutamiento máximo de OGG1 en la línea irradiada. [62] OGG1 es una enzima que elimina el daño oxidativo del ADN 8-oxo-dG del ADN. La eliminación de 8-oxo-dG, durante la reparación por escisión de la base, se produce con una vida media de 11 minutos. [18]
La luz ultravioleta (UV) induce la formación de daños en el ADN, incluidos dímeros de pirimidina (como los dímeros de timina) y fotoproductos 6,4. Este tipo de daños "voluminosos" se reparan mediante reparación por escisión de nucleótidos .
Después de la irradiación con luz ultravioleta, DDB2 , en un complejo con DDB1 , la proteína ubiquitina ligasa CUL4A y la proteína de dedo RING ROC1, se asocia con sitios de daño dentro de la cromatina. La asociación media máxima se produce en 40 segundos. [64] PARP1 también se asocia dentro de este período. [65] La proteína PARP1 se une tanto a DDB1 como a DDB2 y luego PARila (crea una cadena de poli-ADP ribosa) en DDB2 que atrae a la proteína remodeladora del ADN ALC1 . [65] ALC1 relaja la cromatina en los sitios de daño UV al ADN. Además, el complejo de ubiquitina E3 ligasa DDB1-CUL4A lleva a cabo la ubiquitinación de las histonas centrales H2A, H3 y H4, así como de la proteína reparadora XPC, que ha sido atraída al sitio del daño en el ADN. [66] XPC, tras la ubiquitinación, se activa e inicia la vía de reparación por escisión de nucleótidos . Algo más tarde, 30 minutos después del daño causado por los rayos UV, el complejo de remodelación de la cromatina INO80 se recluta en el sitio del daño del ADN, y esto coincide con la unión de otras proteínas reparadoras de escisión de nucleótidos, incluida ERCC1 . [67]
Las roturas de doble hebra (DSB) en sitios específicos se pueden inducir transfectando células con un plásmido que codifica la endonucleasa I-SceI (una endonucleasa homing ). Se pueden inducir múltiples DSB irradiando células sensibilizadas (marcadas con 5'-bromo-2'-desoxiuridina y con tinte Hoechst) con luz de 780 nm. Estos DSB pueden repararse mediante la reparación recombinante homóloga precisa o mediante la vía de reparación de unión de extremos no homóloga menos precisa . Aquí describimos los primeros pasos en la reparación recombinacional homóloga (HRR).
Después de tratar las células para introducir DSB, la proteína quinasa activada por estrés, la quinasa N-terminal c-Jun (JNK) , fosforila SIRT6 en la serina 10. [68] Esta modificación postraduccional facilita la movilización de SIRT6 a los sitios de daño del ADN con la mitad -Reclutamiento máximo en menos de un segundo. [68] Se requiere SIRT6 en el sitio para el reclutamiento eficiente de la poli (ADP-ribosa) polimerasa 1 (PARP1) en un sitio de rotura del ADN y para la reparación eficiente de DSB. [68] La proteína PARP1 comienza a aparecer en los DSB en menos de un segundo, con una acumulación máxima de la mitad dentro de 1,6 segundos después de que se produce el daño. [69] Esto permite el reclutamiento máximo a la mitad de las enzimas reparadoras del ADN MRE11 en 13 segundos y NBS1 en 28 segundos. [69] MRE11 y NBS1 llevan a cabo los primeros pasos de la vía HRR.
γH2AX, la forma fosforilada de H2AX , también participa en los primeros pasos de la reparación de DSB. La variante de histona H2AX constituye aproximadamente el 10% de las histonas H2A en la cromatina humana. [70] γH2AX (H2AX fosforilado en serina 139) se puede detectar tan pronto como 20 segundos después de la irradiación de las células (con formación de rotura de la doble cadena del ADN), y la mitad de la acumulación máxima de γH2AX ocurre en un minuto. [70] La extensión de la cromatina con γH2AX fosforilado es de aproximadamente dos millones de pares de bases en el sitio de una rotura de la doble hebra del ADN. [70] γH2AX por sí solo no causa la descondensación de la cromatina, pero dentro de los 30 segundos posteriores a la irradiación, la proteína RNF8 se puede detectar en asociación con γH2AX. [71] RNF8 media la descondensación extensa de la cromatina, a través de su interacción posterior con CHD4 , [72] un componente de la remodelación del nucleosoma y el complejo de desacetilasa NuRD .
Después de una rápida remodelación de la cromatina , se pueden activar puntos de control del ciclo celular para permitir que se complete la reparación del ADN antes de que avance el ciclo celular. Primero, dos quinasas , ATM y ATR , se activan dentro de los 5 o 6 minutos posteriores al daño del ADN. A esto le sigue la fosforilación de la proteína Chk1 del punto de control del ciclo celular , iniciando su función, aproximadamente 10 minutos después de que se daña el ADN. [73]
El daño al ADN 8-oxo-dG no ocurre al azar en el genoma. En fibroblastos embrionarios de ratón , se encontró un enriquecimiento de 2 a 5 veces de 8-oxo-dG en regiones de control genético, incluidos promotores , regiones 5' no traducidas y regiones 3' no traducidas en comparación con los niveles de 8-oxo-dG encontrados en el gen cuerpos y en regiones intergénicas . [74] En células endoteliales de la arteria pulmonar de rata, cuando se examinaron 22.414 genes codificadores de proteínas en busca de ubicaciones de 8-oxo-dG, la mayoría de los 8-oxo-dG (cuando estaban presentes) se encontraron en regiones promotoras en lugar de dentro de cuerpos genéticos. [75] Entre cientos de genes cuyos niveles de expresión se vieron afectados por la hipoxia, aquellos con el promotor 8-oxo-dG recién adquirido estaban regulados al alza , y aquellos genes cuyos promotores perdieron 8-oxo-dG estaban casi todos regulados a la baja . [75]
Según lo revisado por Wang et al., [76] la guanina oxidada parece tener múltiples funciones reguladoras en la expresión genética. En particular, cuando el estrés oxidativo produce 8-oxo-dG en el promotor de un gen, el estrés oxidativo también puede inactivar OGG1 , una enzima que se dirige a 8-oxo-dG y normalmente inicia la reparación del daño de 8-oxo-dG. El OGG1 inactivo, que ya no escinde 8-oxo-dG, sin embargo se dirige y forma complejos con 8-oxo-dG y provoca una curvatura pronunciada (~70 o ) en el ADN. Esto permite el ensamblaje de un complejo de iniciación transcripcional, que regula positivamente la transcripción del gen asociado. [76] [77]
Cuando se forma 8-oxo-dG en una secuencia potencial formadora de cuádruplex G (PQS) rica en guanina en la cadena codificante de un promotor, el OGG1 activo escinde el 8-oxo-dG y genera un sitio apurínico/apirimidínico (sitio AP). ). El sitio AP permite la fusión del dúplex para desenmascarar el PQS, adoptando un pliegue cuádruplex G (estructura/motivo G4) que tiene un papel regulador en la activación de la transcripción. [76] [78]
Cuando el 8-oxo-dG forma un complejo con OGG1 activo, puede reclutar remodeladores de cromatina para modular la expresión génica. La proteína de unión al ADN cromodominio helicasa 4 (CHD4) , un componente del complejo (NuRD) , es reclutada por OGG1 en los sitios de daño oxidativo del ADN. Luego, CHD4 atrae el ADN y las enzimas metilantes de histonas que reprimen la transcripción de los genes asociados. [76]
La oxidación de guanina, particularmente dentro de los sitios CpG , puede ser especialmente importante en el aprendizaje y la memoria. La metilación de citosinas ocurre en 60 a 90% de los sitios CpG, según el tipo de tejido. [79] En el cerebro de los mamíferos, ~62% de los CpG están metilados. [79] La metilación de sitios CpG tiende a silenciar genes de forma estable. [80] Más de 500 de estos sitios CpG se desmetilan en el ADN de las neuronas durante la formación y consolidación de la memoria en las regiones del hipocampo [81] [82] y la corteza cingulada [82] del cerebro. Como se indica a continuación, el primer paso en la desmetilación de la citosina metilada en un sitio CpG es la oxidación de la guanina para formar 8-oxo-dG.
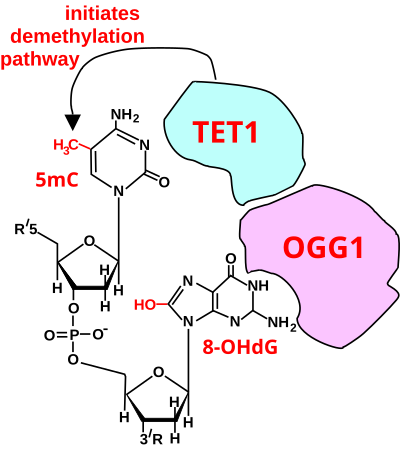
La figura de esta sección muestra un sitio CpG donde la citosina se metila para formar 5-metilcitosina (5 mC) y la guanina se oxida para formar 8-oxo-2'-desoxiguanosina (en la figura, esto se muestra en la forma tautomérica 8- OHdG). Cuando se forma esta estructura, la enzima reparadora de escisión de bases OGG1 se dirige a 8-OHdG y se une a la lesión sin escisión inmediata. OGG1, presente en un sitio de 5mCp-8-OHdG, recluta TET1 , y TET1 oxida el 5mC adyacente al 8-OHdG. Esto inicia la desmetilación de 5 mC. [83] TET1 es una enzima clave involucrada en la desmetilación de 5mCpG. Sin embargo, TET1 solo es capaz de actuar sobre 5mCpG si la guanina se oxidó primero para formar 8-hidroxi-2'-desoxiguanosina (8-OHdG o su tautómero 8-oxo-dG), lo que da como resultado un dinucleótido de 5mCp-8-OHdG ( ver figura en esta sección). [83] Esto inicia la vía de desmetilación de la citosina metilada, lo que finalmente da como resultado una citosina no metilada (consulte Oxidación del ADN para conocer más pasos en la formación de citosina no metilada).
La expresión alterada de proteínas en las neuronas, debido a cambios en la metilación del ADN (probablemente controlada por la desmetilación dependiente de 8-oxo-dG de los sitios CpG en los promotores de genes dentro del ADN de las neuronas) se ha establecido como fundamental para la formación de la memoria. [84]
Las roturas de doble cadena (DSB) en regiones del ADN relacionadas con la actividad neuronal se producen mediante una variedad de mecanismos dentro y alrededor del genoma. La enzima topoisomerasa II , o TOPIIβ, desempeña un papel clave en la formación de DSB al ayudar en la desmetilación o aflojamiento de las histonas envueltas alrededor de la doble hélice para promover la transcripción . [85] Una vez que se abre la estructura de la cromatina, es más probable que se acumulen DSB; sin embargo, esto normalmente lo repara TOPIIβ a través de su capacidad intrínseca de religación que vuelve a unir los extremos del ADN escindido. [85]
La falla de TOPIIβ en la religasa puede tener consecuencias drásticas en la síntesis de proteínas, donde se estima que "el bloqueo de la actividad de TOPIIβ altera la expresión de casi un tercio de todos los genes regulados por el desarrollo", como los genes neuronales tempranos inmediatos (IEG) involucrados en la consolidación de la memoria. . [85] [86] Se ha observado una expresión rápida de egr-1 , c-Fos y Arc IEG en respuesta al aumento de la actividad neuronal en la región del hipocampo del cerebro donde tiene lugar el procesamiento de la memoria. [87] Como medida preventiva contra el fallo de TOPIIβ, las moléculas de reparación DSB se reclutan a través de dos vías diferentes: factores de la vía de unión de extremos no homólogos (NHEJ), que realizan una función de religación similar a la de TOPIIβ, y la recombinación homóloga (HR). vía, que utiliza la cadena hermana no rota como plantilla para reparar la cadena dañada de ADN. [85] [88]
La estimulación de la actividad neuronal, como se mencionó anteriormente en la expresión de IEG, es otro mecanismo a través del cual se generan DSB. Los cambios en el nivel de actividad se han utilizado en estudios como biomarcador para rastrear la superposición entre los DSB y el aumento de la metilación de la histona H3K4 en las regiones promotoras de los IEG. [85] [88] Otros estudios han indicado que los elementos transponibles (TE) pueden causar DSB a través de una actividad endógena que implica el uso de enzimas endonucleasas para insertar y escindir el ADN objetivo en sitios aleatorios. [89] [90]
Si bien la acumulación de DSB generalmente inhibe la consolidación de la memoria a largo plazo , el proceso de reconsolidación , por el contrario, depende de DSB. La reconsolidación de la memoria implica la modificación de recuerdos existentes almacenados en la memoria a largo plazo. [91] La investigación que involucra NPAS4 , un gen que regula la neuroplasticidad en el hipocampo durante el aprendizaje contextual y la formación de la memoria, ha revelado un vínculo entre las eliminaciones en la región codificante y las deficiencias en la evocación de recuerdos de miedo en ratas transgénicas. [85] Además, la enzima H3K4me3, que cataliza la desmetilación de la histona H3K4, se reguló positivamente en la región promotora del gen NPAS4 durante el proceso de reconsolidación, mientras que la desactivación (eliminación del gen) de la misma enzima impidió la reconsolidación. [85] Se observó un efecto similar en TOPIIβ, donde la caída también afectó la respuesta de la memoria de miedo en ratas, lo que indica que los DSB, junto con las enzimas que los regulan, influyen en la formación de la memoria en múltiples etapas.
La acumulación de DSB conduce en términos más generales a la degeneración de las neuronas, lo que dificulta la función de la memoria y los procesos de aprendizaje. Debido a su falta de división celular y su alta actividad metabólica , las neuronas son especialmente propensas a sufrir daños en el ADN. [88] Además, un desequilibrio de las DSB y las moléculas de reparación del ADN para los genes de actividad neuronal se ha relacionado con el desarrollo de diversas enfermedades neurodegenerativas humanas , incluidas la enfermedad de Alzheimer (EA), la enfermedad de Parkinson (EP) y la esclerosis lateral amiotrófica (ELA). [88] En pacientes con enfermedad de Alzheimer, los DSB se acumulan en las neuronas en las primeras etapas y son la fuerza impulsora detrás de la pérdida de memoria, una característica clave de la enfermedad. [88] Otros factores externos que resultan en mayores niveles de DSB dependientes de la actividad en personas con EA son el daño oxidativo a las neuronas, que puede resultar en más DSB cuando ocurren múltiples lesiones cerca unas de otras. Los factores ambientales como los virus y una dieta rica en grasas también se han asociado con la función alterada de las moléculas de reparación del ADN.
Una terapia dirigida para el tratamiento de pacientes con EA ha implicado la supresión del gen BRCA1 en cerebros humanos, inicialmente probada en ratones transgénicos, donde se observó que los niveles de DSB habían aumentado y se había producido pérdida de memoria, lo que sugiere que BRCA1 podría "servir como un objetivo terapéutico para la enfermedad de Alzheimer". EA y demencia relacionada con la EA”. [88] De manera similar, la proteína ATM involucrada en la reparación del ADN y las modificaciones epigenéticas del genoma se correlaciona positivamente con la pérdida neuronal en los cerebros con EA, lo que indica que la proteína es otro componente clave en los procesos intrínsecamente relacionados de neurodegeneración, producción de DSB y formación de memoria. [88]
La mayoría de los daños se pueden reparar sin activar el sistema de respuesta al daño; sin embargo, los daños más complejos activan ATR y ATM, proteínas quinasas clave en el sistema de respuesta al daño. [92] El daño al ADN inhibe las M-CDK, que son un componente clave de la progresión hacia la mitosis .
En todas las células eucariotas, ATR y ATM son proteínas quinasas que detectan daños en el ADN. Se unen a sitios dañados del ADN y activan Chk1 , Chk2 y, en células animales, p53 . Juntas, estas proteínas forman el sistema de respuesta al daño del ADN. Algunos daños en el ADN no requieren el reclutamiento de ATR y ATM; sólo son daños difíciles y extensos que requieren ATR y ATM. ATM y ATR son necesarios para NHEJ, HR, reparación de ICL y NER, así como para la estabilidad de la horquilla de replicación durante la replicación del ADN sin perturbaciones y en respuesta a los bloques de replicación. [2]
ATR se recluta para diferentes formas de daño, como daño de nucleótidos, horquillas de replicación detenidas y roturas de doble cadena. ATM es específicamente para la respuesta al daño causado por roturas de doble hilo. El complejo MRN (compuesto por Mre11, Rad50 y Nbs1) se forma inmediatamente en el sitio de rotura de la doble cadena. Este complejo MRN recluta cajeros automáticos en el lugar del daño. ATR y ATM fosforilan diversas proteínas que contribuyen al sistema de reparación de daños. La unión de ATR y ATM a los sitios dañados del ADN conduce al reclutamiento de Chk1 y Chk2. Estas proteínas quinasas envían señales de daño al sistema de control del ciclo celular para retrasar la progresión del ciclo celular. [13]
Chk1 conduce a la producción de enzimas reparadoras del ADN. Chk2 conduce a una detención reversible del ciclo celular. Chk2, así como ATR/ATM, pueden activar p53, lo que conduce a una detención permanente del ciclo celular o apoptosis.
Cuando hay demasiado daño, se desencadena la apoptosis para proteger al organismo de células potencialmente dañinas.7 p53, también conocido como gen supresor de tumores, es una proteína reguladora importante en el sistema de respuesta al daño del ADN que se une directamente a los promotores de sus genes diana. p53 actúa principalmente en el punto de control G1 (que controla la transición de G1 a S), donde bloquea la progresión del ciclo celular. [7] La activación de p53 puede desencadenar la muerte celular o la detención permanente del ciclo celular. p53 también puede activar ciertas vías de reparación como NER. [92]
En ausencia de daño en el ADN, p53 está regulado por Mdm2 y se degrada constantemente. Cuando hay daño en el ADN, Mdm2 se fosforila, probablemente causado por ATM. La fosforilación de Mdm2 conduce a una reducción de la actividad de Mdm2, impidiendo así la degradación de p53. Las células normales y no dañadas generalmente tienen niveles bajos de p53, mientras que las células bajo estrés y daño en el ADN tendrán niveles altos de p53. [13]
p53 sirve como factor de transcripción tanto para bax , una proteína proapoptótica, como para p21 , un inhibidor de CDK. Los inhibidores de CDK provocan la detención del ciclo celular. Detener la célula le da tiempo a la célula para reparar el daño y, si el daño es irreparable, p53 recluta a bax para desencadenar la apoptosis. [92]
p53 es un actor clave en el crecimiento de células cancerosas. Las células de ADN dañadas con p53 mutado tienen un mayor riesgo de volverse cancerosas. Los tratamientos de quimioterapia comunes son genotóxicos. Estos tratamientos son ineficaces en tumores cancerosos que han mutado p53 ya que no tienen un p53 funcional para detener o matar la célula dañada.
Un indicio de que los daños en el ADN son un problema importante para la vida es que se han encontrado procesos de reparación del ADN para hacer frente a los daños en el ADN en todos los organismos celulares en los que se ha investigado la reparación del ADN. Por ejemplo, en las bacterias, se ha encontrado en muchas especies bacterianas una red reguladora destinada a reparar los daños en el ADN (llamada respuesta SOS en Escherichia coli ). E. coli RecA, una enzima clave en la vía de respuesta SOS, es el miembro definitorio de una clase ubicua de proteínas de intercambio de cadenas de ADN que son esenciales para la recombinación homóloga, una vía que mantiene la integridad genómica mediante la reparación del ADN roto. [93] Los genes homólogos a RecA y a otros genes centrales en la vía de respuesta SOS se encuentran en casi todos los genomas bacterianos secuenciados hasta la fecha, cubriendo una gran cantidad de filos, lo que sugiere tanto un origen antiguo como una ocurrencia generalizada de reparación recombinacional del ADN. daño. [94] Las recombinasas eucariotas que son homólogas de RecA también están muy extendidas en los organismos eucariotas. Por ejemplo, en levaduras de fisión y humanos, los homólogos de RecA promueven el intercambio de cadenas de ADN dúplex-dúplex necesario para la reparación de muchos tipos de lesiones del ADN. [95] [96]
Otro indicio de que los daños en el ADN son un problema importante para la vida es que las células realizan grandes inversiones en los procesos de reparación del ADN. Como señaló Hoeijmakers, [4] reparar una sola rotura de doble hebra podría requerir más de 10.000 moléculas de ATP , como se utiliza para señalar la presencia del daño, la generación de focos de reparación y la formación (en humanos) del RAD51. nucleofilamento (un intermedio en la reparación recombinante homóloga). (RAD51 es un homólogo de RecA bacteriano). Si la modificación estructural ocurre durante la fase G1 de la replicación del ADN, el punto de control G1-S detiene o pospone el avance del ciclo celular antes de que el producto entre en la fase S. [1]
Las células somáticas diferenciadas de los mamíferos adultos generalmente se replican con poca frecuencia o no se replican en absoluto. Estas células, incluidas, por ejemplo, las neuronas cerebrales y los miocitos musculares, tienen poco o ningún recambio celular. Las células que no se replican generalmente no generan mutaciones debido a errores de replicación inducidos por daños en el ADN. Estas células que no se replican no suelen dar lugar a cáncer, pero acumulan daños en el ADN con el tiempo que probablemente contribuyen al envejecimiento ( ). En una célula que no se replica, una rotura de una sola hebra u otro tipo de daño en la hebra de ADN transcrita puede bloquear la transcripción catalizada por la ARN polimerasa II. [97] Esto interferiría con la síntesis de la proteína codificada por el gen en el que se produjo el bloqueo.
Brasnjevic et al. [98] resumieron la evidencia que muestra que las roturas de una sola hebra se acumulan con la edad en el cerebro (aunque la acumulación difería en diferentes regiones del cerebro) y que las roturas de una sola hebra son los daños más frecuentes al ADN en estado estacionario en el cerebro. Como se analizó anteriormente, se esperaría que estas roturas monocatenarias acumuladas bloquearan la transcripción de genes. De acuerdo con esto, según lo revisado por Hetman et al., [99] se identificaron 182 genes y se demostró que tenían una transcripción reducida en los cerebros de personas mayores de 72 años, en comparación con la transcripción en los cerebros de aquellos menores de 43 años. Cuando se evaluaron 40 proteínas particulares en un músculo de ratas, la mayoría de las proteínas mostraron disminuciones significativas durante el envejecimiento desde los 18 meses (rata madura) hasta los 30 meses (rata envejecida) de edad. [100]
Se demostró que otro tipo de daño en el ADN, la rotura de la doble cadena, provoca la muerte celular (pérdida de células) mediante apoptosis . [101] Este tipo de daño en el ADN no se acumularía con la edad, ya que una vez que una célula se perdiera por apoptosis, su daño de doble cadena se perdería con ella. Por lo tanto, los segmentos de ADN dañados socavan la maquinaria de replicación del ADN porque estas secuencias alteradas de ADN no pueden utilizarse como verdaderas plantillas para producir copias del propio material genético. [1]
Cuando el ADN se daña, la célula responde de varias maneras para reparar el daño y minimizar los efectos en la célula. Una de esas respuestas, específicamente en las células eucariotas, es retrasar la división celular: la célula queda detenida durante algún tiempo en la fase G2 antes de avanzar por el resto del ciclo celular. Se han realizado varios estudios para dilucidar el propósito de esta detención de G2 inducida por daño en el ADN. Los investigadores han descubierto que las células que son expulsadas prematuramente del retraso tienen una menor viabilidad celular y tasas más altas de cromosomas dañados en comparación con las células que pueden sufrir una detención completa de G2, lo que sugiere que el propósito del retraso es darle tiempo a la célula para reparar los cromosomas dañados antes de continuar con el ciclo celular. [102] Esto asegura el correcto funcionamiento de la mitosis.
Varias especies de animales exhiben mecanismos similares de retraso celular en respuesta al daño del ADN, que puede ser causado por la exposición a la radiación X. La levadura en ciernes Saccharomyces cerevisiae se ha estudiado específicamente porque la progresión a través del ciclo celular se puede seguir con facilidad mediante la morfología nuclear. Al estudiar Saccharomyces cerevisiae, los investigadores han podido aprender más sobre los genes sensibles a la radiación (RAD) y el efecto que las mutaciones RAD pueden tener en la típica respuesta retardada inducida por daños en el ADN celular. Específicamente, el gen RAD9 desempeña un papel crucial en la detección de daños en el ADN y en la detención de la célula en G2 hasta que se repare el daño.
A través de extensos experimentos, los investigadores han podido arrojar luz sobre el papel que desempeñan los genes RAD en el retraso de la división celular en respuesta al daño del ADN. Cuando las células en crecimiento de tipo salvaje se exponen a varios niveles de irradiación X durante un período de tiempo determinado y luego se analizan con un ensayo de microcolonias , se pueden observar diferencias en la respuesta del ciclo celular según los genes que están mutados en las células. Por ejemplo, mientras que las células no irradiadas progresarán normalmente a lo largo del ciclo celular, las células que están expuestas a la radiación X se detienen permanentemente (se vuelven inviables) o retrasan la fase G2 antes de continuar dividiéndose en la mitosis, lo que corrobora aún más la idea de que el retraso G2 es crucial para la reparación del ADN. Sin embargo, las cepas rad, que son deficientes en la reparación del ADN, exhiben una respuesta marcadamente diferente. Por ejemplo, las células rad52, que no pueden reparar las roturas del ADN de doble cadena, tienden a detenerse permanentemente en G2 cuando se exponen incluso a niveles muy bajos de radiación X, y rara vez terminan progresando a través de las últimas etapas del ciclo celular. Esto se debe a que las células no pueden reparar el daño del ADN y, por lo tanto, no entran en la mitosis. Varios otros mutantes rad exhiben respuestas similares cuando se exponen a la irradiación X.
Sin embargo, la cepa rad9 exhibe un efecto completamente diferente. Estas células no logran retrasar la fase G2 cuando se exponen a la radiación X y terminan progresando a través del ciclo celular sin perturbaciones, antes de morir. Esto sugiere que el gen RAD9, a diferencia de otros genes RAD, desempeña un papel crucial en el inicio de la detención de G2. Para investigar más a fondo estos hallazgos, se han analizado los ciclos celulares de cepas doblemente mutantes. Una cepa mutante rad52 rad9, que tiene defectos en la reparación del ADN y en la detención de G2, no logra detener el ciclo celular cuando se expone a la irradiación X. Esto sugiere que incluso si el daño del ADN no se puede reparar, si RAD9 no está presente, el ciclo celular no se retrasará. Por lo tanto, el daño no reparado del ADN es la señal que le indica a RAD9 que detenga la división y detenga el ciclo celular en G2. Además, existe una respuesta dosis-dependiente; A medida que aumentan los niveles de irradiación X (y el daño posterior al ADN), más células, independientemente de las mutaciones que tengan, quedan detenidas en G2.
Otra forma, y quizás más útil, de visualizar este efecto es observar diapositivas de fotomicroscopía. Inicialmente, los portaobjetos de células haploides RAD+ y rad9 en la fase exponencial de crecimiento muestran células simples e individuales, que son indistinguibles entre sí. Sin embargo, las diapositivas se ven muy diferentes después de haber sido expuestas a radiación X durante 10 horas. Las diapositivas de RAD+ ahora muestran células RAD+ que existen principalmente como microcolonias de dos yemas, lo que sugiere que se ha detenido la división celular. Por el contrario, las diapositivas de rad9 muestran que las células rad9 existen principalmente como de 3 a 8 colonias con gemaciones y parecen más pequeñas que las células RAD+. Esta es una prueba más de que las células RAD mutantes continuaron dividiéndose y son deficientes en la detención de G2.
Sin embargo, existe evidencia de que, aunque el gen RAD9 es necesario para inducir la detención de G2 en respuesta al daño del ADN, dando tiempo a la célula para reparar el daño, en realidad no desempeña un papel directo en la reparación del ADN. Cuando las células rad9 se detienen artificialmente en G2 con MBC, un veneno de microtúbulos que previene la división celular, y luego se tratan con irradiación X, las células pueden reparar su ADN y eventualmente progresar a través del ciclo celular, dividiéndose en células viables. Por lo tanto, el gen RAD9 no desempeña ningún papel en la reparación del ADN dañado: simplemente detecta el ADN dañado y responde retrasando la división celular. El retraso, entonces, está mediado por un mecanismo de control, más que por el ADN físicamente dañado. [103]
Por otro lado, es posible que existan mecanismos de respaldo que cumplan el rol de RAD9 cuando no está presente. De hecho, algunos estudios han descubierto que RAD9 desempeña un papel fundamental en la reparación del ADN. En un estudio, células normales y mutantes rad9 en la fase exponencial de crecimiento fueron expuestas a irradiación UV y sincronizadas en fases específicas del ciclo celular. Después de incubarse para permitir la reparación del ADN, se evaluó el grado de dimerización de la pirimidina (que es indicativa de daño en el ADN) utilizando técnicas de extensión de cebadores sensibles. Se descubrió que la eliminación de las fotolesiones del ADN era mucho menos eficaz en las células mutantes rad9 que en las células normales, lo que proporciona evidencia de que RAD9 participa en la reparación del ADN. Por tanto, el papel de RAD9 en la reparación del daño del ADN sigue sin estar claro. [104]
De todos modos, está claro que RAD9 es necesario para detectar daños en el ADN y detener la división celular. Se ha sugerido que RAD9 posee actividad exonucleasa de 3' a 5', razón por la cual quizás desempeña un papel en la detección de daños en el ADN. Cuando el ADN se daña, se plantea la hipótesis de que RAD9 forma un complejo con RAD1 y HUS1, y este complejo se recluta en los sitios de daño del ADN. De esta forma RAD9 consigue ejercer sus efectos.
Aunque la función de RAD9 se ha estudiado principalmente en la levadura en ciernes Saccharomyces cerevisiae, muchos de los mecanismos de control del ciclo celular son similares entre especies. Por lo tanto, podemos concluir que RAD9 probablemente también desempeñe un papel fundamental en la respuesta al daño del ADN en humanos.
{{cite journal}}: Citar diario requiere |journal=( ayuda )