Un par de cromosomas homólogos , u homólogos , es un conjunto de un cromosoma materno y otro paterno que se emparejan dentro de una célula durante la fertilización . Los homólogos tienen los mismos genes en los mismos loci , donde proporcionan puntos a lo largo de cada cromosoma que permiten que un par de cromosomas se alineen correctamente entre sí antes de separarse durante la meiosis . [1] Esta es la base de la herencia mendeliana , que caracteriza los patrones de herencia del material genético de un organismo a la célula de desarrollo de su descendencia en un momento y área determinados. [2]
Los cromosomas son disposiciones lineales de ácido desoxirribonucleico (ADN) condensado y proteínas histonas , que forman un complejo llamado cromatina . [2] Los cromosomas homólogos están formados por pares de cromosomas de aproximadamente la misma longitud, posición del centrómero y patrón de tinción, para genes con los mismos loci correspondientes . Un cromosoma homólogo se hereda de la madre del organismo; el otro se hereda del padre del organismo. Después de que ocurre la mitosis dentro de las células hijas, tienen la cantidad correcta de genes que son una mezcla de los genes de los dos padres. En los organismos diploides (2n), el genoma está compuesto por un conjunto de cada par de cromosomas homólogos, en comparación con los organismos tetraploides que pueden tener dos conjuntos de cada par de cromosomas homólogos. Los alelos de los cromosomas homólogos pueden ser diferentes, lo que da lugar a diferentes fenotipos de los mismos genes. Esta mezcla de rasgos maternos y paternos se mejora mediante el cruce durante la meiosis , en el que las longitudes de los brazos cromosómicos y el ADN que contienen dentro de un par de cromosomas homólogos se intercambian entre sí. [3]
A principios del siglo XX, William Bateson y Reginald Punnett estaban estudiando la herencia genética y observaron que algunas combinaciones de alelos aparecían con más frecuencia que otras. Thomas Morgan exploró más a fondo esos datos e información . Utilizando experimentos cruzados , reveló que, para un solo padre, los alelos de genes cercanos entre sí a lo largo del cromosoma se mueven juntos. Usando esta lógica concluyó que los dos genes que estaba estudiando estaban ubicados en cromosomas homólogos. Más tarde, durante la década de 1930, Harriet Creighton y Barbara McClintock estaban estudiando la meiosis en células de maíz y examinando loci genéticos en los cromosomas del maíz. [2] Creighton y McClintock descubrieron que las nuevas combinaciones de alelos presentes en la descendencia y el evento de cruce estaban directamente relacionados. [2] Esto demostró la recombinación genética intercromosómica. [2]
Los cromosomas homólogos son pares de cromosomas de un organismo diploide que tienen genes similares, aunque no necesariamente idénticos. [4] Hay dos propiedades principales de los cromosomas homólogos: 1) la longitud de los brazos cromosómicos y 2) la ubicación del centrómero. [5]
La longitud real del brazo, de acuerdo con la ubicación de los genes, es de vital importancia para una alineación adecuada. La ubicación de los centrómeros en el cromosoma se puede caracterizar por cuatro disposiciones principales, ya sea metacéntrica , submetacéntrica , acrocéntrica o telocéntrica . Ambas propiedades (es decir, la longitud de los brazos cromosómicos y la ubicación del centrómero cromosómico) son los factores principales para crear homología estructural entre los cromosomas. Por lo tanto, cuando existen dos cromosomas que contienen relativamente la misma estructura (p. ej., el cromosoma 15 materno y el cromosoma 15 paterno), pueden emparejarse mediante el proceso de sinapsis para formar cromosomas homólogos. [6]
Dado que los cromosomas homólogos no son idénticos y no se originan en el mismo organismo, son diferentes de las cromátidas hermanas . Las cromátidas hermanas resultan después de que se ha producido la replicación del ADN y, por lo tanto, son duplicados idénticos, uno al lado del otro. [7]
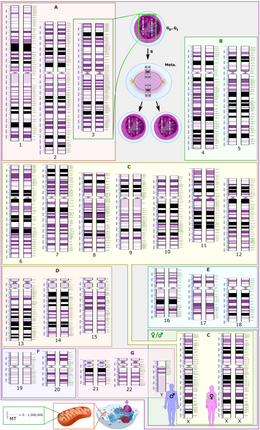
Los humanos tenemos un total de 46 cromosomas, pero sólo hay 22 pares de cromosomas autosómicos homólogos . El par 23 adicional son los cromosomas sexuales, X e Y.
Tenga en cuenta que el par de cromosomas sexuales puede ser homólogo o no, según el sexo del individuo. Por ejemplo, las mujeres contienen XX, por lo que tienen un par homólogo de cromosomas sexuales. Esto significa que las mujeres tienen 23 pares de cromosomas homólogos en total (es decir, 22 pares de cromosomas no sexuales (autosomas), 1 par de cromosomas sexuales). Por el contrario, los machos contienen XY, lo que significa que tienen un par de cromosomas sexuales no homólogos como su par número 23 de cromosomas.
En los seres humanos, los 22 pares de cromosomas autosómicos homólogos contienen los mismos genes pero codifican rasgos diferentes en sus formas alélicas, ya que uno se heredó de la madre y el otro del padre. [8]
Entonces, los humanos tenemos dos juegos de 23 cromosomas en cada célula que contiene un núcleo. Un conjunto de 23 cromosomas (n) es de la madre (22 autosomas, 1 cromosoma sexual (solo X)) y un conjunto de 23 cromosomas (n) es del padre (22 autosomas, 1 cromosoma sexual (X o Y)) . En última instancia, esto significa que los humanos somos organismos diploides (2n). [2]
Los cromosomas homólogos son importantes en los procesos de meiosis y mitosis. Permiten la recombinación y segregación aleatoria del material genético de la madre y el padre en nuevas células. [9]


La meiosis es una ronda de dos divisiones celulares que da como resultado cuatro células hijas haploides, cada una de las cuales contiene la mitad de cromosomas que la célula madre. [10] Reduce el número de cromosomas en una célula germinal a la mitad al separar primero los cromosomas homólogos en la meiosis I y luego las cromátidas hermanas en la meiosis II . El proceso de meiosis I es generalmente más largo que el de la meiosis II porque la cromatina necesita más tiempo para replicarse y para que los cromosomas homólogos se orienten y segreguen adecuadamente mediante los procesos de emparejamiento y sinapsis en la meiosis I. [7] Durante la meiosis, la genética La recombinación (mediante segregación aleatoria) y el entrecruzamiento producen células hijas, cada una de las cuales contiene diferentes combinaciones de genes codificados por la madre y el padre. [10] Esta recombinación de genes permite la introducción de nuevos pares de alelos y variación genética. [2] La variación genética entre organismos ayuda a que una población sea más estable al proporcionar una gama más amplia de rasgos genéticos sobre los que puede actuar la selección natural . [2]
En la profase I de la meiosis I, cada cromosoma se alinea con su pareja homóloga y se empareja completamente. En la profase I, el ADN ya se ha replicado, por lo que cada cromosoma consta de dos cromátidas idénticas conectadas por un centrómero común. [10] Durante la etapa cigoteno de la profase I, los cromosomas homólogos se emparejan entre sí. [10] Este emparejamiento se produce mediante un proceso de sinapsis en el que el complejo sinaptonémico (una estructura proteica) se ensambla y une los cromosomas homólogos a lo largo de su longitud. [7] El entrecruzamiento de cohesina se produce entre los cromosomas homólogos y les ayuda a resistir la separación hasta la anafase . [8] El entrecruzamiento genético , un tipo de recombinación, ocurre durante la etapa de paquiteno de la profase I. [10] Además, con frecuencia ocurre otro tipo de recombinación conocida como recocido de hebras dependiente de la síntesis (SDSA). La recombinación SDSA implica el intercambio de información entre cromátidas homólogas emparejadas , pero no el intercambio físico. La recombinación de SDSA no provoca entrecruzamiento.
En el proceso de entrecruzamiento, los genes se intercambian mediante la ruptura y unión de porciones homólogas de la longitud de los cromosomas. [7] Las estructuras llamadas quiasmas son el lugar del intercambio. Los quiasmas unen físicamente los cromosomas homólogos una vez que se produce el entrecruzamiento y durante todo el proceso de segregación cromosómica durante la meiosis. [7] Tanto el tipo de recombinación cruzado como el no cruzado funcionan como procesos para reparar el daño del ADN , particularmente las roturas de doble cadena. En la etapa diplotena de la profase I el complejo sinaptonémico se desmonta antes de lo cual permitirá que los cromosomas homólogos se separen, mientras que las cromátidas hermanas permanecen asociadas por sus centrómeros. [7]
En la metafase I de la meiosis I, los pares de cromosomas homólogos, también conocidos como bivalentes o tétradas , se alinean en un orden aleatorio a lo largo de la placa de metafase . [10] La orientación aleatoria es otra forma que tienen las células de introducir variación genética. Los husos meióticos que emanan de los polos opuestos del huso se unen a cada uno de los homólogos (cada par de cromátidas hermanas) en el cinetocoro . [8]
En la anafase I de la meiosis I, los cromosomas homólogos se separan entre sí. Los homólogos son escindidos por la enzima separasa para liberar la cohesina que mantenía unidos los brazos del cromosoma homólogo. [8] Esto permite que los quiasmas se liberen y que los homólogos se muevan a los polos opuestos de la célula. [8] Los cromosomas homólogos ahora se segregan aleatoriamente en dos células hijas que se someterán a meiosis II para producir cuatro células germinales hijas haploides . [2]
Después de que las tétradas de cromosomas homólogos se separan en la meiosis I, se separan las cromátidas hermanas de cada par. Las dos células hijas haploides (el número de cromosomas se ha reducido a la mitad: antes estaban presentes dos conjuntos de cromosomas, pero ahora cada conjunto existe en dos células hijas diferentes que han surgido de la única célula madre diploide mediante meiosis I) resultantes de la meiosis Sufro otra división celular en la meiosis II pero sin otra ronda de replicación cromosómica. Las cromátidas hermanas de las dos células hijas se separan durante la anafase II mediante fibras del huso nuclear, lo que da como resultado cuatro células hijas haploides. [2]
Los cromosomas homólogos no funcionan igual en la mitosis que en la meiosis. Antes de cada división mitótica que sufre una célula, los cromosomas de la célula madre se replican. Los cromosomas homólogos dentro de la célula normalmente no se emparejarán ni sufrirán recombinación genética entre sí. [10] En cambio, los replicantes, o cromátidas hermanas, se alinearán a lo largo de la placa de metafase y luego se separarán de la misma manera que en la meiosis II: al ser separados en sus centrómeros por los husos mitóticos nucleares. [11] Si se produce algún cruce entre cromátidas hermanas durante la mitosis, no se produce ningún nuevo genotipo recombinante. [2]
El emparejamiento homólogo en la mayoría de los contextos se referirá a células de la línea germinal, aunque también tiene lugar en células somáticas. Por ejemplo, en los seres humanos, las células somáticas tienen un emparejamiento homólogo muy estrechamente regulado (separados en territorios cromosómicos y emparejados en loci específicos bajo el control de la señalización del desarrollo). Sin embargo, otras especies (en particular, Drosophila ) exhiben emparejamientos homólogos con mucha más frecuencia. En Drosophila, el emparejamiento homólogo respalda un fenómeno regulador de genes llamado transvección en el que un alelo en un cromosoma afecta la expresión del alelo homólogo en el cromosoma homólogo. [12] Una función notable de esto es la regulación sexualmente dimórfica de genes ligados al cromosoma X. [13]

Existen graves repercusiones cuando los cromosomas no se segregan adecuadamente. Una segregación defectuosa puede provocar problemas de fertilidad , muerte de embriones , defectos de nacimiento y cáncer . [14] Aunque los mecanismos para emparejar y adherir cromosomas homólogos varían entre organismos, el funcionamiento adecuado de esos mecanismos es imperativo para que el material genético final se clasifique correctamente. [14]
La separación adecuada de los cromosomas homólogos en la meiosis I es crucial para la separación de las cromátidas hermanas en la meiosis II. [14] La falta de separación adecuada se conoce como no disyunción. Hay dos tipos principales de no disyunción que ocurren: trisomía y monosomía . La trisomía es causada por la presencia de un cromosoma adicional en el cigoto en comparación con el número normal, y la monosomía se caracteriza por la presencia de un cromosoma menos en el cigoto en comparación con el número normal. Si esta división desigual ocurre en la meiosis I, entonces ninguna de las células hijas tendrá una distribución cromosómica adecuada y pueden producirse efectos atípicos, incluido el síndrome de Down. [15] La división desigual también puede ocurrir durante la segunda división meiótica. La no disyunción que se produce en esta etapa puede dar como resultado células hijas normales y células deformadas. [5]
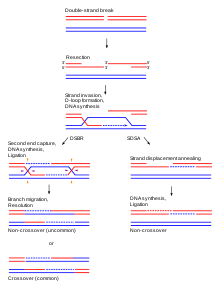
Si bien la función principal de los cromosomas homólogos es su uso en la división nuclear, también se utilizan en la reparación de roturas de doble cadena del ADN . [16] Estas roturas de doble cadena pueden ocurrir en la replicación del ADN y, en la mayoría de los casos, son el resultado de la interacción del ADN con moléculas dañinas de origen natural, como las especies reactivas de oxígeno . Los cromosomas homólogos pueden reparar este daño alineándose con cromosomas de la misma secuencia genética. [16] Una vez que los pares de bases se han emparejado y orientado correctamente entre las dos cadenas, los cromosomas homólogos realizan un proceso que es muy similar a la recombinación o al cruce como se ve en la meiosis. Parte de la secuencia de ADN intacta se superpone con la secuencia del cromosoma dañado . Luego, las proteínas y complejos de replicación se reclutan en el sitio del daño, lo que permite que se produzca la reparación y la replicación adecuada. Gracias a este funcionamiento, se pueden reparar las roturas de la doble cadena y el ADN puede funcionar normalmente. [dieciséis]
La investigación actual y futura sobre el tema del cromosoma homólogo se centra en gran medida en las funciones de diversas proteínas durante la recombinación o durante la reparación del ADN. En un artículo publicado recientemente por Pezza et al. [ ¿cual? ] la proteína conocida como HOP2 es responsable tanto de la sinapsis de los cromosomas homólogos como de la reparación de roturas de doble cadena mediante recombinación homóloga. La deleción de HOP2 en ratones tiene grandes repercusiones en la meiosis. [17] Otros estudios actuales también se centran en proteínas específicas involucradas en la recombinación homóloga.
Se están realizando investigaciones sobre la capacidad de los cromosomas homólogos para reparar roturas de doble cadena del ADN. Los investigadores están investigando la posibilidad de explotar esta capacidad para la medicina regenerativa. [18] Este medicamento podría ser muy frecuente en relación con el cáncer, ya que se cree que el daño al ADN contribuye a la carcinogénesis. La manipulación de la función de reparación de los cromosomas homólogos podría permitir mejorar el sistema de respuesta al daño de una célula. Si bien las investigaciones aún no han confirmado la eficacia de dicho tratamiento, puede convertirse en una terapia útil para el cáncer. [19]