
En genética , una deleción (también llamada deleción genética , deficiencia o mutación por deleción ) (signo: Δ ) es una mutación (una aberración genética) en la que una parte de un cromosoma o una secuencia de ADN queda fuera durante la replicación del ADN. Se puede eliminar cualquier número de nucleótidos , desde una sola base hasta un fragmento completo de cromosoma. [1] Algunos cromosomas tienen puntos frágiles donde se producen roturas, que resultan en la eliminación de una parte del cromosoma. Las roturas pueden ser inducidas por calor, virus, radiación o reacciones químicas. Cuando un cromosoma se rompe, si una parte del mismo se elimina o se pierde, la parte faltante del cromosoma se denomina eliminación o deficiencia. [2]
Para que se produzca sinapsis entre un cromosoma con una gran deficiencia intercalar y un homólogo completo normal, la región no apareada del homólogo normal debe salir de la estructura lineal hacia un bucle de deleción o compensación .
Las mutaciones por deleción de una sola base más pequeñas ocurren por un cambio de una sola base en el ADN plantilla, seguido del deslizamiento de la cadena del ADN plantilla, dentro del sitio activo de la ADN polimerasa. [3] [4] [5]
Las deleciones pueden ser causadas por errores en el cruce cromosómico durante la meiosis , lo que causa varias enfermedades genéticas graves . Las eliminaciones que no ocurren en múltiplos de tres bases pueden causar un cambio de marco al cambiar el marco de lectura de la proteína de 3 nucleótidos de la secuencia genética. Las deleciones son representativas de organismos eucariotas , incluidos los humanos, y no de organismos procarióticos , como las bacterias.
Las causas incluyen las siguientes:
Los tipos de eliminación incluyen los siguientes:
La microdeleción suele encontrarse en niños con anomalías físicas. Una gran cantidad de eliminación resultaría en un aborto inmediato (aborto espontáneo).

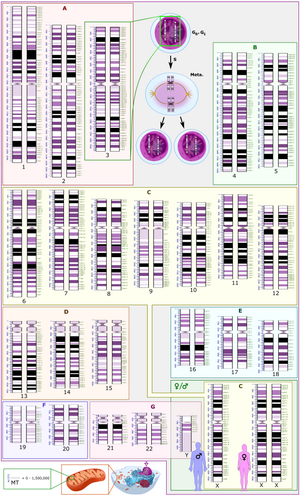
El Sistema Internacional de Nomenclatura Citogenómica Humana (ISCN) es un estándar internacional para la nomenclatura de los cromosomas humanos , que incluye nombres de bandas, símbolos y términos abreviados utilizados en la descripción de los cromosomas humanos y las anomalías cromosómicas. Las abreviaturas incluyen un signo menos (-) para eliminaciones de cromosomas y del para eliminaciones de partes de un cromosoma. [7]
Es menos probable que las eliminaciones pequeñas sean fatales; las deleciones grandes suelen ser fatales; siempre hay variaciones según los genes que se pierden. Algunas deleciones de tamaño mediano provocan trastornos humanos reconocibles, por ejemplo el síndrome de Williams .
La eliminación de un número de pares que no es divisible por tres dará lugar a una mutación por desplazamiento del marco de lectura , lo que provocará que todos los codones que aparecen después de la eliminación se lean incorrectamente durante la traducción , produciendo una proteína gravemente alterada y potencialmente no funcional . Por el contrario, una eliminación que es divisible por tres se denomina eliminación dentro del marco . [8]
Las deleciones son responsables de una variedad de trastornos genéticos, incluidos algunos casos de infertilidad masculina , dos tercios de los casos de distrofia muscular de Duchenne , [1] y dos tercios de los casos de fibrosis quística (los causados por ΔF508 ). [9] La eliminación de parte del brazo corto del cromosoma 5 produce el síndrome de Cri du chat . [1] Las deleciones en el gen que codifica SMN causan atrofia muscular espinal , la causa genética más común de muerte infantil.
Las microdeleciones están asociadas con muchas afecciones diferentes, incluido el síndrome de Angelman, el síndrome de Prader-Willi y el síndrome de DiGeorge. [10] Algunos síndromes, incluidos el síndrome de Angelman y el síndrome de Prader-Willi, están asociados tanto con microdeleciones como con impronta genómica, lo que significa que la misma microdeleción puede causar dos síndromes diferentes según de qué padre provenga la deleción. [11]
Trabajos recientes sugieren que algunas eliminaciones de secuencias altamente conservadas (CONDEL) pueden ser responsables de las diferencias evolutivas presentes entre especies estrechamente relacionadas. Estas deleciones en humanos, denominadas hCONDEL , pueden ser responsables de las diferencias anatómicas y de comportamiento entre humanos, chimpancés y otras variedades de mamíferos como los simios o los monos. [12]
La reciente clasificación integral a nivel de paciente y la cuantificación de los eventos impulsores en cohortes de TCGA revelaron que hay en promedio 12 eventos impulsores por tumor, de los cuales 2,1 son eliminaciones de supresores de tumores . [13]
La introducción de técnicas moleculares junto con métodos citogenéticos clásicos ha mejorado enormemente en los últimos años el potencial diagnóstico de anomalías cromosómicas. En particular, la hibridación genómica comparativa con microarrays (CGH) basada en el uso de clones BAC promete una estrategia sensible para la detección de cambios en el número de copias del ADN a escala de todo el genoma. La resolución de detección podría ser tan alta como >30.000 "bandas" y el tamaño de la deleción cromosómica detectada podría ser tan pequeño como 5 a 20 kb de longitud. [14] Se seleccionaron otros métodos de cálculo para descubrir errores de eliminación de secuenciación de ADN, como la elaboración de perfiles de secuencia final . [15] [16]
En la levadura Saccharomyces cerevisiae , los genes nucleares Rad51 p, Rad52 p y Rad59p codifican proteínas que son necesarias para la reparación recombinacional y se emplean en la reparación de roturas de doble cadena en el ADN mitocondrial . [17] La pérdida de estas proteínas disminuye la tasa de eventos de eliminación espontánea de ADN en las mitocondrias. [17] Este hallazgo implica que la reparación de roturas de la doble cadena del ADN mediante recombinación homóloga es un paso en la formación de deleciones del ADN mitocondrial.
{{cite book}}: Mantenimiento CS1: falta el editor de la ubicación ( enlace ){{cite journal}}: Mantenimiento CS1: varios nombres: lista de autores ( enlace )