Las inserciones y eliminaciones de firmas conservadas ( CSI ) en secuencias de proteínas proporcionan una categoría importante de marcadores moleculares para comprender las relaciones filogenéticas. [1] [2] Los CSI, provocados por cambios genéticos raros, proporcionan marcadores filogenéticos útiles que generalmente son de tamaño definido y están flanqueados en ambos lados por regiones conservadas para garantizar su confiabilidad. Si bien los indeles pueden ser inserciones o eliminaciones arbitrarias, los CSI se definen como solo aquellos indeles de proteínas que están presentes dentro de regiones conservadas de la proteína. [2] [3] [4] [5]
Los CSI que están restringidos a un clado o grupo de especies particular generalmente proporcionan buenos marcadores filogenéticos de una ascendencia evolutiva común. [2] Debido a la rareza y la naturaleza altamente específica de tales cambios, es menos probable que puedan surgir de forma independiente mediante una evolución convergente o paralela (es decir, homoplasia) y, por lo tanto, es probable que representen una sinapomorfía . Otros factores de confusión, como las diferencias en las tasas evolutivas en diferentes sitios o entre diferentes especies, generalmente tampoco afectan la interpretación de un CSI. [2] [3] Al determinar la presencia o ausencia de CSI en una especie fuera del grupo, se puede inferir si la forma ancestral de CSI fue una inserción o eliminación y esto puede usarse para desarrollar una relación filogenética arraigada entre organismos. [1] [2]
Los CSI se descubren buscando cambios compartidos en un árbol filogenético construido a partir de secuencias de proteínas. Se ha descubierto que la mayoría de los CSI que se han identificado tienen un alto valor predictivo al agregar nuevas secuencias, conservando la especificidad para los clados de especies identificados originalmente. Se pueden utilizar para identificar especies conocidas e incluso previamente desconocidas que pertenecen a estos grupos en diferentes entornos. [3] En comparación con las órdenes de ramificación de árboles que pueden variar entre métodos, los CSI específicos crean circunscripciones más concretas que son computacionalmente más baratas de aplicar. [6]

Los CSI específicos de grupo son comúnmente compartidos por diferentes especies que pertenecen a un taxón particular (por ejemplo, género, familia, clase, orden, filo), pero no están presentes en otros grupos. Lo más probable es que estos CSI se introdujeran en un ancestro del grupo de especies antes de que los miembros de los taxones divergieran. Proporcionan medios moleculares para distinguir a los miembros de un taxón particular de todos los demás organismos. [2] [5]
La Figura 1 muestra un ejemplo de 5aa CSI que se encuentra en todas las especies pertenecientes al taxón X. Esta es una característica distintiva de este taxón ya que no se encuentra en ninguna otra especie. Esta firma probablemente fue introducida en un ancestro común de la especie de este taxón. De manera similar, otras firmas específicas de grupo (no mostradas) podrían ser compartidas por A1 y A2 o B1 y B2, etc., o incluso por X1 y X2 o por X3 y X4, etc. Los grupos A, B, C, D y X, en este diagrama podría corresponder a diversos filos bacterianos o eucariotas . [7]
Los CSI específicos de grupo se han utilizado en el pasado para determinar la relación filogenética de varios filos bacterianos y subgrupos dentro de ellos. Por ejemplo, los miembros del filo Thermotogota (anteriormente Thermotogae) compartían de forma única un inserto de 3 aminoácidos en la proteína ribosómica esencial 50S L7/L12 , dentro de una región altamente conservada (82-124 aminoácidos). Esto no está presente en ninguna otra especie de bacteria y podría usarse para caracterizar a los miembros de Thermotogota de todas las demás bacterias. También se utilizaron CSI específicos de grupo para caracterizar subgrupos dentro de Thermotogota. [8]

Los CSI principales son aquellos en los que varios filos principales comparten una inserción o eliminación conservada, pero están ausentes en otros filos. [2]
La Figura 2 muestra un ejemplo de 5aa CSI encontrado en una región conservada que está comúnmente presente en las especies que pertenecen a los filos X, Y y Z, pero está ausente en otros filos (A, B y C). Esta firma indica una relación específica de los taxones X, Y y Z y también de A, B y C. Según la presencia o ausencia de dicho indel, en especies fuera del grupo (a saber, Archaea), se puede inferir si el indel es una inserción o una eliminación, y cuál de estos dos grupos A, B, C o X, Y, Z es ancestral. [7]
Los CSI principales se han utilizado en el pasado para determinar la relación filogenética de varios filos bacterianos. El gran CSI de aproximadamente 150 a 180 aminoácidos dentro de una región conservada de Girasa B (entre los aminoácidos 529 a 751), se comparte comúnmente entre varias especies de Pseudomonadota , Chlamydiota , Planctomycetota y Aquificota . Este CSI está ausente en otros filos bacterianos ancestrales, así como en Archaea . [9] De manera similar, un CSI grande de aproximadamente 100 aminoácidos en homólogos de RpoB (entre los aminoácidos 919-1058) está presente en varias especies pertenecientes a Pseudomonadota, Bacteroidota , Chlorobiota , Chlamydiota , Planctomycetota y Aquificota. Este CSI está ausente en otros filos bacterianos ancestrales, así como en Archaea. [10] [11] En ambos casos se puede inferir que los grupos que carecen del CSI son ancestrales.


Una cuestión clave en la filogenia bacteriana es comprender cómo se relacionan las diferentes especies bacterianas entre sí y su orden de ramificación a partir de un ancestro común. Actualmente, la mayoría de los árboles filogenéticos se basan en el ARNr 16S u otros genes/proteínas. Estos árboles no siempre pueden resolver cuestiones filogenéticas clave con un alto grado de certeza. [12] [13] [14] [15] [16] Sin embargo, en los últimos años, el descubrimiento y los análisis de indeles conservados (CSI) en muchas proteínas distribuidas universalmente han ayudado en esta búsqueda. Se postula que los eventos genéticos que los llevaron a haber ocurrido en importantes puntos de ramificación evolutiva y los patrones de distribución de sus especies proporcionan información valiosa sobre el orden de ramificación y las interrelaciones entre diferentes filos bacterianos. [1] [2] [8]
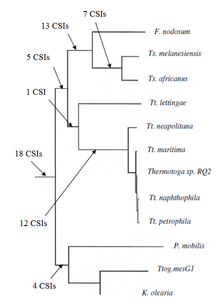
Recientemente se caracterizó la relación filogenética del grupo Thermotogota con base en el enfoque CSI. Hasta ahora no se conocían marcadores bioquímicos o moleculares que pudieran distinguir claramente las especies de este filo de todas las demás bacterias. Se descubrieron más de 60 CSI que eran específicos de todo el filo Thermotogota o sus diferentes subgrupos. 18 CSI están presentes de manera única en varias especies de Thermotogota y proporcionan marcadores moleculares para el filo. Además, hubo muchos CSI que eran específicos de varios subgrupos de Thermotogota. 12 CSI eran específicos de un clado que constaba de varias especies de Thermotogota excepto Tt. Lettingae. 14 CSI eran específicos de un clado formado por los géneros Fervidobacterium y Thermosipho y 18 CSI eran específicos del género Thermosiphon . [ cita necesaria ]
Por último, se informaron 16 CSI que fueron compartidos por algunas o todas las especies de Thermotogota o algunas especies de otros taxones como Archaea , Aquificota , Bacillota , Pseudomonadota , Deinococcota , Fusobacteriota , Dictyoglomota , Chloroflexota y eucariotas . La presencia compartida de algunos de estos CSI podría deberse a la transferencia lateral de genes (LGT) entre estos grupos. Sin embargo, el número de CSI que se comparten comúnmente con otros taxones es mucho menor que los que son específicos de Thermotogota y no exhiben ningún patrón específico. Por tanto, no tienen ningún efecto significativo en la distinción de Thermotogota. [8]
Los termoproteotas mesófilos se colocaron recientemente en un nuevo filo de Archaea llamado Nitrososphaerota (anteriormente Thaumarchaeota). Sin embargo, existen muy pocos marcadores moleculares que puedan distinguir este grupo de arqueas del filo Thermoproteota (anteriormente Crenarchaeota). Se llevó a cabo un estudio filogenético detallado utilizando el enfoque CSI para distinguir estos filos en términos moleculares. Se encontraron 6 CSI de forma única en varios Nitrososphaerota, a saber, Cenarchaeum symbiosum , Nitrosopumilus maritimus y varios Thermoproteota marinos no cultivados. Se encontraron 3 CSI que eran comúnmente compartidos entre especies pertenecientes a Nitrososphaerota y Thermoproteota. Además, se encontraron varios CSI que son específicos para diferentes órdenes de Thermoproteota: 3 CSI para Sulfolobales , 5 CSI para Thermoproteales y, por último, 2 CSI comunes para Sulfolobales y Desulfurococcales . Las firmas descritas proporcionan medios novedosos para distinguir Thermoproteota y Nitrososphaerota, además podrían usarse como una herramienta para la clasificación e identificación de especies relacionadas. [17]
Los miembros del orden Pasteurellales se distinguen actualmente principalmente por su posición en la ramificación del árbol 16srRNA. Actualmente se conocen muy pocos marcadores moleculares que puedan distinguir a los miembros de este orden de otras bacterias. Recientemente se utilizó un enfoque CSI para dilucidar las relaciones filogenéticas entre las especies en este orden; Se descubrieron más de 40 CSI que eran compartidos de forma única por todas o la mayoría de las especies. Dentro de este Pasteurellales se forman dos clados principales: el clado I, que abarca Aggregatibacter , Pasteurella , Actinobacillus succinogenes , Mannheimia succiniciproducens , Haemophilus influenzae y Haemophilus somnus , fue apoyado por 13 CSI. El clado II, que abarca Actinobacillus pleuropneumoniae , Actinobacillus minor , Haemophilus ducreyi , Mannheimia haemolytica y Haemophilus parasuis , contó con el apoyo de nueve CSI. Con base en estos resultados, se propuso dividir Pasteurellales de su familia actual en dos diferentes. Además, las firmas descritas proporcionarían medios novedosos para identificar especies de Pasteurellales no descubiertas. [18]
La clase Gammaproteobacteria forma uno de los grupos más grandes de bacterias. Actualmente se distingue de otras bacterias únicamente por árboles filogenéticos basados en ARNr 16s . No se conocen características moleculares exclusivas de la clase o sus diferentes subgrupos. Se realizó un estudio detallado basado en CSI para comprender mejor la filogenia de esta clase. En primer lugar, se creó un árbol filogenético basado en secuencias concatenadas de varias proteínas distribuidas universalmente. El orden de ramificación de los diferentes órdenes de la clase Gammaproteobacteria (desde el más reciente hasta el más antiguo) fue: Enterobacteriales > Pasteurellales > Vibrionales , Aeromonadales > Alteromonadales > Oceanospirillales , Pseudomonadales >Chromatiales, Legionellales , Methylococcales , Xanthomonadales , Cardiobacteriales , Thiotrichales . Además, se descubrieron 4 CSI que eran exclusivas de la mayoría de las especies de la clase Gammaproteobacteria. Una eliminación de 2 aa en la transformilasa AICAR fue compartida exclusivamente por todas las gammaproteobacterias excepto Francisella tularensis . Se encontró una deleción de 4 aa en la subunidad b de la ARN polimerasa y una deleción de 1 aa en la proteína ribosómica L16 de forma única en varias especies pertenecientes a los órdenes Enterobacteriales, Pasteurellales, Vibrionales, Aeromonadales y Alteromonadales, pero no se encontraron en otras gammaproteobacterias. Por último, una deleción de 2 aa en la leucil-ARNt sintetasa estaba comúnmente presente en los órdenes anteriores de la clase Gammaproteobacteria y en algunos miembros del orden Oceanospirillales. [19] Otro estudio basado en CSI también ha identificado 4 CSI que son exclusivos del orden Xanthomonadales. En conjunto, estos dos hechos muestran que Xanthomonadales es un grupo monofilético ancestral de otras Gammaproteobacteria, lo que muestra además que Xanthomonadales es una subdivisión independiente y constituye uno de los linajes con ramificación más profunda dentro del clado Gammaproteobacteria. [4] [19]
{{cite web}}: Mantenimiento CS1: bot: estado de la URL original desconocido ( enlace )