

La estructura terciaria de una proteína es la forma tridimensional de una proteína . La estructura terciaria tendrá una única cadena polipeptídica "esquelética" con una o más estructuras secundarias de proteínas , los dominios proteicos . Las cadenas laterales de aminoácidos y la columna vertebral pueden interactuar y unirse de varias maneras. Las interacciones y enlaces de las cadenas laterales dentro de una proteína particular determinan su estructura terciaria. La estructura terciaria de la proteína está definida por sus coordenadas atómicas . Estas coordenadas pueden referirse a un dominio proteico o a toda la estructura terciaria. [1] [2] Varias de estas estructuras pueden unirse entre sí, formando una estructura cuaternaria . [3]
La ciencia de la estructura terciaria de las proteínas ha progresado de una hipótesis a una definición detallada. Aunque Emil Fischer había sugerido que las proteínas estaban formadas por cadenas polipeptídicas y cadenas laterales de aminoácidos, fue Dorothy Maud Wrinch quien incorporó la geometría a la predicción de las estructuras de las proteínas . Wrinch lo demostró con el modelo Cyclol , la primera predicción de la estructura de una proteína globular . [4] Los métodos contemporáneos son capaces de determinar, sin predicción, estructuras terciarias dentro de 5 Å (0,5 nm) para proteínas pequeñas (<120 residuos) y, en condiciones favorables, predicciones confiables de estructuras secundarias .
Una proteína plegada en su estado nativo o conformación nativa normalmente tiene una energía libre de Gibbs (una combinación de entalpía y entropía ) más baja que la conformación desplegada. Una proteína tenderá a conformaciones de baja energía, lo que determinará el pliegue de la proteína en el entorno celular . Debido a que muchas conformaciones similares tendrán energías similares, las estructuras de las proteínas son dinámicas y fluctúan entre estas estructuras similares.
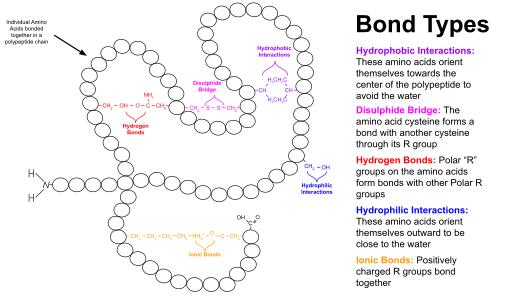
Las proteínas globulares tienen un núcleo de residuos de aminoácidos hidrófobos y una región superficial de residuos hidrófilos , cargados y expuestos al agua . Esta disposición puede estabilizar las interacciones dentro de la estructura terciaria. Por ejemplo, en las proteínas secretadas , que no están bañadas en citoplasma , los enlaces disulfuro entre los residuos de cisteína ayudan a mantener la estructura terciaria. Existe una similitud de estructuras terciarias estables que se observan en proteínas de diversa función y diversa evolución . Por ejemplo, el barril TIM , llamado así por la enzima triosafosfatoisomerasa , es una estructura terciaria común, al igual que la estructura en espiral , dimérica y altamente estable . Por tanto, las proteínas pueden clasificarse según las estructuras que contienen. Las bases de datos de proteínas que utilizan dicha clasificación incluyen SCOP y CATH .
La cinética de plegamiento puede atrapar una proteína en una conformación de alta energía , es decir, una conformación intermedia de alta energía bloquea el acceso a la conformación de menor energía. La conformación de alta energía puede contribuir a la función de la proteína. Por ejemplo, la proteína hemaglutinina de la influenza es una cadena polipeptídica única que, cuando se activa, se escinde proteolíticamente para formar dos cadenas polipeptídicas. Las dos cadenas se mantienen en una conformación de alta energía. Cuando el pH local cae, la proteína sufre un reordenamiento conformacional energéticamente favorable que le permite penetrar la membrana de la célula huésped .
Algunas estructuras de proteínas terciarias pueden existir en estados de larga duración que no son el estado más estable esperado. Por ejemplo, muchas serpinas (inhibidores de la serina proteasa) muestran esta metaestabilidad . Sufren un cambio conformacional cuando una proteasa corta un bucle de la proteína . [5] [6] [7]
Comúnmente se supone que el estado nativo de una proteína es también el más termodinámicamente estable y que una proteína alcanzará su estado nativo, dada su cinética química , antes de ser traducida . Las chaperonas proteicas dentro del citoplasma de una célula ayudan a un polipéptido recién sintetizado a alcanzar su estado nativo. Algunas proteínas chaperonas son muy específicas en su función, por ejemplo, la proteína disulfuro isomerasa ; otros son generales en su función y pueden ayudar a la mayoría de las proteínas globulares, por ejemplo, el sistema de proteínas procarióticas GroEL / GroES y las proteínas de choque térmico eucariotas homólogas (el sistema Hsp60/Hsp10).
La predicción de la estructura terciaria de las proteínas se basa en conocer la estructura primaria de la proteína y comparar la posible estructura terciaria predicha con las estructuras terciarias conocidas en los bancos de datos de proteínas . Esto sólo tiene en cuenta el entorno citoplasmático presente en el momento de la síntesis de proteínas en la medida en que un entorno citoplasmático similar también puede haber influido en la estructura de las proteínas registradas en el banco de datos de proteínas.
La estructura de una proteína, como una enzima , puede cambiar al unirse sus ligandos naturales, por ejemplo un cofactor . En este caso, la estructura de la proteína unida al ligando se conoce como estructura holo, mientras que la proteína no unida tiene una estructura apo. [8]
Estructura estabilizada por la formación de enlaces débiles entre las cadenas laterales de aminoácidos - Determinada por el plegamiento de la cadena polipeptídica sobre sí misma (los residuos no polares se encuentran dentro de la proteína, mientras que los residuos polares se encuentran principalmente en el exterior) - La envoltura de la proteína acerca la proteína y se refiere a situados en regiones distantes de la secuencia - La adquisición de la estructura terciaria conduce a la formación de bolsas y sitios adecuados para el reconocimiento y la unión de moléculas específicas (bioespecificidad).
El conocimiento de la estructura terciaria de las proteínas globulares solubles está más avanzado que el de las proteínas de membrana porque las primeras son más fáciles de estudiar con la tecnología disponible.
La cristalografía de rayos X es la herramienta más común utilizada para determinar la estructura de las proteínas . Proporciona una alta resolución de la estructura pero no proporciona información sobre la flexibilidad conformacional de las proteínas .
La RMN de proteínas proporciona una resolución comparativamente más baja de la estructura de las proteínas. Se limita a proteínas más pequeñas. Sin embargo, puede proporcionar información sobre cambios conformacionales de una proteína en solución.
La microscopía electrónica criogénica (crio-EM) puede brindar información sobre la estructura terciaria y cuaternaria de una proteína. Es particularmente adecuado para proteínas grandes y complejos simétricos de subunidades proteicas .
La interferometría de polarización dual proporciona información complementaria sobre las proteínas capturadas en la superficie. Ayuda a determinar los cambios de estructura y conformación a lo largo del tiempo.
El proyecto Folding@home de la Universidad de Pensilvania es un esfuerzo de investigación en computación distribuida que utiliza aproximadamente 5 petaFLOPS (≈10 x86 petaFLOPS) de computación disponible. Su objetivo es encontrar un algoritmo que prediga consistentemente las estructuras terciarias y cuaternarias de las proteínas dada la secuencia de aminoácidos de la proteína y sus condiciones celulares. [9] [10]
Puede encontrar una lista de software para la predicción de la estructura terciaria de proteínas en Lista de software de predicción de la estructura de proteínas .
Las enfermedades de agregación de proteínas , como la enfermedad de Alzheimer y la enfermedad de Huntington, y las enfermedades priónicas , como la encefalopatía espongiforme bovina, pueden comprenderse mejor mediante la construcción (y reconstrucción) de modelos de enfermedades . Esto se hace provocando la enfermedad en animales de laboratorio, por ejemplo, mediante la administración de una toxina , como el MPTP, para provocar la enfermedad de Parkinson, o mediante manipulación genética . [11] [12] La predicción de la estructura de las proteínas es una nueva forma de crear modelos de enfermedades, que pueden evitar el uso de animales. [13]
Hacer coincidir patrones en la estructura terciaria de una proteína determinada con una gran cantidad de estructuras terciarias de proteínas conocidas y recuperar las más similares en orden de clasificación es el corazón de muchas áreas de investigación, como la predicción de funciones de nuevas proteínas, el estudio de la evolución, el diagnóstico de enfermedades, el descubrimiento de fármacos, diseño de anticuerpos, etc. El proyecto CoMOGrad en BUET es un esfuerzo de investigación para diseñar un método extremadamente rápido y muy preciso para la recuperación de la estructura terciaria de proteínas y desarrollar una herramienta en línea basada en los resultados de la investigación. [14] [15]