La detección de dos híbridos (originalmente conocida como sistema de dos híbridos de levadura o Y2H ) es una técnica de biología molecular que se utiliza para descubrir interacciones proteína-proteína (PPI) [1] e interacciones proteína-ADN [2] [3] mediante pruebas de interacciones físicas. (como la unión) entre dos proteínas o una sola proteína y una molécula de ADN , respectivamente.
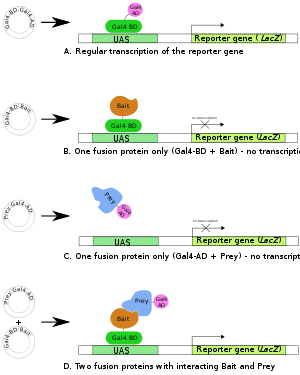
La premisa detrás de la prueba es la activación de genes informadores aguas abajo mediante la unión de un factor de transcripción a una secuencia activadora aguas arriba (UAS). Para la detección de dos híbridos, el factor de transcripción se divide en dos fragmentos separados, llamados dominio de unión al ADN (DBD o, a menudo, también abreviado como BD) y dominio de activación (AD). El BD es el dominio responsable de la unión al UAS y el AD es el dominio responsable de la activación de la transcripción . [1] [2] El Y2H es, por tanto, un ensayo de complementación de fragmentos de proteínas .
La técnica , iniciada por Stanley Fields y Ok-Kyu Song en 1989, se diseñó originalmente para detectar interacciones proteína-proteína utilizando el activador transcripcional Gal4 de la levadura Saccharomyces cerevisiae . La proteína Gal4 activó la transcripción de un gen implicado en la utilización de galactosa, que formó la base de la selección. [4] Desde entonces, el mismo principio se ha adaptado para describir muchos métodos alternativos, incluidos algunos que detectan interacciones proteína-ADN o interacciones ADN-ADN, así como métodos que utilizan diferentes organismos hospedadores como Escherichia coli o células de mamíferos en lugar de levadura. [3] [5]
La clave para la detección de dos híbridos es que en la mayoría de los factores de transcripción eucarióticos , los dominios de activación y unión son modulares y pueden funcionar cerca uno del otro sin unión directa. [6] Esto significa que aunque el factor de transcripción se divide en dos fragmentos, aún puede activar la transcripción cuando los dos fragmentos están conectados indirectamente.
El método de detección más común es el ensayo de dos híbridos de levadura. En este enfoque, el investigador sabe dónde se encuentra cada presa en el medio utilizado (placas de agar). En la última década se han analizado millones de interacciones potenciales en varios organismos utilizando sistemas de detección de alto rendimiento (a menudo utilizando robots) y se han detectado y categorizado más de miles de interacciones en bases de datos como BioGRID. [7] [8] Este sistema a menudo utiliza una cepa de levadura genéticamente modificada en la que falta la biosíntesis de ciertos nutrientes (generalmente aminoácidos o ácidos nucleicos ). Cuando se cultiva en medios que carecen de estos nutrientes, la levadura no logra sobrevivir. Se puede hacer que esta cepa de levadura mutante incorpore ADN extraño en forma de plásmidos . En el cribado de dos híbridos de levadura, se introducen simultáneamente plásmidos de cebo y presa separados en la cepa de levadura mutante o se utiliza una estrategia de apareamiento para obtener ambos plásmidos en una célula huésped. [9]
El segundo enfoque de alto rendimiento es el método de selección de bibliotecas. En esta configuración, las células que albergan el cebo y la presa se aparean en un orden aleatorio. Después de aparear y seleccionar las células supervivientes en un medio selectivo, el científico secuenciará los plásmidos aislados para ver qué presa (secuencia de ADN) interactúa con el cebo utilizado. Este enfoque tiene una tasa de reproducibilidad más baja y tiende a generar mayores cantidades de falsos positivos en comparación con el enfoque matricial. [9]
Los plásmidos se diseñan para producir un producto proteico en el que el fragmento del dominio de unión al ADN (BD) se fusiona con una proteína, mientras que otro plásmido se diseña para producir un producto proteico en el que el fragmento del dominio de activación (AD) se fusiona con otra proteína. La proteína fusionada al BD puede denominarse proteína cebo y, por lo general, es una proteína conocida que el investigador utiliza para identificar nuevos socios de unión. La proteína fusionada a la AD puede denominarse proteína presa y puede ser una única proteína conocida o una biblioteca de proteínas conocidas o desconocidas. En este contexto, una biblioteca puede consistir en una colección de secuencias codificantes de proteínas que representan todas las proteínas expresadas en un organismo o tejido particular, o puede generarse mediante la síntesis de secuencias aleatorias de ADN. [3] Independientemente de la fuente, posteriormente se incorporan a la secuencia codificante de proteínas de un plásmido, que luego se transfecta en las células elegidas para el método de detección. [3] Esta técnica, cuando se utiliza una biblioteca, supone que cada célula se transfecta con no más de un único plásmido y que, por lo tanto, cada célula finalmente expresa no más de un solo miembro de la biblioteca de proteínas.
Si las proteínas del cebo y la presa interactúan (es decir, se unen), entonces el AD y el BD del factor de transcripción están conectados indirectamente, acercando el AD al sitio de inicio de la transcripción y puede ocurrir la transcripción del gen indicador. Si las dos proteínas no interactúan, no se produce la transcripción del gen informador. De esta forma, una interacción exitosa entre la proteína fusionada está relacionada con un cambio en el fenotipo celular. [1]
El desafío de separar las células que expresan proteínas que interactúan con sus proteínas de fusión homólogas de aquellas que no lo hacen se aborda en la siguiente sección.
En cualquier estudio, algunos de los dominios proteicos, los que se están investigando, variarán según los objetivos del estudio, mientras que otros dominios, los que no están siendo investigados, se mantendrán constantes. Por ejemplo, en un estudio de dos híbridos para seleccionar dominios de unión al ADN, el dominio de unión al ADN, BD, variará, mientras que las dos proteínas que interactúan, el cebo y la presa, deben mantenerse constantes para mantener una unión fuerte entre el BD. y ANUNCIO. Hay una serie de dominios entre los que elegir el BD, el cebo y la presa y el AD, si estos se mantienen constantes. En las investigaciones de interacción proteína-proteína, el BD puede elegirse entre cualquiera de los muchos dominios fuertes de unión al ADN, como Zif268 . [2] Una elección frecuente de dominios de cebo y presa son los residuos 263–352 de la levadura Gal11P con una mutación N342V [2] y los residuos 58–97 de la levadura Gal4, [2] respectivamente. Estos dominios se pueden utilizar en técnicas de selección basadas tanto en levaduras como en bacterias y se sabe que se unen fuertemente entre sí. [1] [2]
El AD elegido debe ser capaz de activar la transcripción del gen informador, utilizando la propia maquinaria de transcripción de la célula. Por lo tanto, la variedad de AD disponibles para su uso en técnicas basadas en levaduras puede no ser adecuada para su uso en sus análogos basados en bacterias. La AD derivada del virus del herpes simple, VP16 y la AD Gal4 de levadura se han utilizado con éxito en levaduras [1], mientras que una porción de la subunidad α de la ARN polimerasa de E. coli se ha utilizado en métodos basados en E. coli . [2] [3]
Si bien los dominios de activación poderosa pueden permitir una mayor sensibilidad hacia interacciones más débiles, a la inversa, un AD más débil puede proporcionar una mayor rigurosidad.
Se deben incorporar varias secuencias genéticas diseñadas a la célula huésped para realizar un análisis de dos híbridos o una de sus técnicas derivadas. Las consideraciones y métodos utilizados en la construcción y entrega de estas secuencias difieren según las necesidades del ensayo y el organismo elegido como fondo experimental.
Hay dos categorías amplias de bibliotecas híbridas: bibliotecas aleatorias y bibliotecas basadas en ADNc. Una biblioteca de ADNc está constituida por el ADNc producido mediante transcripción inversa de ARNm recogido de células específicas de tipos de células. Esta biblioteca se puede ligar en una construcción de modo que se una al BD o AD que se utiliza en el ensayo. [1] Una biblioteca aleatoria utiliza longitudes de ADN de secuencia aleatoria en lugar de estas secciones de ADNc. Existen varios métodos para la producción de estas secuencias aleatorias, incluida la mutagénesis en casete . [2] Independientemente de la fuente de la biblioteca de ADN, se liga en el lugar apropiado del plásmido/fagémido relevante utilizando las endonucleasas de restricción apropiadas . [2]
Al colocar las proteínas híbridas bajo el control de promotores lac inducibles por IPTG , se expresan sólo en medios suplementados con IPTG. Además, al incluir diferentes genes de resistencia a los antibióticos en cada construcción genética, el crecimiento de células no transformadas se previene fácilmente mediante cultivo en medios que contienen los antibióticos correspondientes. Esto es particularmente importante para los métodos de contraselección en los que se necesita una falta de interacción para la supervivencia celular. [2]
El gen informador puede insertarse en el genoma de E. coli insertándolo primero en un episoma , un tipo de plásmido con la capacidad de incorporarse al genoma de la célula bacteriana [2] con un número de copias de aproximadamente una por célula. [10]
Los fagémidos de expresión híbridos se pueden electroporar en células E. coli XL-1 Blue que, después de la amplificación y la infección con el fago auxiliar VCS-M13 , producirán una reserva de fagos de biblioteca. Cada uno de estos fagos contendrá un miembro monocatenario de la biblioteca de fagémidos. [2]
Una vez realizada la selección, se debe determinar la estructura primaria de las proteínas que presentan las características adecuadas. Esto se logra mediante la recuperación de las secuencias que codifican proteínas (como se insertaron originalmente) de las células que muestran el fenotipo apropiado.
El fagémido utilizado para transformar células de E. coli se puede "rescatar" de las células seleccionadas infectándolas con el fago auxiliar VCS-M13. Las partículas de fagos resultantes que se producen contienen fagémidos monocatenarios y se utilizan para infectar células XL-1 Blue. [2] Los fagémidos de doble cadena se recolectan posteriormente de estas células XL-1 Blue, invirtiendo esencialmente el proceso utilizado para producir el fago de la biblioteca original. Finalmente, las secuencias de ADN se determinan mediante secuenciación didesoxi . [2]
El represor Tet-R derivado de Escherichia coli se puede utilizar junto con un gen indicador convencional y se puede controlar mediante tetraciclina o doxiciclina (inhibidores de Tet-R). Así, la expresión de Tet-R está controlada por el sistema estándar de dos híbridos, pero el Tet-R a su vez controla (reprime) la expresión de un informador mencionado anteriormente, como HIS3 , a través de su promotor Tet-R. Luego se puede usar tetraciclina o sus derivados para regular la sensibilidad de un sistema que utiliza Tet-R. [1]
La sensibilidad también puede controlarse variando la dependencia de las células de sus genes indicadores. Por ejemplo, esto puede verse afectado alterando la concentración de histidina en el medio de crecimiento para las células dependientes de his3 y alterando la concentración de estreptomicina para las células dependientes de aadA . [2] [3] La dependencia del gen de selección también se puede controlar aplicando un inhibidor del gen de selección en una concentración adecuada. El 3-amino-1,2,4-triazol (3-AT), por ejemplo, es un inhibidor competitivo del producto del gen HIS3 y puede usarse para valorar el nivel mínimo de expresión de HIS3 requerido para el crecimiento en medios deficientes en histidina. [2]
La sensibilidad también se puede modular variando el número de secuencias operadoras en el ADN informador.
Una tercera proteína que no es de fusión puede coexpresarse con dos proteínas de fusión. Dependiendo de la investigación, la tercera proteína puede modificar una de las proteínas de fusión o mediar o interferir en su interacción. [1]
La coexpresión de la tercera proteína puede ser necesaria para la modificación o activación de una o ambas proteínas de fusión. Por ejemplo, S. cerevisiae no posee tirosina quinasa endógena. Si una investigación involucra una proteína que requiere fosforilación de tirosina, la quinasa debe suministrarse en forma de un gen de tirosina quinasa. [1]
La proteína que no es de fusión puede mediar en la interacción uniendo ambas proteínas de fusión simultáneamente, como en el caso de la dimerización del receptor dependiente de ligando. [1]
Para una proteína con una pareja que interactúa, su homología funcional con otras proteínas puede evaluarse suministrando la tercera proteína en forma no fusionada, que luego puede competir o no con la proteína de fusión por su pareja de unión. La unión entre la tercera proteína y la otra proteína de fusión interrumpirá la formación del complejo de activación de la expresión informadora y, por lo tanto, reducirá la expresión informadora, lo que conducirá al cambio distintivo en el fenotipo. [1]
Una limitación de las pantallas clásicas de dos híbridos de levadura es que se limitan a proteínas solubles. Por lo tanto, es imposible utilizarlos para estudiar las interacciones proteína-proteína entre proteínas integrales de membrana insolubles . El sistema de ubiquitina dividida proporciona un método para superar esta limitación. [11] En el sistema de ubiquitina dividida, dos proteínas integrales de membrana que se van a estudiar se fusionan con dos restos de ubiquitina diferentes : un resto de ubiquitina C-terminal ("Cub", residuos 35-76) y un resto de ubiquitina N-terminal (" Nub", residuos 1–34). Estas proteínas fusionadas se denominan cebo y presa, respectivamente. Además de estar fusionado a una proteína integral de membrana, el resto Cub también está fusionado a un factor de transcripción (TF) que puede ser escindido por proteasas específicas de ubiquitina . Tras la interacción cebo-presa, las mitades Nub y Cub se ensamblan, reconstituyendo la ubiquitina dividida. La molécula de ubiquitina dividida reconstituida es reconocida por proteasas específicas de ubiquitina, que escinden el factor de transcripción, lo que le permite inducir la transcripción de genes informadores . [12]
Zolghadr y sus compañeros de trabajo presentaron un sistema fluorescente de dos híbridos que utiliza dos proteínas híbridas que están fusionadas con diferentes proteínas fluorescentes, así como con LacI, el represor lac . La estructura de las proteínas de fusión se ve así: FP2-LacI-bait y FP1-prey donde las proteínas cebo y presa interactúan y acercan las proteínas fluorescentes (FP1 = GFP , FP2 = mCherry ) al sitio de unión de LacI. proteína en el genoma de la célula huésped. [13] El sistema también se puede utilizar para detectar inhibidores de las interacciones proteína-proteína. [14]
Mientras que el sistema Y2H original utilizaba un factor de transcripción reconstituido, otros sistemas crean actividades enzimáticas para detectar IBP. Por ejemplo, el sensor de sustrato KInase ("KISS"), es un enfoque de dos híbridos de mamíferos que se ha diseñado para mapear los PPI intracelulares. Aquí, una proteína cebo se fusiona con una porción de TYK2 que contiene quinasa y una presa se acopla a un fragmento del receptor de citocina gp130 . Cuando el cebo y la presa interactúan, TYK2 fosforila los sitios de acoplamiento de STAT3 en la quimera de la presa, lo que finalmente conduce a la activación de un gen informador . [15]
La variación de un híbrido de esta técnica está diseñada para investigar las interacciones proteína-ADN y utiliza una única proteína de fusión en la que la AD está vinculada directamente al dominio de unión. Sin embargo, en este caso el dominio de unión no es necesariamente de secuencia fija como en el análisis de dos híbridos proteína-proteína, sino que puede estar constituido por una biblioteca. Esta biblioteca se puede seleccionar frente a la secuencia diana deseada, que se inserta en la región promotora de la construcción del gen informador. En un sistema de selección positiva, se selecciona un dominio de unión que se une con éxito al UAS y permite la transcripción. [1]
Tenga en cuenta que la selección de dominios de unión al ADN no se realiza necesariamente utilizando un sistema de un híbrido, sino que también se puede realizar utilizando un sistema de dos híbridos en el que se varía el dominio de unión y las proteínas del cebo y la presa se mantienen constantes. [2] [3]

Las interacciones ARN-proteína se han investigado mediante una variación de tres híbridos de la técnica de dos híbridos. En este caso, una molécula de ARN híbrida sirve para unir los dos dominios de fusión de proteínas, que no están destinados a interactuar entre sí sino más bien con la molécula de ARN intermediaria (a través de sus dominios de unión a ARN). [1] Las técnicas que involucran proteínas que no son de fusión y que realizan una función similar, como se describe en la sección anterior "proteínas que no son de fusión", también pueden denominarse métodos de tres híbridos.
El uso simultáneo de los métodos de uno y dos híbridos (es decir, interacción simultánea proteína-proteína y proteína-ADN) se conoce como enfoque de uno-dos híbridos y se espera que aumente la rigurosidad de la evaluación. [1]
Aunque teóricamente cualquier célula viva podría usarse como fondo para un análisis de dos híbridos, existen consideraciones prácticas que dictan cuál se elige. La línea celular elegida debe ser relativamente barata y fácil de cultivar y suficientemente robusta para resistir la aplicación de los métodos y reactivos de investigación. [1] Esto último es especialmente importante para realizar estudios de alto rendimiento . Por lo tanto, la levadura S. cerevisiae ha sido el principal organismo huésped de los estudios de dos híbridos. Sin embargo, no siempre es el sistema ideal para estudiar proteínas que interactúan de otros organismos. [16] Las células de levadura a menudo no tienen las mismas modificaciones postraduccionales, tienen un uso de codones diferente o carecen de ciertas proteínas que son importantes para la expresión correcta de las proteínas. Para hacer frente a estos problemas se han desarrollado varios sistemas novedosos de dos híbridos. Dependiendo del sistema utilizado, se utilizan placas de agar o un medio de crecimiento específico para hacer crecer las células y permitir la selección para la interacción. El método utilizado más comúnmente es el de siembra en agar, en el que las células se siembran en un medio selectivo para ver si se produce la interacción. Las células que no tienen proteínas de interacción no deberían sobrevivir en este medio selectivo. [7] [17]
La levadura S. cerevisiae fue el organismo modelo utilizado durante el inicio de la técnica de dos híbridos. Se le conoce comúnmente como sistema Y2H. Tiene varias características que lo convierten en un organismo robusto para albergar la interacción, incluida la capacidad de formar estructuras de proteínas terciarias, pH interno neutro, capacidad mejorada para formar enlaces disulfuro y glutatión en estado reducido, entre otros factores amortiguadores citosólicos, para mantener un ambiente interno hospitalario. ambiente. [1] El modelo de levadura puede manipularse mediante técnicas no moleculares y se conoce la secuencia completa de su genoma. [1] Los sistemas de levadura son tolerantes a diversas condiciones de cultivo y a productos químicos agresivos que no podrían aplicarse a cultivos de tejidos de mamíferos. [1]
Se han creado varias cepas de levadura específicamente para las pantallas Y2H, por ejemplo, Y187 [18] y AH109 [19] , ambas producidas por Clontech . También se han utilizado las cepas de levadura R2HMet y BK100. [20]
C. albicans es una levadura con una característica particular: traduce el codón CUG en serina en lugar de leucina. Debido a este uso diferente de codones, es difícil utilizar el sistema modelo S. cerevisiae como Y2H para comprobar las interacciones proteína-proteína utilizando genes de C. albicans . Para proporcionar un entorno más nativo,se desarrolló un sistema de dos híbridos (C2H) de C. albicans . Con este sistema se pueden estudiar las interacciones proteína-proteína en la propia C. albicans . [21] [22] Una adición reciente fue la creación de un sistema de alto rendimiento. [23] [24] [25]
Los métodos bacterianos de dos híbridos (B2H o BTH) generalmente se llevan a cabo en E. coli y tienen algunas ventajas sobre los sistemas basados en levadura. Por ejemplo, la mayor eficiencia de transformación y la mayor tasa de crecimiento hacen que E. coli utilice bibliotecas más grandes (más de 10 8 ). [2] La ausencia de requisitos para que se incluya una señal de localización nuclear en la secuencia de proteínas y la capacidad de estudiar proteínas que serían tóxicas para la levadura también pueden ser factores importantes a considerar al elegir un organismo de fondo experimental. [2]
La actividad de metilación de ciertas proteínas ADN metiltransferasa de E. coli puede interferir con algunas selecciones de proteínas de unión al ADN. Si esto se prevé, el uso de una cepa de E. coli que sea defectuosa para una metiltransferasa particular puede ser una solución obvia. [2] El B2H puede no ser ideal cuando se estudian interacciones proteína-proteína eucariotas (por ejemplo, proteínas humanas), ya que las proteínas pueden no plegarse como en las células eucariotas o pueden carecer de otro procesamiento.
En los últimos años se ha diseñado un sistema de dos híbridos de mamíferos (M2H) para estudiar las interacciones proteína-proteína de los mamíferos en un entorno celular que imita estrechamente el entorno de las proteínas nativas. [26] En este sistema se utilizan células de mamíferos transfectadas transitoriamente para encontrar interacciones proteína-proteína. [27] [28] El uso de una línea celular de mamíferos para estudiar las interacciones proteína-proteína de mamíferos brinda la ventaja de trabajar en un contexto más nativo. [5] Las modificaciones postraduccionales, fosforilación, acilación y glicosilación son similares. La localización intracelular de las proteínas también es más correcta en comparación con el uso de un sistema híbrido de dos levaduras. [29] [30] También es posible con el sistema de dos híbridos de mamíferos estudiar las entradas de señales. [31] Otra gran ventaja es que los resultados se pueden obtener dentro de las 48 horas posteriores a la transfección. [5]
En 2005 se desarrolló un sistema de dos híbridos en plantas. Utilizando protoplastos de A. thaliana se pueden estudiar las interacciones proteína-proteína en plantas. De esta manera las interacciones pueden estudiarse en su contexto nativo. En este sistema, GAL4 AD y BD están bajo el control del fuerte promotor 35S. La interacción se mide utilizando un reportero GUS. Para permitir una detección de alto rendimiento, los vectores se hicieron compatibles con la puerta de enlace. El sistema se conoce como sistema de dos híbridos de protoplastos (P2H). [32]
La liebre de mar A californica es un organismo modelo en neurobiología para estudiar, entre otros, los mecanismos moleculares de la memoria a largo plazo. Para estudiar las interacciones, importantes en neurología, en un entorno más nativo se ha desarrollado un sistema bihíbrido en las neuronas de A californica . En este sistema se utilizan GAL4 AD y BD. [33] [34]
Se desarrolló un sistema de dos híbridos de insectos (I2H) en una línea celular de gusano de seda a partir de la larva u oruga de la polilla de la seda domesticada, Bombyx mori (células BmN4). Este sistema utiliza GAL4 BD y el dominio de activación del ratón NF-κB P65. Ambos están bajo el control del promotor OpIE2. [35]
Al cambiar aminoácidos específicos mediante la mutación de los pares de bases de ADN correspondientes en los plásmidos utilizados, se puede determinar la importancia de esos residuos de aminoácidos en el mantenimiento de la interacción. [1]
Después de utilizar un método basado en células bacterianas para seleccionar proteínas de unión al ADN, es necesario comprobar la especificidad de estos dominios, ya que existe un límite en la medida en que el genoma de la célula bacteriana puede actuar como sumidero de dominios con afinidad por otros. secuencias (o incluso, una afinidad general por el ADN). [2]
Las interacciones de señalización proteína-proteína plantean objetivos terapéuticos adecuados debido a su especificidad y omnipresencia. El enfoque de descubrimiento aleatorio de fármacos utiliza bancos de compuestos que comprenden estructuras químicas aleatorias y requiere un método de alto rendimiento para probar estas estructuras en el objetivo previsto. [1] [17]
La célula elegida para la investigación puede diseñarse específicamente para reflejar el aspecto molecular que el investigador pretende estudiar y luego usarse para identificar nuevas terapias o agentes antiplagas para humanos o animales. [1] [17]
Mediante la determinación de las parejas de interacción de proteínas desconocidas se pueden deducir las posibles funciones de estas nuevas proteínas. [1] Esto se puede hacer utilizando una única proteína conocida frente a una biblioteca de proteínas desconocidas o, por el contrario, seleccionando de una biblioteca de proteínas conocidas utilizando una única proteína de función desconocida. [1]
Para seleccionar proteínas con dedos de zinc (ZFP) para la ingeniería de proteínas , se han utilizado con éxito métodos adaptados de la técnica de detección de dos híbridos. [2] [3] Una ZFP es en sí misma una proteína de unión al ADN utilizada en la construcción de dominios de unión al ADN personalizados que se unen a una secuencia de ADN deseada. [36]
Utilizando un gen de selección con la secuencia diana deseada incluida en la UAS y aleatorizando las secuencias de aminoácidos relevantes para producir una biblioteca de ZFP, se pueden seleccionar células que albergan una interacción ADN-ZFP con las características requeridas. Cada ZFP normalmente reconoce solo de 3 a 4 pares de bases, por lo que para evitar el reconocimiento de sitios fuera del UAS, la ZFP aleatorizada se diseña en un "andamio" que consta de otras dos ZFP de secuencia constante. Por lo tanto, el UAS está diseñado para incluir la secuencia objetivo del andamio constante además de la secuencia para la cual se selecciona una ZFP. [2] [3]
También se pueden investigar otros dominios de unión al ADN utilizando este sistema. [2]
La razón de esta alta tasa de error radica en las características de la pantalla:
Cada uno de estos puntos por sí solo puede dar lugar a resultados falsos. Debido a los efectos combinados de todas las fuentes de error, los dos híbridos de levadura deben interpretarse con precaución. La probabilidad de generar falsos positivos significa que todas las interacciones deben confirmarse mediante un ensayo de alta confianza, por ejemplo, la coinmunoprecipitación de las proteínas endógenas, lo cual es difícil para los datos de interacción proteína-proteína a gran escala. Alternativamente, los datos de Y2H se pueden verificar utilizando múltiples variantes de Y2H [38] o técnicas bioinformáticas. Este último prueba si las proteínas que interactúan se expresan al mismo tiempo, comparten algunas características comunes (como anotaciones de ontología genética o ciertas topologías de red ) y tienen interacciones homólogas en otras especies. [39]