


La hibridación in situ (ISH) es un tipo de hibridación que utiliza una, ARN o ácido nucleico modificado complementario marcado (es decir, una sonda ) para localizar una secuencia específica de ADN o ARN en una porción o sección de tejido ( in situ ) o si el tejido es lo suficientemente pequeño (por ejemplo, semillas de plantas, embriones de Drosophila ), en todo el tejido (ISH de montaje completo), en células y en células tumorales circulantes (CTC). Esto es distinto de la inmunohistoquímica , que generalmente localiza proteínas en secciones de tejido.
La hibridación in situ se utiliza para revelar la ubicación de secuencias específicas de ácidos nucleicos en cromosomas o tejidos, un paso crucial para comprender la organización, regulación y función de los genes. Las técnicas clave que se utilizan actualmente incluyen la hibridación in situ con ARNm con sondas de oligonucleótidos y ARN (tanto radiomarcadas como marcadas con hapteno), el análisis con microscopios ópticos y electrónicos, la hibridación in situ de montaje completo , la doble detección de ARN y ARN más proteína, y la hibridación in situ fluorescente para detectar secuencias cromosómicas. La hibridación in situ de ADN se puede utilizar para determinar la estructura de los cromosomas. La hibridación in situ de ADN fluorescente (FISH) se puede utilizar, por ejemplo, en diagnósticos médicos para evaluar la integridad cromosómica. La hibridación in situ de ARN (ISH ) de ARN se utiliza para medir y localizar ARN (ARNm, lncRNA y miRNA) dentro de secciones de tejido, células, montajes completos y células tumorales circulantes (CTC). La hibridación in situ fue inventada por los biólogos estadounidenses Mary-Lou Pardue y Joseph G. Gall . [1] [2] [3]
La hibridación in situ es una técnica poderosa para identificar especies específicas de ARNm dentro de células individuales en secciones de tejido, lo que proporciona información sobre los procesos fisiológicos y la patogénesis de enfermedades. Sin embargo, la hibridación in situ requiere que se tomen muchos pasos con una optimización precisa para cada tejido examinado y para cada sonda utilizada. Para preservar el ARNm objetivo dentro de los tejidos, a menudo se requiere el uso de fijadores de reticulación (como el formaldehído ). [4]
Además, la hibridación in situ en secciones de tejido requiere que las rodajas de tejido sean muy finas, normalmente de 3 μm a 7 μm de espesor. Los métodos habituales para preparar las secciones de tejido para el procesamiento de hibridación in situ incluyen el corte de muestras con un criostato o un cortador de tejido Compresstome . Un criostato toma tejido fresco o fijado y lo sumerge en nitrógeno líquido para congelarlo rápidamente. A continuación, el tejido se incorpora a un medio de congelación llamado OCT y se cortan secciones finas. Los obstáculos incluyen la aparición de artefactos de congelación en el tejido que pueden interferir con la tinción adecuada del ARNm. El Compresstome corta el tejido en rodajas finas sin un proceso de congelación; las secciones que flotan libremente se cortan después de ser incorporadas en agarosa para lograr estabilidad. Este método evita la congelación del tejido y, por lo tanto, los artefactos de congelación asociados. El proceso es permanente e irreversible una vez que se completa. [5]
Para la histoquímica de hibridación , las células y los tejidos de muestra generalmente se tratan para fijar las transcripciones objetivo en su lugar y aumentar el acceso de la sonda. Como se señaló anteriormente, la sonda es un ADN complementario marcado o, ahora más comúnmente, un ARN complementario ( ribosonda ). La sonda se hibrida con la secuencia objetivo a temperatura elevada y luego se lava el exceso de sonda (después de la hidrólisis previa utilizando ARNasa en el caso de la sonda de ARN en exceso no hibridada). Los parámetros de la solución como la temperatura, la sal y/o la concentración de detergente se pueden manipular para eliminar cualquier interacción no idéntica (es decir, solo las coincidencias de secuencia exactas permanecerán unidas). Luego, la sonda que se marcó con bases radiomarcadas, fluorescentes o marcadas con antígeno (p. ej., digoxigenina ) se localiza y cuantifica en el tejido utilizando autorradiografía , microscopía de fluorescencia o inmunohistoquímica , respectivamente. La ISH también puede utilizar dos o más sondas, marcadas con radiactividad u otras etiquetas no radiactivas, para detectar simultáneamente dos o más transcripciones.
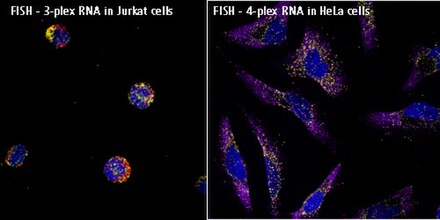
Una tecnología alternativa, el ensayo de ADN ramificado , se puede utilizar para ensayos de hibridación in situ de ARN (ARNm, lncRNA y miRNA) con sensibilidad de molécula única sin el uso de radiactividad. Este enfoque (por ejemplo, ensayos ViewRNA) se puede utilizar para visualizar hasta cuatro objetivos en un ensayo, y utiliza un diseño de sonda patentado y amplificación de señal de bDNA para generar señales sensibles y específicas. Las muestras (células, tejidos y CTC) se fijan y luego se tratan para permitir la accesibilidad del objetivo de ARN (desenmascaramiento de ARN). Las sondas específicas del objetivo se hibridan con cada ARN objetivo. La amplificación de señal posterior se basa en la hibridación específica de sondas adyacentes ( oligonucleótidos individuales [oligos] que se unen lado a lado en los objetivos de ARN). Una sonda específica del objetivo típica contendrá 40 oligonucleótidos, lo que da como resultado 20 pares de oligos que se unen lado a lado en el objetivo para la detección de ARNm y lncRNA, y 2 oligos o un solo par para la detección de miRNA. La amplificación de la señal se logra mediante una serie de pasos de hibridación secuenciales. Una molécula preamplificadora se hibrida con cada par de oligonucleótidos en el ARN específico del objetivo, luego múltiples moléculas amplificadoras se hibridan con cada preamplificador. A continuación, múltiples oligonucleótidos de sonda de marcado (conjugados con fosfatasa alcalina o directamente con fluoróforos) se hibridan con cada molécula amplificadora. Una estructura de amplificación de señal completamente ensamblada, "árbol", tiene 400 sitios de unión para las sondas de marcado. Cuando todas las sondas específicas del objetivo se unen al transcrito de ARNm objetivo, se produce una amplificación de señal de 8000 veces para ese transcrito. Los sistemas de amplificación de señal separados pero compatibles permiten los ensayos multiplex. La señal se puede visualizar utilizando un microscopio de fluorescencia o de campo claro.
El protocolo lleva entre dos y tres días y su puesta en marcha lleva algún tiempo. Algunas empresas venden robots para automatizar el proceso (por ejemplo, CEM InsituPro). Como resultado, se han realizado pruebas a gran escala en laboratorios sobre miles de genes. Por lo general, se puede acceder a los resultados a través de sitios web (consulte los enlaces externos). [6]