La clasificación de linaje incompleta , [1] [2] [3] también denominada hemiplasia, coalescencia profunda , retención de polimorfismo ancestral o polimorfismo transespecies, describe un fenómeno en genética de poblaciones cuando las copias de genes ancestrales no logran fusionarse (mirando hacia atrás en el tiempo). en una copia ancestral común hasta niveles más profundos que los eventos de especiación anteriores. Es causada por la clasificación de linajes de polimorfismos genéticos que se retuvieron en nodos sucesivos del árbol de especies. [4] En otras palabras, el árbol producido por un solo gen difiere del árbol a nivel de población o especie, produciendo un árbol discordante. Cualquiera que sea el mecanismo, el resultado es que un árbol a nivel de especie generado puede diferir dependiendo de los genes seleccionados utilizados para la evaluación. [5] [6] Esto contrasta con la clasificación de linaje completo , donde el árbol producido por el gen es el mismo que el árbol a nivel de población o especie. Ambos son resultados comunes en el análisis filogenético, aunque depende del gen, el organismo y la técnica de muestreo.

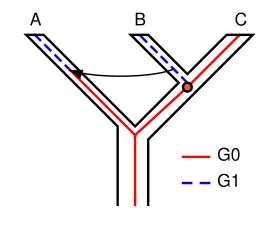
El concepto de clasificación de linaje incompleto tiene algunas implicaciones importantes para las técnicas filogenéticas. La persistencia de polimorfismos en diferentes eventos de especiación puede provocar una clasificación de linaje incompleta. Supongamos que ocurren dos eventos de especiación posteriores en los que una especie ancestral da lugar, en primer lugar, a la especie A y, en segundo lugar, a las especies B y C. Cuando se estudia un solo gen, puede tener múltiples versiones ( alelos ), lo que provoca que aparezcan diferentes caracteres (polimorfismos). En el ejemplo que se muestra en la Figura 1, el gen G tiene dos versiones (alelos), G0 y G1. El antepasado de A, B y C originalmente tenía sólo una versión del gen G, G0. En algún momento, se produjo una mutación y la población ancestral se volvió polimórfica, algunos individuos tenían G0 y otros G1. Cuando la especie A se separó, retuvo sólo G1, mientras que el ancestro de B y C permaneció polimórfico. Cuando B y C divergieron, B retuvo sólo G1 y C sólo G0; ninguno de los dos era ahora polimórfico en G. El árbol del gen G muestra A y B como hermanas, mientras que el árbol de especies muestra a B y C como hermanas. Si la filogenia de estas especies se basa en el gen G, no representará las relaciones reales entre las especies. En otras palabras, las especies más relacionadas no necesariamente heredarán los genes más relacionados. Este es, por supuesto, un ejemplo simplificado de clasificación de linaje incompleta, y en la investigación real suele ser más complejo y contiene más genes y especies. [7] [8]
Sin embargo, otros mecanismos pueden conducir a la misma discordancia aparente; por ejemplo, los alelos pueden cruzar los límites de las especies mediante hibridación y el ADN puede transferirse entre especies mediante virus. [9] Esto se ilustra en la Figura 2. Aquí el antepasado de A, B y C, y el antepasado de B y C, tenían solo la versión G0 del gen G. Se produjo una mutación en la divergencia de B y C, y B adquirió una versión mutada, G1. Algún tiempo después, la flecha muestra que G1 fue transferido de B a A por algún medio (por ejemplo, hibridación o transferencia horizontal de genes). Estudiar sólo los estados finales de G en las tres especies hace que parezca que A y B son hermanas en lugar de B y C, como en la Figura 1, pero en la Figura 2 esto no se debe a una clasificación de linaje incompleta.
La clasificación incompleta de linajes tiene implicaciones importantes para la investigación filogenética. Existe la posibilidad de que al crear un árbol filogenético no se parezca a relaciones reales debido a esta clasificación de linaje incompleta. Sin embargo, el flujo de genes entre linajes mediante hibridación o transferencia horizontal de genes puede producir el mismo árbol filogenético conflictivo. Distinguir estos diferentes procesos puede parecer difícil, pero se están desarrollando muchas investigaciones y diferentes enfoques estadísticos para obtener una mayor comprensión de estas dinámicas evolutivas. [10] Una de las resoluciones para reducir las implicaciones de la clasificación de linajes incompleta es utilizar múltiples genes para crear especies o filogenias de poblaciones. Cuantos más genes se utilizan, más fiable se vuelve la filogenia. [8]
La clasificación de linaje incompleta ocurre comúnmente con la reproducción sexual porque la especie no se puede rastrear hasta una sola persona o pareja reproductora. Cuando las poblaciones de tribus de organismos son grandes (es decir, miles), cada gen tiene cierta diversidad y el árbol genético consta de otros linajes preexistentes. Si la población es mayor, estos linajes ancestrales persistirán por más tiempo. Cuando se juntan grandes poblaciones ancestrales con eventos de especiación en fechas cercanas, estas diferentes piezas de ADN conservan afiliaciones en conflicto. Esto dificulta determinar un ancestro común o puntos de ramificación. [5]
Al estudiar los primates, los chimpancés y los bonobos están más relacionados entre sí que cualquier otro taxón y, por tanto, son taxones hermanos . Aún así, para el 1,6% del genoma del bonobo, las secuencias están más estrechamente relacionadas con homólogos de humanos que con chimpancés, lo que probablemente sea el resultado de una clasificación de linaje incompleta. [5] Un estudio de más de 23.000 alineaciones de secuencias de ADN en la familia Hominidae (grandes simios, incluidos los humanos) mostró que alrededor del 23% no apoyaba la conocida relación hermana de chimpancés y humanos. [9]
En la evolución humana, la clasificación de linajes incompleta se utiliza para diagramar los linajes de homínidos que pueden no haber logrado clasificarse al mismo tiempo que ocurrió la especiación en la prehistoria. [11] Debido a la llegada de las pruebas genéticas y la secuenciación del genoma, los investigadores descubrieron que las relaciones genéticas entre los linajes de homínidos podrían no estar de acuerdo con las comprensiones previas de su relación basada en características físicas. [11] Además, la divergencia del último ancestro común (LCA) no necesariamente puede ocurrir al mismo tiempo que la especiación. [12] La clasificación de linajes es un método que permite a los paleoantropólogos explorar las relaciones y divergencias genéticas que pueden no encajar con sus modelos de especiación anteriores basados únicamente en la filogenia . [11]
La clasificación incompleta del linaje del árbol genealógico humano es un área de gran interés. Hay una serie de incógnitas al considerar tanto la transición de los humanos arcaicos a los humanos modernos como la divergencia de los otros grandes simios del linaje de los homínidos. [13]
La clasificación de linaje incompleta significa que el tiempo de divergencia promedio entre genes puede diferir del tiempo de divergencia entre especies. Los modelos sugieren que el tiempo promedio de divergencia entre los genes del genoma humano y del chimpancé es más antiguo que la división entre humanos y gorilas. Lo que esto significa es que el ancestro común de humanos y chimpancés ha dejado rastros de material genético que estaba presente en el ancestro común de humanos, chimpancés y gorilas. [12] Sin embargo, el árbol genético difiere ligeramente del de especies o árbol de filogenia. [14] En el árbol de filogenia, cuando observamos la relación evolutiva entre el ser humano, el chimpancé bonobo y el gorila, los resultados muestran que la separación del bonobo y el chimpancé se produjo en una proximidad temporal cercana al ancestro común del bonobo-chimpancé. ancestro y humanos, [12] lo que indica que los humanos y los chimpancés compartieron un ancestro común durante varios millones de años después de la separación de los gorilas. Esto crea el fenómeno de clasificación de linaje incompleta. Hoy en día, los investigadores confían en fragmentos de ADN para estudiar las relaciones evolutivas entre los humanos y sus homólogos con la esperanza de que proporcionen información sobre la especiación y los procesos ancestrales a partir de genomas de diferentes tipos de humanos. [15]

La clasificación de linaje incompleta es una característica común en la filodinámica viral , donde la filogenia representada por la transmisión de una enfermedad de una persona a otra, es decir, el árbol a nivel de población, a menudo no corresponde al árbol creado a partir de un análisis genético debido a los cuellos de botella demográficos que son una característica inherente de la transmisión viral de enfermedades. La Figura 3 ilustra cómo puede ocurrir esto. Esto tiene importancia para la transmisión criminal del VIH , donde en algunos casos penales se ha utilizado un análisis filogenético de uno o dos genes de las cepas del acusado y de la víctima para inferir la transmisión; sin embargo, la similitud de la clasificación de linaje incompleta significa que la transmisión no puede inferirse únicamente sobre la base de un análisis tan básico. [dieciséis]
Jacques y List (2019) [17] muestran que el concepto de clasificación de linaje incompleto se puede aplicar para explicar fenómenos no arbóreos en la evolución del lenguaje. Kalyan y François (2019), defensores del método de glotometría histórica , un modelo que desafía la aplicabilidad del modelo de árbol en lingüística histórica, coinciden en que "la glotometría histórica no desafía el modelo de árbol genealógico una vez que se ha tenido en cuenta la clasificación de linaje incompleta. " [18]
{{cite book}}: Mantenimiento CS1: falta el editor de la ubicación ( enlace )