La ATP sintasa es una enzima que cataliza la formación de la molécula de almacenamiento de energía trifosfato de adenosina (ATP) utilizando difosfato de adenosina (ADP) y fosfato inorgánico (P i ). La ATP sintasa es una máquina molecular . La reacción general catalizada por la ATP sintasa es:
La ATP sintasa se encuentra a través de la membrana celular y forma una abertura que los protones pueden cruzar desde áreas de alta concentración a áreas de baja concentración, impartiendo energía para la síntesis de ATP. Este gradiente electroquímico es generado por la cadena de transporte de electrones y permite a las células almacenar energía en ATP para su uso posterior. En las células procariotas, la ATP sintasa se encuentra a través de la membrana plasmática , mientras que en las células eucariotas se encuentra a través de la membrana mitocondrial interna . Los organismos capaces de realizar la fotosíntesis también tienen ATP sintasa a través de la membrana tilacoide , que en las plantas se encuentra en el cloroplasto y en las cianobacterias se encuentra en el citoplasma .
Las ATP sintetasas eucariotas son F-ATPasas , que funcionan "en sentido inverso" a una ATPasa . Este artículo trata principalmente de este tipo. Una F-ATPasa consta de dos subunidades principales, F O y F 1 , que tienen un mecanismo motor rotatorio que permite la producción de ATP. [1] [2]
La fracción F 1 deriva su nombre del término "Fracción 1" y F O (escrito como una letra subíndice "o", no "cero") deriva su nombre de ser la fracción de unión para la oligomicina , un tipo de antibiótico de origen natural que es capaz de inhibir la unidad F O de la ATP sintasa. [3] [4] Estas regiones funcionales consisten en diferentes subunidades proteicas; consulte las tablas. Esta enzima se utiliza en la síntesis de ATP a través de la respiración aeróbica.



Ubicada dentro de la membrana tilacoide y la membrana mitocondrial interna , la ATP sintasa consta de dos regiones F O y F 1 . F O causa la rotación de F 1 y está hecha de un anillo c y subunidades a, dos b, F6. F 1 está hecha de subunidades α, β, γ y δ. F 1 tiene una parte soluble en agua que puede hidrolizar ATP. F O por otro lado tiene regiones principalmente hidrofóbicas. F O F 1 crea una vía para el movimiento de protones a través de la membrana. [7]
La porción F 1 de la ATP sintasa es hidrófila y se encarga de hidrolizar el ATP. La unidad F 1 sobresale hacia el espacio de la matriz mitocondrial . Las subunidades α y β forman un hexámero con 6 sitios de unión. Tres de ellos son catalíticamente inactivos y se unen al ADP.
Otras tres subunidades catalizan la síntesis de ATP. Las otras subunidades F 1 γ, δ y ε son parte de un mecanismo motor rotacional (rotor/eje). La subunidad γ permite que β pase por cambios conformacionales (es decir, estados cerrado, semiabierto y abierto) que permiten que el ATP se una y se libere una vez sintetizado. La partícula F 1 es grande y se puede ver en el microscopio electrónico de transmisión mediante tinción negativa. [8] Estas son partículas de 9 nm de diámetro que salpican la membrana mitocondrial interna.

F O es una proteína insoluble en agua con ocho subunidades y un anillo transmembrana. El anillo tiene una forma tetramérica con una proteína hélice-bucle-hélice que pasa por cambios conformacionales cuando se protona y desprotona, empujando a las subunidades vecinas a rotar, causando el giro de F O que luego también afecta la conformación de F 1 , lo que resulta en el cambio de estados de las subunidades alfa y beta. La región F O de la ATP sintasa es un poro de protones que está incrustado en la membrana mitocondrial. Consta de tres subunidades principales, a, b y c. Seis subunidades c forman el anillo rotor, y la subunidad b forma un tallo que se conecta a F 1 OSCP que evita que el hexámero αβ rote. La subunidad a conecta b al anillo c. [11] Los humanos tienen seis subunidades adicionales, d , e , f , g , F6 y 8 (o A6L). Esta parte de la enzima se encuentra en la membrana interna mitocondrial y acopla la translocación de protones a la rotación que provoca la síntesis de ATP en la región F 1 .
En los eucariotas, el F O mitocondrial forma dímeros que doblan la membrana. Estos dímeros se autoorganizan en largas filas al final de las crestas , posiblemente el primer paso de la formación de las crestas. [12] Se determinó un modelo atómico para la región dimérica del F O de la levadura mediante crio-EM a una resolución general de 3,6 Å. [13]

Entre los años 1960 y 1970, Paul Boyer , profesor de la UCLA , desarrolló la teoría del mecanismo de cambio de enlace, o flip-flop, que postulaba que la síntesis de ATP depende de un cambio conformacional en la ATP sintasa generado por la rotación de la subunidad gamma. El grupo de investigación de John E. Walker , entonces en el Laboratorio de Biología Molecular del MRC en Cambridge , cristalizó el dominio catalítico F 1 de la ATP sintasa. La estructura, en ese momento la estructura proteica asimétrica más grande conocida, indicó que el modelo de catálisis rotatoria de Boyer era, en esencia, correcto. Por dilucidar esto, Boyer y Walker compartieron la mitad del Premio Nobel de Química de 1997 .
La estructura cristalina de la F 1 mostró subunidades alfa y beta alternas (3 de cada una), dispuestas como segmentos de una naranja alrededor de una subunidad gamma asimétrica rotatoria. Según el modelo actual de síntesis de ATP (conocido como el modelo catalítico alterno), el potencial transmembrana creado por los cationes de protones (H+) suministrados por la cadena de transporte de electrones, impulsa a los cationes de protones (H+) desde el espacio intermembrana a través de la membrana mediante la región F O de la ATP sintasa. Una porción del F O (el anillo de subunidades c ) gira a medida que los protones pasan a través de la membrana. El anillo c está firmemente unido al tallo central asimétrico (que consiste principalmente en la subunidad gamma), lo que hace que gire dentro de la alfa 3 beta 3 de F 1, lo que hace que los 3 sitios de unión de nucleótidos catalíticos pasen por una serie de cambios conformacionales que conducen a la síntesis de ATP. Las subunidades principales de F 1 no pueden rotar en simpatía con el rotor del tallo central debido a un tallo periférico que une la alfa 3 beta 3 a la porción no rotatoria de F O . La estructura de la ATP sintasa intacta se conoce actualmente a baja resolución a partir de estudios de criomicroscopía electrónica (crio-EM) del complejo. El modelo crio-EM de la ATP sintasa sugiere que el tallo periférico es una estructura flexible que envuelve el complejo a medida que une F 1 a F O . En las condiciones adecuadas, la reacción enzimática también se puede llevar a cabo a la inversa, con la hidrólisis de ATP impulsando el bombeo de protones a través de la membrana.
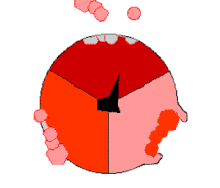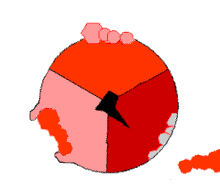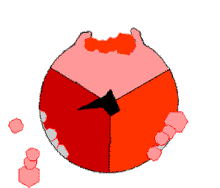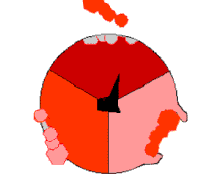
El mecanismo de cambio de unión implica el ciclo del sitio activo de una subunidad β entre tres estados. [14] En el estado "suelto", el ADP y el fosfato entran en el sitio activo; en el diagrama adyacente, esto se muestra en rosa. La enzima luego experimenta un cambio de forma y fuerza a estas moléculas a unirse, con el sitio activo en el estado "apretado" resultante (mostrado en rojo) uniendo la molécula de ATP recién producida con una afinidad muy alta . Finalmente, el sitio activo vuelve al estado abierto (naranja), liberando ATP y uniendo más ADP y fosfato, listo para el siguiente ciclo de producción de ATP. [15]
Al igual que otras enzimas, la actividad de la F 1 F O ATP sintasa es reversible. Cantidades suficientemente grandes de ATP hacen que se cree un gradiente de protones transmembrana , que es utilizado por bacterias fermentadoras que no tienen una cadena de transporte de electrones, sino que hidrolizan el ATP para formar un gradiente de protones, que utilizan para impulsar los flagelos y el transporte de nutrientes hacia el interior de la célula.
En las bacterias que respiran en condiciones fisiológicas, la ATP sintasa, en general, funciona en la dirección opuesta, creando ATP mientras utiliza la fuerza motriz de protones creada por la cadena de transporte de electrones como fuente de energía. El proceso general de creación de energía de esta manera se denomina fosforilación oxidativa . El mismo proceso tiene lugar en las mitocondrias , donde la ATP sintasa se encuentra en la membrana mitocondrial interna y la parte F 1 se proyecta hacia la matriz mitocondrial . Al bombear cationes de protones hacia la matriz, la ATP sintasa convierte el ADP en ATP.
Se cree que la evolución de la ATP sintasa ha sido modular, por lo que dos subunidades funcionalmente independientes se asociaron y adquirieron una nueva funcionalidad. [16] [17] Esta asociación parece haber ocurrido temprano en la historia evolutiva, porque esencialmente la misma estructura y actividad de las enzimas ATP sintasa están presentes en todos los reinos de la vida. [16] La F-ATP sintasa muestra una gran similitud funcional y mecanicista con la V-ATPasa . [18] Sin embargo, mientras que la F-ATP sintasa genera ATP utilizando un gradiente de protones, la V-ATPasa genera un gradiente de protones a expensas del ATP, generando valores de pH tan bajos como 1. [19]
La región F 1 también muestra una similitud significativa con las helicasas de ADN hexaméricas (especialmente el factor Rho ), y toda la región enzimática muestra cierta similitud con H+
-complejos motores flagelares o T3SS potenciados . [18] [20] [21] El hexámero α 3 β 3 de la región F 1 muestra una similitud estructural significativa con las helicasas de ADN hexaméricas; ambas forman un anillo con simetría rotacional triple con un poro central. Ambas tienen funciones que dependen de la rotación relativa de una macromolécula dentro del poro; las helicasas de ADN utilizan la forma helicoidal del ADN para impulsar su movimiento a lo largo de la molécula de ADN y para detectar el superenrollamiento, mientras que el hexámero α 3 β 3 utiliza los cambios conformacionales a través de la rotación de la subunidad γ para impulsar una reacción enzimática. [22]
La H+
El motor de la partícula F O muestra una gran similitud funcional con el H+
motores que impulsan los flagelos. [18] Ambos presentan un anillo de muchas proteínas alfa-helicoidales pequeñas que giran en relación con las proteínas estacionarias cercanas, utilizando un H+
gradiente de potencial como fuente de energía. Sin embargo, este vínculo es tenue, ya que la estructura general de los motores flagelares es mucho más compleja que la de la partícula F O y el anillo con aproximadamente 30 proteínas rotatorias es mucho más grande que las 10, 11 o 14 proteínas helicoidales del complejo F O. Sin embargo, datos estructurales más recientes muestran que el anillo y el tallo son estructuralmente similares a la partícula F 1. [21]
La teoría de la evolución modular para el origen de la ATP sintasa sugiere que existen dos subunidades con función independiente, una helicasa de ADN con actividad ATPasa y una H+
motor, pudieron unirse, y la rotación del motor impulsó la actividad ATPasa de la helicasa en sentido inverso. [16] [22] Este complejo luego desarrolló una mayor eficiencia y finalmente se convirtió en las intrincadas sintasas de ATP actuales. Alternativamente, la helicasa de ADN/ H+
El complejo motor pudo haber tenido H+
Actividad de bombeo con la actividad ATPasa de la helicasa que impulsa la H+
motor en reversa. [16] Esto puede haber evolucionado para llevar a cabo la reacción inversa y actuar como una ATP sintasa. [17] [23] [24]
Se han descubierto diversos inhibidores naturales y sintéticos de la ATP sintasa. [25] Estos se han utilizado para investigar la estructura y el mecanismo de la ATP sintasa. Algunos pueden tener uso terapéutico. Existen varias clases de inhibidores de la ATP sintasa, incluidos inhibidores de péptidos, fitoquímicos polifenólicos, policétidos, compuestos organoestánnicos, derivados poliénicos de α-pirona, inhibidores catiónicos, análogos de sustrato, modificadores de aminoácidos y otros productos químicos diversos. [25] Algunos de los inhibidores de la ATP sintasa más utilizados son la oligomicina y el DCCD .
La ATP sintasa de E. coli es la forma más simple conocida de ATP sintasa, con 8 tipos de subunidades diferentes.[11]
Las F-ATPasas bacterianas pueden ocasionalmente operar a la inversa, convirtiéndolas en una ATPasa. [26] Algunas bacterias no tienen F-ATPasa, y utilizan una ATPasa de tipo A/V de forma bidireccional. [9]
La ATP sintasa de levadura es una de las ATP sintasas eucariotas mejor estudiadas; se han identificado cinco subunidades F 1 , ocho subunidades F O y siete proteínas asociadas. [7] La mayoría de estas proteínas tienen homólogos en otros eucariotas. [27] [28] [29] [30]
En las plantas, la ATP sintasa también está presente en los cloroplastos (CF 1 F O -ATP sintasa). La enzima está integrada en la membrana del tilacoide ; la parte CF 1 se adhiere al estroma , donde tienen lugar las reacciones oscuras de la fotosíntesis (también llamadas reacciones independientes de la luz o ciclo de Calvin ) y la síntesis de ATP. La estructura general y el mecanismo catalítico de la ATP sintasa del cloroplasto son casi los mismos que los de la enzima bacteriana. Sin embargo, en los cloroplastos, la fuerza motriz de protones no se genera por la cadena de transporte de electrones respiratorios sino por proteínas fotosintéticas primarias. La sintasa tiene un inserto de 40 aa en la subunidad gamma para inhibir la actividad derrochadora cuando está oscuro. [31]
La ATP sintasa aislada de las mitocondrias del corazón bovino ( Bos taurus ) es, en términos de bioquímica y estructura, la ATP sintasa mejor caracterizada. El corazón de vacuno se utiliza como fuente de la enzima debido a la alta concentración de mitocondrias en el músculo cardíaco. Sus genes tienen una homología cercana con las ATP sintasas humanas. [32] [33] [34]
Genes humanos que codifican componentes de las ATP sintasas:
Los eucariotas que pertenecen a algunos linajes divergentes tienen organizaciones muy especiales de la ATP sintasa. Una ATP sintasa de euglenozoos forma un dímero con una cabeza F 1 en forma de bumerán como otras ATP sintasas mitocondriales, pero el subcomplejo F O tiene muchas subunidades únicas. Utiliza cardiolipina . El inhibidor IF 1 también se une de manera diferente, de una manera compartida con los tripanosomatida . [35]
Las arqueas no suelen tener una F-ATPasa, sino que sintetizan ATP utilizando la A-ATPasa/sintasa, una máquina rotatoria estructuralmente similar a la V-ATPasa pero que funciona principalmente como una ATP sintasa. [26] Al igual que la F-ATPasa bacteriana, se cree que también funciona como una ATPasa. [9]
El enlace genético y el orden genético de la F-ATPasa están ampliamente conservados en los linajes procariotas antiguos, lo que implica que este sistema ya existía en una fecha anterior al último ancestro común universal , el LUCA. [36]