
En biología molecular , la agregación de proteínas es un fenómeno en el que proteínas intrínsecamente desordenadas o mal plegadas se agregan (es decir, se acumulan y agrupan) ya sea intra o extracelularmente. [1] [2] Los agregados de proteínas han sido implicados en una amplia variedad de enfermedades conocidas como amiloidosis , incluidas la ELA , el Alzheimer , el Parkinson y la enfermedad priónica . [3] [4]
Después de la síntesis, las proteínas normalmente se pliegan en una conformación tridimensional particular que es la más termodinámicamente favorable : su estado nativo . [5] Este proceso de plegamiento es impulsado por el efecto hidrofóbico : una tendencia de las porciones hidrofóbicas (que temen al agua) de la proteína a protegerse del entorno hidrofílico (amantes del agua) de la célula enterrándose en el interior de la proteína. Por tanto, el exterior de una proteína suele ser hidrófilo, mientras que el interior suele ser hidrófobo.
Las estructuras de las proteínas se estabilizan mediante interacciones no covalentes y enlaces disulfuro entre dos residuos de cisteína . Las interacciones no covalentes incluyen interacciones iónicas e interacciones débiles de van der Waals . Se forman interacciones iónicas entre un anión y un catión y forman puentes salinos que ayudan a estabilizar la proteína. Las interacciones de Van der Waals incluyen interacciones no polares (es decir, fuerza de dispersión de London ) e interacciones polares (es decir, enlaces de hidrógeno , enlaces dipolo-dipolo ). Estos juegan un papel importante en la estructura secundaria de una proteína , como la formación de una hélice alfa o una lámina beta , y la estructura terciaria. Las interacciones entre residuos de aminoácidos en una proteína específica son muy importantes en la estructura final de esa proteína.
Cuando hay cambios en las interacciones no covalentes, como puede ocurrir con un cambio en la secuencia de aminoácidos, la proteína es susceptible de plegarse o desplegarse mal. En estos casos, si la célula no ayuda a la proteína a replegarse o degradar la proteína desplegada, la proteína desplegada/mal plegada puede agregarse, en la que las porciones hidrófobas expuestas de la proteína pueden interactuar con los parches hidrófobos expuestos de otras proteínas. . [6] [7] Hay tres tipos principales de agregados de proteínas que pueden formarse: agregados amorfos, oligómeros y fibrillas de amiloide . [8]
La agregación de proteínas puede ocurrir debido a una variedad de causas. Hay cuatro clases en las que se pueden clasificar estas causas, que se detallan a continuación.
Las mutaciones que ocurren en la secuencia del ADN pueden afectar o no la secuencia de aminoácidos de la proteína. Cuando la secuencia se ve afectada, un aminoácido diferente puede cambiar las interacciones entre las cadenas laterales que afectan el plegamiento de la proteína. Esto puede llevar a regiones hidrofóbicas expuestas de la proteína que se agregan con la misma proteína mal plegada/desplegada o con una proteína diferente. [9]
Además de las mutaciones en las propias proteínas afectadas, la agregación de proteínas también podría deberse indirectamente a través de mutaciones en proteínas en vías reguladoras como la vía de replegamiento ( chaperonas moleculares ) o la vía ubiquitina-proteosoma (ubiquitina ligasas). [10] Los acompañantes ayudan con el replegamiento de proteínas al proporcionar un ambiente seguro para que la proteína se pliegue. Las ubiquitina ligasas se dirigen a las proteínas para su degradación mediante la modificación de la ubiquitina. [11]
La agregación de proteínas puede deberse a problemas que ocurren durante la transcripción o traducción . Durante la transcripción, el ADN se copia en ARNm, formando una hebra de pre-ARNm que se procesa para formar ARNm. [12] Durante la traducción, los ribosomas y el ARNt ayudan a traducir la secuencia del ARNm en una secuencia de aminoácidos. [12] Si surgen problemas durante cualquiera de los pasos, al producir una cadena de ARNm incorrecta y/o una secuencia de aminoácidos incorrecta, esto puede causar que la proteína se pliegue mal, lo que lleva a la agregación de proteínas. [ cita necesaria ]
El estrés ambiental, como las temperaturas extremas y el pH o el estrés oxidativo, también pueden provocar la agregación de proteínas. [13] Una de esas enfermedades es la crioglobulinemia .
Las temperaturas extremas pueden debilitar y desestabilizar las interacciones no covalentes entre los residuos de aminoácidos. Los pH fuera del rango de pH de la proteína pueden cambiar el estado de protonación de los aminoácidos, lo que puede aumentar o disminuir las interacciones no covalentes. Esto también puede conducir a interacciones menos estables y provocar el desarrollo de proteínas.
El estrés oxidativo puede ser causado por radicales como las especies reactivas de oxígeno (ROS). Estos radicales inestables pueden atacar los residuos de aminoácidos, provocando la oxidación de las cadenas laterales (por ejemplo, cadenas laterales aromáticas , cadenas laterales de metionina ) y/o la escisión de los enlaces polipeptídicos. [14] Esto puede afectar las interacciones no covalentes que mantienen la proteína unida correctamente, lo que puede causar la desestabilización de la proteína y puede hacer que la proteína se despliegue. [13]
Las células tienen mecanismos que pueden replegarse o degradar agregados de proteínas. Sin embargo, a medida que las células envejecen, estos mecanismos de control se debilitan y la célula es menos capaz de resolver los agregados. [13]
La hipótesis de que la agregación de proteínas es un proceso causal del envejecimiento es ahora comprobable, ya que se dispone de algunos modelos de envejecimiento retrasado. Si el desarrollo de agregados de proteínas fuera un proceso independiente del envejecimiento, ralentizar el envejecimiento no mostrará ningún efecto sobre la tasa de proteotoxicidad a lo largo del tiempo. Sin embargo, si el envejecimiento se asocia con una disminución en la actividad de los mecanismos protectores contra la proteotoxicidad, los modelos de envejecimiento lento mostrarían una agregación y proteotoxicidad reducidas. Para abordar este problema se han realizado varios ensayos de toxicidad en C. elegans . Estos estudios indicaron que la reducción de la actividad de la señalización de insulina/IGF (IIS), una importante vía reguladora del envejecimiento, protege de la agregación de proteínas tóxicas relacionada con la neurodegeneración. La validez de este enfoque ha sido probada y confirmada en mamíferos, ya que la reducción de la actividad de la vía de señalización del IGF-1 protegió a los ratones modelo de Alzheimer de los deterioros bioquímicos y de comportamiento asociados con la enfermedad. [15]
Varios estudios han demostrado que las respuestas celulares a la agregación de proteínas están bien reguladas y organizadas. Los agregados de proteínas se localizan en áreas específicas de la célula y se han realizado investigaciones sobre estas localizaciones en procariotas (E. coli) y eucariotas (levaduras, células de mamíferos). [16] Desde el punto de vista macroscópico, los trazadores de tomografía por emisión de positrones se utilizan para determinadas proteínas mal plegadas. [17] Recientemente, un equipo de investigadores dirigido por el Dr. Alessandro Crimi ha propuesto un método de aprendizaje automático para predecir la futura deposición en el cerebro. [18]
Los agregados de las bacterias terminan asimétricamente en uno de los polos de la célula, el "polo más viejo". Después de que la célula se divide, las células hijas con el polo más viejo obtienen el agregado de proteínas y crecen más lentamente que las células hijas sin el agregado. Esto proporciona un mecanismo de selección natural para reducir los agregados de proteínas en la población bacteriana. [19]
La mayoría de los agregados de proteínas en las células de levadura son replegados por chaperonas moleculares. Sin embargo, algunos agregados, como las proteínas dañadas por oxidación o las proteínas marcadas para degradación, no pueden replegarse. Más bien, hay dos compartimentos en los que pueden terminar. Los agregados de proteínas pueden localizarse en el compartimento yuxtanuclear de control de calidad ( JUNQ ), que está cerca de la membrana nuclear, o en el depósito de proteínas insolubles ( IPOD ), cerca de la vacuola en células de levadura. [13] Los agregados de proteínas se localizan en JUNQ cuando están ubiquitinados y son objetivo de degradación. Las proteínas agregadas e insolubles se localizan en IPOD como una deposición más permanente. Existe evidencia de que las proteínas aquí pueden eliminarse mediante autofagia. [20] Estas dos vías funcionan juntas en el sentido de que las proteínas tienden a llegar al IPOD cuando la vía del proteasoma está sobrecargada. [20]
En las células de los mamíferos, estos agregados de proteínas se denominan "agresores" y se forman cuando la célula está enferma. Esto se debe a que tienden a formarse agregados cuando hay proteínas heterólogas presentes en la célula, que pueden surgir cuando la célula sufre una mutación. Diferentes mutaciones de la misma proteína pueden formar agresiones de diferentes morfologías, que van desde la dispersión difusa de especies solubles hasta puntos grandes, que a su vez tienen diferente patogenicidad. [21] La ubiquitina ligasa E3 es capaz de reconocer proteínas mal plegadas y ubiquinarlas. Luego, HDAC6 puede unirse a la ubiquitina y a la proteína motora dineína para llevar los agregados marcados al centro organizador de microtúbulos ( MTOC ). Allí, se agrupan formando una esfera que rodea al MTOC. Traen chaperonas y proteosomas y activan la autofagia. [22]
Existen dos sistemas principales de control de calidad de las proteínas en la célula que se encargan de eliminar los agregados de proteínas. Las proteínas mal plegadas pueden volver a plegarse mediante el sistema bi-chaperona o degradarse mediante el sistema de proteasoma de ubiquitina o la autofagia. [23]
El sistema bi-chaperona utiliza las chaperonas Hsp70 (DnaK-DnaJ-GrpE en E. coli y Ssa1-Ydj1/Sis1-Sse1/Fe1 en levadura) y Hsp100 (ClpB en E. coli y Hsp104 en levadura) para la desagregación y el replegamiento de proteínas. . [24]
Hsp70 interactúa con los agregados de proteínas y recluta Hsp100. Hsp70 estabiliza una Hsp100 activada. Las proteínas Hsp100 tienen bucles de poros aromáticos que se utilizan para la actividad de enhebrado para desenredar polipéptidos individuales. Esta actividad de enhebrado puede iniciarse en el extremo N, el extremo C o en el medio del polipéptido. El polipéptido se transloca a través de Hsp100 en una serie de pasos, utilizando un ATP en cada paso. [24] El polipéptido se despliega y luego se le permite replegarse por sí solo o con la ayuda de proteínas de choque térmico. [25]
Las proteínas mal plegadas se pueden eliminar mediante el sistema ubiquitina-proteasoma ( UPS ). Consiste en una vía E1-E2-E3 que ubiquina las proteínas para marcarlas para su degradación. En los eucariotas, las proteínas son degradadas por el proteosoma 26S. En las células de mamíferos, la ligasa E3, proteína que interactúa con Hsp70 carboxi-terminal (CHIP), se dirige a las proteínas unidas a Hsp70. En la levadura, las ligasas E3 Doa10 y Hrd1 tienen funciones similares en las proteínas del retículo endoplásmico . [26] A nivel molecular, la tasa de degradación de los agregados varía de una proteína a otra debido a sus diferentes entornos internos y, por lo tanto, a la diferente accesibilidad de las moléculas de proteasa. [27]

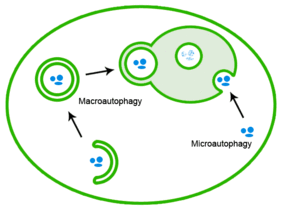
Las proteínas mal plegadas también se pueden eliminar mediante autofagia, en la que los agregados de proteínas se entregan al lisosoma. [26]
Aunque se ha pensado que los agregados de proteínas maduras son tóxicos en sí mismos, la evidencia sugiere que, de hecho, son los agregados de proteínas inmaduros los más tóxicos. [28] [29] Los parches hidrofóbicos de estos agregados pueden interactuar con otros componentes de la célula y dañarlos. Las hipótesis son que la toxicidad de los agregados proteicos está relacionada con mecanismos de secuestro de componentes celulares, la generación de especies reactivas de oxígeno y la unión a receptores específicos en la membrana o mediante la alteración de membranas. [30] Se ha utilizado un ensayo cuantitativo para determinar que especies de mayor peso molecular son responsables de la permeación de la membrana. [31] Se sabe que los agregados de proteínas in vitro pueden desestabilizar las bicapas de fosfolípidos artificiales , lo que lleva a la permeabilización de la membrana. [ cita necesaria ]
La agregación de proteínas también es un fenómeno común en el proceso de fabricación biofarmacéutica, que puede suponer riesgos para los pacientes al generar respuestas inmunitarias adversas. [32]