Bacterias ( / b æ k ˈ t ɪər i ə / ;sg.: bacteria) son organismos ubicuos, en su mayoría de vida libre, que a menudo consisten en unacélula biológica. Constituyen un grandominiodemicroorganismosprocariotas . Por lo general, de unos pocosmicrómetrosde longitud, las bacterias estuvieron entre las primeras formas de vida que aparecieron enla Tierray están presentes en la mayoría de sushábitats. Las bacterias habitan el suelo, el agua,las fuentes termales ácidas,los desechos radiactivosy labiosfera profundadecorteza terrestre. Las bacterias desempeñan un papel vital en muchas etapas delciclo de los nutrientesal reciclar nutrientes y lafijación de nitrógenode laatmósfera. El ciclo de los nutrientes incluye ladescomposicióndecadáveres; las bacterias son responsables de lade putrefacciónen este proceso. En las comunidades biológicas que rodeanlos respiraderos hidrotermalesylas filtraciones frías,extremófilasproporcionan los nutrientes necesarios para mantener la vida al convertir compuestos disueltos, comoel sulfuro de hidrógenoyel metano, en energía. Las bacterias también viven enmutualistas,comensalesyparasitariascon plantas y animales. La mayoría de las bacterias no han sido caracterizadas y hay muchas especies que no se puedencultivaren el laboratorio. El estudio de las bacterias se conoce comobacteriología, una rama dela microbiología.
Al igual que todos los animales, los seres humanos son portadores de una gran cantidad de bacterias (aproximadamente entre 10 13 y 10 14 ). [2] La mayoría se encuentran en el intestino , aunque hay muchas en la piel. La mayoría de las bacterias que se encuentran en el interior y exterior del cuerpo son inofensivas o se vuelven inofensivas gracias a los efectos protectores del sistema inmunitario , y muchas son beneficiosas , [3] en particular las que se encuentran en el intestino. Sin embargo, varias especies de bacterias son patógenas y causan enfermedades infecciosas , como el cólera , la sífilis , el ántrax , la lepra , la tuberculosis , el tétanos y la peste bubónica . Las enfermedades bacterianas mortales más comunes son las infecciones respiratorias . Los antibióticos se utilizan para tratar las infecciones bacterianas y también se utilizan en la agricultura, lo que hace que la resistencia a los antibióticos sea un problema creciente. Las bacterias son importantes en el tratamiento de aguas residuales y la descomposición de derrames de petróleo , la producción de queso y yogur mediante fermentación , la recuperación de oro, paladio , cobre y otros metales en el sector minero ( biominería , biolixiviación ), así como en la biotecnología y la fabricación de antibióticos y otros productos químicos.
Las bacterias , que en el pasado eran plantas que formaban parte de la clase Schizomycetes ("hongos de fisión"), ahora se clasifican como procariotas . A diferencia de las células de los animales y otros eucariotas , las células bacterianas no contienen un núcleo y rara vez albergan orgánulos rodeados de membranas . Aunque el término bacteria incluía tradicionalmente a todos los procariotas, la clasificación científica cambió después del descubrimiento en la década de 1990 de que los procariotas consisten en dos grupos muy diferentes de organismos que evolucionaron a partir de un ancestro común antiguo . Estos dominios evolutivos se denominan Bacteria y Archaea . [4]

La palabra bacteria es el plural del neolatino bacterium , que es la latinización del griego antiguo βακτήριον ( baktḗrion ), [5] el diminutivo de βακτηρία ( baktēría ), que significa "bastón, bastón", [6] porque los primeros que se descubrieron tenían forma de bastón . [7] [8]

Los ancestros de las bacterias eran microorganismos unicelulares que fueron las primeras formas de vida que aparecieron en la Tierra, hace unos 4 mil millones de años. [10] Durante unos 3 mil millones de años, la mayoría de los organismos eran microscópicos, y las bacterias y las arqueas eran las formas de vida dominantes. [11] [12] [13] Aunque existen fósiles bacterianos , como los estromatolitos , su falta de morfología distintiva impide que se utilicen para examinar la historia de la evolución bacteriana o para fechar el momento del origen de una especie bacteriana en particular. Sin embargo, las secuencias genéticas se pueden utilizar para reconstruir la filogenia bacteriana , y estos estudios indican que las bacterias divergieron primero del linaje arqueal/eucariota. [14] El ancestro común más reciente (MRCA) de bacterias y arqueas fue probablemente un hipertermófilo que vivió hace unos 2500 millones a 3200 millones de años. [15] [16] [17] La vida más temprana en la tierra puede haber sido la de las bacterias hace unos 3220 millones de años. [18]
Las bacterias también estuvieron involucradas en la segunda gran divergencia evolutiva, la de las arqueas y los eucariotas. [19] [20] Aquí, los eucariotas resultaron de la entrada de bacterias antiguas en asociaciones endosimbióticas con los ancestros de las células eucariotas, que posiblemente estaban relacionadas con las arqueas. [21] [22] Esto implicó la fagocitosis por parte de células protoeucariotas de simbiontes alfaproteobacterianos para formar mitocondrias o hidrogenosomas , que todavía se encuentran en todos los Eukarya conocidos (a veces en forma altamente reducida , por ejemplo, en los antiguos protozoos "amitocondriales"). Más tarde, algunos eucariotas que ya contenían mitocondrias también fagocitaron organismos similares a las cianobacterias , lo que llevó a la formación de cloroplastos en algas y plantas. Esto se conoce como endosimbiosis primaria . [23]
Las bacterias son omnipresentes y viven en todos los hábitats posibles del planeta, incluido el suelo, el agua, las profundidades de la corteza terrestre e incluso en entornos tan extremos como las fuentes termales ácidas y los residuos radiactivos. [24] [25] Se cree que hay aproximadamente 2×10 30 bacterias en la Tierra, [26] formando una biomasa que solo es superada por las plantas. [27] Son abundantes en lagos y océanos, en el hielo ártico y en los manantiales geotermales [28] donde proporcionan los nutrientes necesarios para sustentar la vida al convertir compuestos disueltos, como el sulfuro de hidrógeno y el metano , en energía. [29] Viven sobre y en plantas y animales. La mayoría no causan enfermedades, son beneficiosas para sus entornos y son esenciales para la vida. [3] [30] El suelo es una rica fuente de bacterias y unos pocos gramos contienen alrededor de mil millones de ellas. Todas son esenciales para la ecología del suelo, descomponiendo los desechos tóxicos y reciclando los nutrientes. Incluso se encuentran en la atmósfera y un metro cúbico de aire contiene alrededor de cien millones de células bacterianas. Los océanos y los mares albergan alrededor de 3 x 10 26 bacterias que proporcionan hasta el 50% del oxígeno que respiramos los humanos. [31] Solo alrededor del 2% de las especies bacterianas han sido completamente estudiadas. [32]
Tamaño . Las bacterias presentan una amplia diversidad de formas y tamaños. Las células bacterianas tienen aproximadamente una décima parte del tamaño de las células eucariotas y suelen tener una longitud de entre 0,5 y 5,0 micrómetros . Sin embargo, algunas especies son visibles a simple vista; por ejemplo, Thiomargarita namibiensis mide hasta medio milímetro de largo, [34] Epulopiscium fishelsoni alcanza los 0,7 mm, [35] y Thiomargarita magnifica puede alcanzar incluso los 2 cm de longitud, que es 50 veces más grande que otras bacterias conocidas. [36] [37] Entre las bacterias más pequeñas se encuentran los miembros del género Mycoplasma , que miden solo 0,3 micrómetros, tan pequeños como los virus más grandes . [38] Algunas bacterias pueden ser incluso más pequeñas, pero estas ultramicrobacterias no están bien estudiadas. [39]
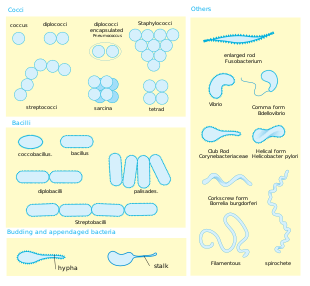
Forma . La mayoría de las especies bacterianas son esféricas, llamadas cocos ( singular coccus , del griego kókkos , grano, semilla), o con forma de bastón, llamadas bacilos ( singular bacillus, del latín baculus , palo). [40] Algunas bacterias, llamadas vibrio , tienen forma de bastón ligeramente curvado o de coma; otras pueden tener forma de espiral, llamadas espirilas , o estar muy enrolladas, llamadas espiroquetas . Se han descrito una pequeña cantidad de otras formas inusuales, como las bacterias con forma de estrella. [41] Esta amplia variedad de formas está determinada por la pared celular bacteriana y el citoesqueleto y es importante porque puede influir en la capacidad de las bacterias para adquirir nutrientes, adherirse a superficies, nadar a través de líquidos y escapar de los depredadores . [42] [43]

Multicelularidad . La mayoría de las especies bacterianas existen como células individuales; otras se asocian en patrones característicos: Neisseria forma diploides (pares), los estreptococos forman cadenas y los estafilococos se agrupan en racimos de "racimos de uvas". Las bacterias también pueden agruparse para formar estructuras multicelulares más grandes, como los filamentos alargados de las especies de Actinomycetota , los agregados de las especies de Myxobacteria y las hifas complejas de las especies de Streptomyces . [45] Estas estructuras multicelulares a menudo solo se ven en ciertas condiciones. Por ejemplo, cuando carecen de aminoácidos, las mixobacterias detectan las células circundantes en un proceso conocido como detección de quórum , migran unas hacia otras y se agregan para formar cuerpos fructíferos de hasta 500 micrómetros de largo y que contienen aproximadamente 100.000 células bacterianas. [46] En estos cuerpos fructíferos, las bacterias realizan tareas separadas; Por ejemplo, aproximadamente una de cada diez células migran a la parte superior de un cuerpo fructífero y se diferencian a un estado latente especializado llamado mixospora, que es más resistente a la desecación y otras condiciones ambientales adversas. [47]
Biopelículas . Las bacterias a menudo se adhieren a las superficies y forman agregaciones densas llamadas biopelículas [48] y formaciones más grandes conocidas como tapetes microbianos . [49] Estas biopelículas y tapetes pueden variar desde unos pocos micrómetros de espesor hasta medio metro de profundidad, y pueden contener múltiples especies de bacterias, protistas y arqueas. Las bacterias que viven en biopelículas muestran una disposición compleja de células y componentes extracelulares, formando estructuras secundarias, como microcolonias , a través de las cuales hay redes de canales para permitir una mejor difusión de nutrientes. [50] [51] En entornos naturales, como el suelo o las superficies de las plantas, la mayoría de las bacterias están unidas a las superficies en biopelículas. [52] Las biopelículas también son importantes en medicina, ya que estas estructuras a menudo están presentes durante infecciones bacterianas crónicas o en infecciones de dispositivos médicos implantados , y las bacterias protegidas dentro de las biopelículas son mucho más difíciles de matar que las bacterias individuales aisladas. [53]

La célula bacteriana está rodeada por una membrana celular , que está hecha principalmente de fosfolípidos . Esta membrana encierra el contenido de la célula y actúa como una barrera para retener nutrientes, proteínas y otros componentes esenciales del citoplasma dentro de la célula. [54] A diferencia de las células eucariotas , las bacterias generalmente carecen de grandes estructuras unidas a la membrana en su citoplasma, como un núcleo , mitocondrias , cloroplastos y otros orgánulos presentes en las células eucariotas. [55] Sin embargo, algunas bacterias tienen orgánulos unidos a proteínas en el citoplasma que compartimentan aspectos del metabolismo bacteriano, [56] [57] como el carboxisoma . [58] Además, las bacterias tienen un citoesqueleto de múltiples componentes para controlar la localización de proteínas y ácidos nucleicos dentro de la célula, y para gestionar el proceso de división celular . [59] [60] [61]
Muchas reacciones bioquímicas importantes , como la generación de energía, ocurren debido a gradientes de concentración a través de las membranas, lo que crea una diferencia de potencial análoga a una batería. La falta general de membranas internas en las bacterias significa que estas reacciones, como el transporte de electrones , ocurren a través de la membrana celular entre el citoplasma y el exterior de la célula o periplasma . [62] Sin embargo, en muchas bacterias fotosintéticas, la membrana plasmática está muy plegada y llena la mayor parte de la célula con capas de membrana que recogen luz. [63] Estos complejos que recogen luz pueden incluso formar estructuras encerradas en lípidos llamadas clorosomas en las bacterias verdes del azufre . [64]

Las bacterias no tienen un núcleo rodeado por una membrana y su material genético es típicamente un único cromosoma bacteriano circular de ADN ubicado en el citoplasma en un cuerpo de forma irregular llamado nucleoide . [65] El nucleoide contiene el cromosoma con sus proteínas asociadas y ARN . Al igual que todos los demás organismos , las bacterias contienen ribosomas para la producción de proteínas, pero la estructura del ribosoma bacteriano es diferente a la de los eucariotas y las arqueas. [66]
Algunas bacterias producen gránulos de almacenamiento de nutrientes intracelulares, como glucógeno , [67] polifosfato , [68] azufre [69] o polihidroxialcanoatos . [70] Bacterias como las cianobacterias fotosintéticas , producen vacuolas de gas internas , que utilizan para regular su flotabilidad, lo que les permite moverse hacia arriba o hacia abajo en capas de agua con diferentes intensidades de luz y niveles de nutrientes. [71]
Alrededor del exterior de la membrana celular se encuentra la pared celular . Las paredes celulares bacterianas están hechas de peptidoglicano (también llamado mureína), que está hecho de cadenas de polisacáridos reticuladas por péptidos que contienen D- aminoácidos . [72] Las paredes celulares bacterianas son diferentes de las paredes celulares de las plantas y los hongos , que están hechas de celulosa y quitina , respectivamente. [73] La pared celular de las bacterias también es distinta de la de las aqueas, que no contienen peptidoglicano. La pared celular es esencial para la supervivencia de muchas bacterias, y el antibiótico penicilina (producido por un hongo llamado Penicillium ) es capaz de matar bacterias al inhibir un paso en la síntesis de peptidoglicano. [73]
En líneas generales, existen dos tipos diferentes de pared celular en las bacterias, que las clasifican en bacterias Gram-positivas y bacterias Gram-negativas . Los nombres se originan a partir de la reacción de las células a la tinción de Gram , una prueba de larga data para la clasificación de especies bacterianas. [74]
Las bacterias grampositivas poseen una pared celular gruesa que contiene muchas capas de peptidoglicano y ácidos teicoicos . Por el contrario, las bacterias gramnegativas tienen una pared celular relativamente delgada que consiste en unas pocas capas de peptidoglicano rodeadas por una segunda membrana lipídica que contiene lipopolisacáridos y lipoproteínas . La mayoría de las bacterias tienen la pared celular gramnegativa, y solo los miembros del grupo Bacillota y actinomycetota (anteriormente conocidas como bacterias grampositivas de bajo G+C y alto G+C, respectivamente) tienen la disposición grampositiva alternativa. [75] Estas diferencias en la estructura pueden producir diferencias en la susceptibilidad a los antibióticos; por ejemplo, la vancomicina puede matar solo bacterias grampositivas y es ineficaz contra patógenos gramnegativos , como Haemophilus influenzae o Pseudomonas aeruginosa . [76] Algunas bacterias tienen estructuras de pared celular que no son ni clásicamente grampositivas ni gramnegativas. Esto incluye bacterias clínicamente importantes como las micobacterias, que tienen una pared celular gruesa de peptidoglicano como una bacteria Gram-positiva, pero también una segunda capa externa de lípidos. [77]
En muchas bacterias, una capa S de moléculas de proteína dispuestas de manera rígida cubre el exterior de la célula. [78] Esta capa proporciona protección química y física para la superficie celular y puede actuar como una barrera de difusión macromolecular . Las capas S tienen diversas funciones y se sabe que actúan como factores de virulencia en las especies de Campylobacter y contienen enzimas de superficie en Bacillus stearothermophilus . [79] [80]
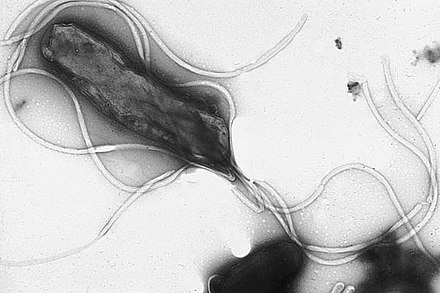
Los flagelos son estructuras proteicas rígidas, de unos 20 nanómetros de diámetro y hasta 20 micrómetros de longitud, que se utilizan para la movilidad . Los flagelos son impulsados por la energía liberada por la transferencia de iones a través de un gradiente electroquímico a través de la membrana celular. [81]
Las fimbrias (a veces llamadas " pili de unión ") son filamentos finos de proteína, generalmente de 2 a 10 nanómetros de diámetro y hasta varios micrómetros de longitud. Se distribuyen sobre la superficie de la célula y se parecen a pelos finos cuando se observan bajo el microscopio electrónico . [82] Se cree que las fimbrias están involucradas en la unión a superficies sólidas o a otras células, y son esenciales para la virulencia de algunos patógenos bacterianos. [83] Los pili ( sing . pilus) son apéndices celulares, ligeramente más grandes que las fimbrias, que pueden transferir material genético entre células bacterianas en un proceso llamado conjugación , donde se denominan pili de conjugación o pili sexuales (ver genética bacteriana, a continuación). [84] También pueden generar movimiento, donde se denominan pili tipo IV . [85]
Muchas bacterias producen el glicocálix para rodear sus células [86] y su complejidad estructural varía: desde una capa viscosa desorganizada de sustancias poliméricas extracelulares hasta una cápsula altamente estructurada . Estas estructuras pueden proteger a las células de ser absorbidas por células eucariotas como los macrófagos (parte del sistema inmunológico humano ). [87] También pueden actuar como antígenos y participar en el reconocimiento celular, además de ayudar a la adhesión a las superficies y la formación de biopelículas. [88]
El ensamblaje de estas estructuras extracelulares depende de los sistemas de secreción bacterianos , que transfieren proteínas desde el citoplasma al periplasma o al entorno que rodea a la célula. Se conocen muchos tipos de sistemas de secreción y estas estructuras suelen ser esenciales para la virulencia de los patógenos, por lo que se estudian intensamente. [88]
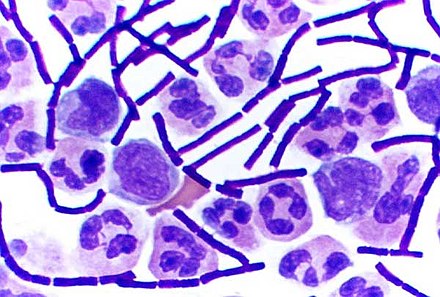
Algunos géneros de bacterias Gram-positivas, como Bacillus , Clostridium , Sporohalobacter , Anaerobacter y Heliobacterium , pueden formar estructuras latentes y altamente resistentes llamadas endosporas . [90] Las endosporas se desarrollan dentro del citoplasma de la célula; generalmente, se desarrolla una sola endospora en cada célula. [91] Cada endospora contiene un núcleo de ADN y ribosomas rodeado por una capa de corteza y protegido por una capa rígida multicapa compuesta de peptidoglicano y una variedad de proteínas. [91]
Las endosporas no muestran un metabolismo detectable y pueden sobrevivir a tensiones físicas y químicas extremas, como altos niveles de luz ultravioleta , radiación gamma , detergentes , desinfectantes , calor, congelación, presión y desecación . [92] En este estado latente, estos organismos pueden permanecer viables durante millones de años. [93] [94] [95] Las endosporas incluso permiten que las bacterias sobrevivan a la exposición al vacío y la radiación del espacio exterior , lo que lleva a la posibilidad de que las bacterias puedan distribuirse por todo el Universo mediante polvo espacial , meteoroides , asteroides , cometas , planetoides o panspermia dirigida . [96] [97]
Las bacterias formadoras de endosporas pueden causar enfermedades; por ejemplo, el ántrax se puede contraer por la inhalación de endosporas de Bacillus anthracis , y la contaminación de heridas punzantes profundas con endosporas de Clostridium tetani causa tétanos , que, como el botulismo , es causado por una toxina liberada por las bacterias que crecen a partir de las esporas. [98] La infección por Clostridioides difficile , un problema común en los entornos de atención médica, es causada por bacterias formadoras de esporas. [99]
Las bacterias exhiben una variedad extremadamente amplia de tipos metabólicos . [100] La distribución de rasgos metabólicos dentro de un grupo de bacterias se ha utilizado tradicionalmente para definir su taxonomía , pero estos rasgos a menudo no corresponden con las clasificaciones genéticas modernas. [101] El metabolismo bacteriano se clasifica en grupos nutricionales sobre la base de tres criterios principales: la fuente de energía , los donadores de electrones utilizados y la fuente de carbono utilizada para el crecimiento. [102]
Las bacterias fototróficas obtienen energía de la luz mediante la fotosíntesis , mientras que las bacterias quimiotróficas descomponen compuestos químicos mediante oxidación , [103] impulsando el metabolismo mediante la transferencia de electrones de un donante de electrones determinado a un aceptor terminal de electrones en una reacción redox . Los quimiotrofos se dividen además por los tipos de compuestos que utilizan para transferir electrones. Las bacterias que obtienen electrones de compuestos inorgánicos como el hidrógeno, el monóxido de carbono o el amoníaco se denominan litotrofos , mientras que las que utilizan compuestos orgánicos se denominan organotrofos . [103] Aún así, más específicamente, los organismos aeróbicos utilizan el oxígeno como aceptor terminal de electrones, mientras que los organismos anaeróbicos utilizan otros compuestos como el nitrato , el sulfato o el dióxido de carbono. [103]
Muchas bacterias, llamadas heterótrofas , obtienen su carbono de otro carbono orgánico . Otras, como las cianobacterias y algunas bacterias púrpuras , son autótrofas , lo que significa que obtienen carbono celular fijando dióxido de carbono . [104] En circunstancias inusuales, el gas metano puede ser utilizado por bacterias metanotróficas como fuente de electrones y como sustrato para el anabolismo del carbono . [105]
En muchos sentidos, el metabolismo bacteriano proporciona rasgos que son útiles para la estabilidad ecológica y para la sociedad humana. Por ejemplo, los diazótrofos tienen la capacidad de fijar el gas nitrógeno utilizando la enzima nitrogenasa . [106] Este rasgo, que se puede encontrar en bacterias de la mayoría de los tipos metabólicos enumerados anteriormente, [107] conduce a los procesos ecológicamente importantes de desnitrificación , reducción de sulfato y acetogénesis , respectivamente. [108] Los procesos metabólicos bacterianos son impulsores importantes en las respuestas biológicas a la contaminación ; por ejemplo, las bacterias reductoras de sulfato son en gran medida responsables de la producción de las formas altamente tóxicas de mercurio ( metil- y dimetilmercurio ) en el medio ambiente. [109] Los anaerobios no respiratorios utilizan la fermentación para generar energía y poder reductor, secretando subproductos metabólicos (como el etanol en la elaboración de cerveza) como desechos. Los anaerobios facultativos pueden cambiar entre la fermentación y diferentes aceptores terminales de electrones dependiendo de las condiciones ambientales en las que se encuentren. [110]


A diferencia de los organismos multicelulares, los aumentos en el tamaño celular ( crecimiento celular ) y la reproducción por división celular están estrechamente vinculados en los organismos unicelulares. Las bacterias crecen hasta un tamaño fijo y luego se reproducen a través de fisión binaria , una forma de reproducción asexual . [112] En condiciones óptimas, las bacterias pueden crecer y dividirse extremadamente rápido, y algunas poblaciones bacterianas pueden duplicarse tan rápido como cada 17 minutos. [113] En la división celular, se producen dos células hijas de clones idénticos. Algunas bacterias, mientras aún se reproducen asexualmente, forman estructuras reproductivas más complejas que ayudan a dispersar las células hijas recién formadas. Los ejemplos incluyen la formación del cuerpo fructífero por mixobacterias y la formación de hifas aéreas por especies de Streptomyces , o gemación. La gemación implica que una célula forme una protuberancia que se desprende y produce una célula hija. [114]
En el laboratorio, las bacterias se cultivan generalmente utilizando medios sólidos o líquidos. [115] Los medios de crecimiento sólidos , como las placas de agar , se utilizan para aislar cultivos puros de una cepa bacteriana. Sin embargo, los medios de crecimiento líquidos se utilizan cuando se requiere la medición del crecimiento o grandes volúmenes de células. El crecimiento en medios líquidos agitados se produce como una suspensión celular uniforme, lo que hace que los cultivos sean fáciles de dividir y transferir, aunque es difícil aislar bacterias individuales de los medios líquidos. El uso de medios selectivos (medios con nutrientes específicos añadidos o deficientes, o con antibióticos añadidos) puede ayudar a identificar organismos específicos. [116]
La mayoría de las técnicas de laboratorio para el cultivo de bacterias utilizan altos niveles de nutrientes para producir grandes cantidades de células de forma barata y rápida. [115] Sin embargo, en entornos naturales, los nutrientes son limitados, lo que significa que las bacterias no pueden seguir reproduciéndose indefinidamente. Esta limitación de nutrientes ha llevado a la evolución de diferentes estrategias de crecimiento (véase la teoría de selección r/K ). Algunos organismos pueden crecer extremadamente rápido cuando los nutrientes están disponibles, como la formación de floraciones de algas y cianobacterias que a menudo ocurren en lagos durante el verano. [117] Otros organismos tienen adaptaciones a entornos hostiles, como la producción de múltiples antibióticos por Streptomyces que inhiben el crecimiento de microorganismos competidores. [118] En la naturaleza, muchos organismos viven en comunidades (por ejemplo, biopelículas ) que pueden permitir un mayor suministro de nutrientes y protección contra el estrés ambiental. [52] Estas relaciones pueden ser esenciales para el crecimiento de un organismo o grupo de organismos en particular ( sintrofia ). [119]
El crecimiento bacteriano sigue cuatro fases. Cuando una población de bacterias ingresa por primera vez a un entorno con alto contenido de nutrientes que permite el crecimiento, las células necesitan adaptarse a su nuevo entorno. La primera fase de crecimiento es la fase de retraso , un período de crecimiento lento cuando las células se adaptan al entorno con alto contenido de nutrientes y se preparan para un crecimiento rápido. La fase de retraso tiene altas tasas de biosíntesis, ya que se producen las proteínas necesarias para un crecimiento rápido. [120] [121] La segunda fase de crecimiento es la fase logarítmica , también conocida como fase exponencial. La fase logarítmica está marcada por un crecimiento exponencial rápido . La velocidad a la que crecen las células durante esta fase se conoce como tasa de crecimiento ( k ), y el tiempo que tardan las células en duplicarse se conoce como tiempo de generación ( g ). Durante la fase logarítmica, los nutrientes se metabolizan a máxima velocidad hasta que uno de los nutrientes se agota y comienza a limitar el crecimiento. La tercera fase de crecimiento es la fase estacionaria y es causada por nutrientes agotados. Las células reducen su actividad metabólica y consumen proteínas celulares no esenciales. La fase estacionaria es una transición de un crecimiento rápido a un estado de respuesta al estrés y hay una mayor expresión de genes involucrados en la reparación del ADN , el metabolismo antioxidante y el transporte de nutrientes . [122] La fase final es la fase de muerte donde las bacterias se quedan sin nutrientes y mueren. [123]

La mayoría de las bacterias tienen un solo cromosoma circular que puede variar en tamaño desde solo 160.000 pares de bases en la bacteria endosimbiótica Carsonella ruddii , [125] a 12.200.000 pares de bases (12,2 Mbp) en la bacteria que habita en el suelo Sorangium cellulosum . [126] Hay muchas excepciones a esto; por ejemplo, algunas especies de Streptomyces y Borrelia contienen un solo cromosoma lineal, [127] [128] mientras que algunas especies de Vibrio contienen más de un cromosoma. [129] Algunas bacterias contienen plásmidos , pequeñas moléculas extracromosómicas de ADN que pueden contener genes para varias funciones útiles como resistencia a antibióticos , capacidades metabólicas o varios factores de virulencia . [130]
Los genomas bacterianos suelen codificar entre unos cientos y unos miles de genes. Los genes de los genomas bacterianos suelen ser una única extensión continua de ADN. Aunque existen varios tipos diferentes de intrones en las bacterias, estos son mucho más raros que en los eucariotas. [131]
Las bacterias, como organismos asexuales, heredan una copia idéntica del genoma de sus progenitores y son clonales . Sin embargo, todas las bacterias pueden evolucionar por selección a partir de cambios en su material genético (ADN) causados por recombinación genética o mutaciones . Las mutaciones surgen de errores cometidos durante la replicación del ADN o de la exposición a mutágenos . Las tasas de mutación varían ampliamente entre diferentes especies de bacterias e incluso entre diferentes clones de una misma especie de bacteria. [132] Los cambios genéticos en los genomas bacterianos surgen de una mutación aleatoria durante la replicación o de una "mutación dirigida por estrés", donde los genes involucrados en un proceso particular que limita el crecimiento tienen una mayor tasa de mutación. [133]
Algunas bacterias transfieren material genético entre células. Esto puede ocurrir de tres formas principales. Primero, las bacterias pueden absorber ADN exógeno de su entorno en un proceso llamado transformación . [134] Muchas bacterias pueden absorber naturalmente ADN del entorno, mientras que otras deben ser alteradas químicamente para inducirlas a absorber ADN. [135] El desarrollo de la competencia en la naturaleza generalmente se asocia con condiciones ambientales estresantes y parece ser una adaptación para facilitar la reparación del daño del ADN en las células receptoras. [136] En segundo lugar, los bacteriófagos pueden integrarse en el cromosoma bacteriano, introduciendo ADN extraño en un proceso conocido como transducción . Existen muchos tipos de bacteriófagos; algunos infectan y lisan a sus bacterias hospedadoras , mientras que otros se insertan en el cromosoma bacteriano. [ 137] Las bacterias resisten la infección por fagos a través de sistemas de modificación de restricción que degradan el ADN extraño [138] y un sistema que usa secuencias CRISPR para retener fragmentos de los genomas de fagos con los que las bacterias han estado en contacto en el pasado, lo que les permite bloquear la replicación del virus a través de una forma de interferencia de ARN . [139] [140] En tercer lugar, las bacterias pueden transferir material genético a través del contacto celular directo mediante conjugación . [141]
En circunstancias normales, la transducción, la conjugación y la transformación implican la transferencia de ADN entre bacterias individuales de la misma especie, pero ocasionalmente la transferencia puede ocurrir entre individuos de diferentes especies bacterianas, y esto puede tener consecuencias significativas, como la transferencia de resistencia a los antibióticos. [142] [143] En tales casos, la adquisición de genes de otras bacterias o del medio ambiente se denomina transferencia horizontal de genes y puede ser común en condiciones naturales. [144]

Muchas bacterias son móviles (capaces de moverse por sí mismas) y lo hacen utilizando una variedad de mecanismos. Los más estudiados de estos son los flagelos , filamentos largos que son girados por un motor en la base para generar un movimiento similar al de una hélice. [145] El flagelo bacteriano está formado por unas 20 proteínas, y se requieren aproximadamente otras 30 proteínas para su regulación y ensamblaje. [145] El flagelo es una estructura giratoria impulsada por un motor reversible en la base que utiliza el gradiente electroquímico a través de la membrana para obtener energía. [146]

Las bacterias pueden usar los flagelos de diferentes maneras para generar diferentes tipos de movimiento. Muchas bacterias (como E. coli ) tienen dos modos distintos de movimiento: movimiento hacia adelante (nadar) y volteretas. Las volteretas les permiten reorientarse y hacen de su movimiento un paseo aleatorio tridimensional . [147] Las especies bacterianas difieren en el número y disposición de los flagelos en su superficie; algunas tienen un solo flagelo ( monótricas ), un flagelo en cada extremo ( anfítricas ), grupos de flagelos en los polos de la célula ( lofótricas ), mientras que otras tienen flagelos distribuidos por toda la superficie de la célula ( perítricas ). Los flagelos de un grupo de bacterias, las espiroquetas , se encuentran entre dos membranas en el espacio periplásmico. Tienen un cuerpo helicoidal distintivo que se retuerce mientras se mueve. [145]
Otros dos tipos de movimiento bacteriano se denominan motilidad de espasmo , que se basa en una estructura llamada pilus tipo IV [148] , y motilidad de deslizamiento , que utiliza otros mecanismos. En la motilidad de espasmo, el pilus en forma de bastón se extiende desde la célula, se une a un sustrato y luego se retrae, tirando de la célula hacia adelante. [149]
Las bacterias móviles son atraídas o repelidas por ciertos estímulos en comportamientos llamados taxs : estos incluyen quimiotaxis , fototaxis , taxis energéticos y magnetotaxis . [150] [151] [152] En un grupo peculiar, las mixobacterias, las bacterias individuales se mueven juntas para formar ondas de células que luego se diferencian para formar cuerpos fructíferos que contienen esporas. [47] Las mixobacterias se mueven solo cuando están en superficies sólidas, a diferencia de E. coli , que es móvil en medios líquidos o sólidos. [153]
Varias especies de Listeria y Shigella se desplazan dentro de las células huésped usurpando el citoesqueleto , que normalmente se utiliza para mover orgánulos dentro de la célula. Al promover la polimerización de actina en un polo de sus células, pueden formar una especie de cola que las empuja a través del citoplasma de la célula huésped. [154]
Algunas bacterias tienen sistemas químicos que generan luz. Esta bioluminiscencia se da a menudo en bacterias que viven en asociación con peces, y la luz probablemente sirve para atraer a los peces u otros animales grandes. [155]
Las bacterias a menudo funcionan como agregados multicelulares conocidos como biopelículas , intercambiando una variedad de señales moleculares para la comunicación intercelular y participando en un comportamiento multicelular coordinado. [156] [157]
Los beneficios comunitarios de la cooperación multicelular incluyen una división celular del trabajo , el acceso a recursos que no pueden ser utilizados eficazmente por células individuales, la defensa colectiva contra antagonistas y la optimización de la supervivencia de la población mediante la diferenciación en distintos tipos de células. [156] Por ejemplo, las bacterias en biopelículas pueden tener una resistencia más de quinientas veces mayor a los agentes antibacterianos que las bacterias "planctónicas" individuales de la misma especie. [157]
Un tipo de comunicación intercelular mediante una señal molecular se denomina detección de quórum , que sirve para determinar si la densidad de población local es suficiente para sustentar la inversión en procesos que solo tienen éxito si un gran número de organismos similares se comportan de manera similar, como excretar enzimas digestivas o emitir luz. [158] [159] La detección de quórum permite a las bacterias coordinar la expresión genética y producir, liberar y detectar autoinductores o feromonas que se acumulan con el crecimiento de la población celular. [160]


La clasificación busca describir la diversidad de especies bacterianas nombrando y agrupando organismos en función de similitudes. Las bacterias se pueden clasificar en función de la estructura celular, el metabolismo celular o las diferencias en los componentes celulares, como el ADN , los ácidos grasos , los pigmentos, los antígenos y las quinonas . [116] Si bien estos esquemas permitieron la identificación y clasificación de cepas bacterianas, no estaba claro si estas diferencias representaban variación entre especies distintas o entre cepas de la misma especie. Esta incertidumbre se debió a la falta de estructuras distintivas en la mayoría de las bacterias, así como a la transferencia lateral de genes entre especies no relacionadas. [162] Debido a la transferencia lateral de genes, algunas bacterias estrechamente relacionadas pueden tener morfologías y metabolismos muy diferentes. Para superar esta incertidumbre, la clasificación bacteriana moderna enfatiza la sistemática molecular , utilizando técnicas genéticas como la determinación de la relación citosina- guanina , la hibridación genoma-genoma, así como la secuenciación de genes que no han sufrido una transferencia lateral extensa de genes, como el gen ARNr . [163] La clasificación de las bacterias se determina mediante la publicación en el International Journal of Systematic Bacteriology, [164] y el Bergey's Manual of Systematic Bacteriology. [165] El Comité Internacional de Bacteriología Sistemática (ICSB) mantiene reglas internacionales para la denominación de bacterias y categorías taxonómicas y para la clasificación de las mismas en el Código Internacional de Nomenclatura de Bacterias . [166]
Históricamente, las bacterias se consideraban parte de Plantae , el reino vegetal, y se las llamaba "Schizomycetes" (hongos de fisión). [167] Por esta razón, las bacterias colectivas y otros microorganismos en un huésped a menudo se denominan "flora". [168] El término "bacteria" se aplicaba tradicionalmente a todos los procariotas unicelulares microscópicos. Sin embargo, la sistemática molecular mostró que la vida procariota constaba de dos dominios separados , originalmente llamados Eubacteria y Archaebacteria, pero ahora llamados Bacteria y Archaea que evolucionaron independientemente de un ancestro común antiguo. [4] Las arqueas y los eucariotas están más estrechamente relacionados entre sí que cualquiera de ellos con las bacterias. Estos dos dominios, junto con Eukarya, son la base del sistema de tres dominios , que actualmente es el sistema de clasificación más utilizado en microbiología. [169] Sin embargo, debido a la introducción relativamente reciente de la sistemática molecular y un rápido aumento en el número de secuencias de genoma disponibles, la clasificación bacteriana sigue siendo un campo cambiante y en expansión. [170] [171] Por ejemplo, Cavalier-Smith argumentó que las arqueas y los eucariotas evolucionaron a partir de bacterias grampositivas. [172]
La identificación de bacterias en el laboratorio es particularmente relevante en medicina , donde el tratamiento correcto está determinado por la especie bacteriana que causa una infección. En consecuencia, la necesidad de identificar patógenos humanos fue un impulso importante para el desarrollo de técnicas para identificar bacterias. [173]
La tinción de Gram , desarrollada en 1884 por Hans Christian Gram , caracteriza a las bacterias basándose en las características estructurales de sus paredes celulares. [174] [74] Las capas gruesas de peptidoglicano en la pared celular "Gram-positiva" se tiñen de púrpura, mientras que la pared celular "Gram-negativa" delgada aparece rosa. [174] Al combinar la morfología y la tinción de Gram, la mayoría de las bacterias pueden clasificarse como pertenecientes a uno de los cuatro grupos (cocos Gram-positivos, bacilos Gram-positivos, cocos Gram-negativos y bacilos Gram-negativos). Algunos organismos se identifican mejor mediante tinciones distintas a la tinción de Gram, en particular las micobacterias o Nocardia , que muestran resistencia a los ácidos en tinciones de Ziehl–Neelsen o similares. [175] Otros organismos pueden necesitar ser identificados por su crecimiento en medios especiales, o por otras técnicas, como la serología . [176]
Las técnicas de cultivo están diseñadas para promover el crecimiento e identificar bacterias particulares mientras se restringe el crecimiento de las otras bacterias en la muestra. [177] A menudo, estas técnicas están diseñadas para muestras específicas; por ejemplo, una muestra de esputo se tratará para identificar organismos que causan neumonía , mientras que las muestras de heces se cultivan en medios selectivos para identificar organismos que causan diarrea mientras se previene el crecimiento de bacterias no patógenas. Las muestras que normalmente son estériles, como sangre , orina o líquido cefalorraquídeo , se cultivan en condiciones diseñadas para cultivar todos los organismos posibles. [116] [178] Una vez que se ha aislado un organismo patógeno, se puede caracterizar aún más por su morfología, patrones de crecimiento (como crecimiento aeróbico o anaeróbico ), patrones de hemólisis y tinción. [179]
Al igual que con la clasificación bacteriana, la identificación de bacterias utiliza cada vez más métodos moleculares, [180] y espectroscopia de masas . [181] La mayoría de las bacterias no han sido caracterizadas y hay muchas especies que no se pueden cultivar en el laboratorio. [182] Los diagnósticos que utilizan herramientas basadas en ADN, como la reacción en cadena de la polimerasa , son cada vez más populares debido a su especificidad y velocidad, en comparación con los métodos basados en cultivos. [183] Estos métodos también permiten la detección e identificación de células " viables pero no cultivables " que son metabólicamente activas pero que no se dividen. [184] Sin embargo, incluso utilizando estos métodos mejorados, el número total de especies bacterianas no se conoce y ni siquiera se puede estimar con certeza. Siguiendo la clasificación actual, hay un poco menos de 9.300 especies conocidas de procariotas, que incluyen bacterias y arqueas; [185] pero los intentos de estimar el número real de diversidad bacteriana han variado de 10 7 a 10 9 especies totales, e incluso estas estimaciones diversas pueden estar erradas en muchos órdenes de magnitud. [186] [187]
Los siguientes filos han sido publicados válidamente según el Código Bacteriológico : [188]
A pesar de su aparente simplicidad, las bacterias pueden formar asociaciones complejas con otros organismos. Estas asociaciones simbióticas pueden dividirse en parasitismo , mutualismo y comensalismo . [190]
La palabra " comensalismo " se deriva de la palabra "comensal", que significa "comer en la misma mesa" [191] y todas las plantas y animales están colonizados por bacterias comensales. En los seres humanos y otros animales, millones de ellas viven en la piel, las vías respiratorias, el intestino y otros orificios. [192] [193] Conocidas como "flora normal", [194] o "comensales", [195] estas bacterias normalmente no causan daño, pero ocasionalmente pueden invadir otros sitios del cuerpo y causar infecciones. Escherichia coli es un comensal en el intestino humano, pero puede causar infecciones del tracto urinario. [196] De manera similar, los estreptococos, que son parte de la flora normal de la boca humana, pueden causar enfermedades cardíacas . [197]
Algunas especies de bacterias matan y luego consumen otros microorganismos; estas especies se denominan bacterias depredadoras . [198] Entre ellas se incluyen organismos como Myxococcus xanthus , que forma enjambres de células que matan y digieren cualquier bacteria que encuentran. [199] Otros depredadores bacterianos se adhieren a sus presas para digerirlas y absorber nutrientes o invaden otra célula y se multiplican dentro del citosol. [200] Se cree que estas bacterias depredadoras evolucionaron a partir de saprófagos que consumían microorganismos muertos, a través de adaptaciones que les permitieron atrapar y matar a otros organismos. [201]
Ciertas bacterias forman asociaciones espaciales estrechas que son esenciales para su supervivencia. Una de estas asociaciones mutualistas, llamada transferencia de hidrógeno entre especies, ocurre entre grupos de bacterias anaeróbicas que consumen ácidos orgánicos , como el ácido butírico o el ácido propiónico , y producen hidrógeno , y arqueas metanogénicas que consumen hidrógeno. [202] Las bacterias en esta asociación son incapaces de consumir los ácidos orgánicos ya que esta reacción produce hidrógeno que se acumula en su entorno. Solo la asociación íntima con las arqueas que consumen hidrógeno mantiene la concentración de hidrógeno lo suficientemente baja como para permitir que las bacterias crezcan. [203]
En el suelo, los microorganismos que residen en la rizosfera (una zona que incluye la superficie de la raíz y el suelo que se adhiere a la raíz después de una suave agitación) llevan a cabo la fijación de nitrógeno , convirtiendo el gas nitrógeno en compuestos nitrogenados. [204] Esto sirve para proporcionar una forma de nitrógeno fácilmente absorbible para muchas plantas, que no pueden fijar el nitrógeno por sí mismas. Muchas otras bacterias se encuentran como simbiontes en humanos y otros organismos. Por ejemplo, la presencia de más de 1.000 especies bacterianas en la flora intestinal humana normal de los intestinos puede contribuir a la inmunidad intestinal, sintetizar vitaminas , como el ácido fólico , la vitamina K y la biotina , convertir azúcares en ácido láctico (ver Lactobacillus ), así como fermentar carbohidratos complejos no digeribles . [205] [206] [207] La presencia de esta flora intestinal también inhibe el crecimiento de bacterias potencialmente patógenas (generalmente a través de la exclusión competitiva ) y estas bacterias beneficiosas se venden en consecuencia como suplementos dietéticos probióticos . [208]
Casi toda la vida animal depende de las bacterias para sobrevivir, ya que solo las bacterias y algunas arqueas poseen los genes y las enzimas necesarias para sintetizar vitamina B 12 , también conocida como cobalamina , y proporcionarla a través de la cadena alimentaria. La vitamina B 12 es una vitamina soluble en agua que participa en el metabolismo de cada célula del cuerpo humano. Es un cofactor en la síntesis de ADN y en el metabolismo de los ácidos grasos y aminoácidos . Es particularmente importante en el funcionamiento normal del sistema nervioso a través de su papel en la síntesis de mielina . [209]


El cuerpo está continuamente expuesto a muchas especies de bacterias, incluyendo comensales benéficos, que crecen en la piel y las mucosas , y saprofitos , que crecen principalmente en el suelo y en materia en descomposición . La sangre y los fluidos tisulares contienen nutrientes suficientes para sostener el crecimiento de muchas bacterias. El cuerpo tiene mecanismos de defensa que le permiten resistir la invasión microbiana de sus tejidos y le dan una inmunidad natural o resistencia innata contra muchos microorganismos . [210] A diferencia de algunos virus , las bacterias evolucionan relativamente lentamente por lo que muchas enfermedades bacterianas también ocurren en otros animales. [211]
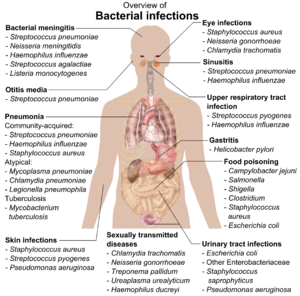
Si las bacterias forman una asociación parasitaria con otros organismos, se clasifican como patógenos. [212] Las bacterias patógenas son una de las principales causas de muerte y enfermedad humana y causan infecciones como el tétanos (causado por Clostridium tetani ), fiebre tifoidea , difteria , sífilis , cólera , enfermedades transmitidas por alimentos , lepra (causada por Mycobacterium leprae ) y tuberculosis (causada por Mycobacterium tuberculosis ). [213] Una causa patógena para una enfermedad médica conocida solo puede descubrirse muchos años después, como fue el caso de Helicobacter pylori y la enfermedad de úlcera péptica . [214] Las enfermedades bacterianas también son importantes en la agricultura , y las bacterias causan manchas en las hojas , fuego bacteriano y marchitez en las plantas, así como enfermedad de Johne , mastitis , salmonela y ántrax en animales de granja. [215]

Cada especie de patógeno tiene un espectro característico de interacciones con sus huéspedes humanos . Algunos organismos, como Staphylococcus o Streptococcus , pueden causar infecciones de la piel, neumonía , meningitis y sepsis , una respuesta inflamatoria sistémica que produce shock , vasodilatación masiva y muerte. [216] Sin embargo, estos organismos también son parte de la flora humana normal y generalmente existen en la piel o en la nariz sin causar ninguna enfermedad. Otros organismos invariablemente causan enfermedades en humanos, como Rickettsia , que son parásitos intracelulares obligados capaces de crecer y reproducirse solo dentro de las células de otros organismos. Una especie de Rickettsia causa tifus , mientras que otra causa fiebre maculosa de las Montañas Rocosas . Chlamydia , otro filo de parásitos intracelulares obligados, contiene especies que pueden causar neumonía o infección del tracto urinario y pueden estar involucradas en la enfermedad cardíaca coronaria . [217] Algunas especies, como Pseudomonas aeruginosa , Burkholderia cenocepacia y Mycobacterium avium , son patógenos oportunistas y causan enfermedades principalmente en personas inmunodeprimidas o con fibrosis quística . [218] [219] Algunas bacterias producen toxinas , que causan enfermedades. [220] Estas son endotoxinas , que provienen de células bacterianas rotas, y exotoxinas , que son producidas por bacterias y liberadas al medio ambiente. [221] La bacteria Clostridium botulinum , por ejemplo, produce una potente exotoxina que causa parálisis respiratoria, y Salmonellae produce una endotoxina que causa gastroenteritis. [221] Algunas exotoxinas se pueden convertir en toxoides , que se utilizan como vacunas para prevenir la enfermedad. [222]
Las infecciones bacterianas pueden tratarse con antibióticos , que se clasifican como bactericidas si matan las bacterias o bacteriostáticos si solo previenen el crecimiento bacteriano. Hay muchos tipos de antibióticos, y cada clase inhibe un proceso que es diferente en el patógeno del que se encuentra en el huésped. Un ejemplo de cómo los antibióticos producen toxicidad selectiva son el cloranfenicol y la puromicina , que inhiben el ribosoma bacteriano , pero no el ribosoma eucariota estructuralmente diferente. [223] Los antibióticos se utilizan tanto en el tratamiento de enfermedades humanas como en la agricultura intensiva para promover el crecimiento animal, donde pueden estar contribuyendo al rápido desarrollo de resistencia a los antibióticos en las poblaciones bacterianas. [224] Las infecciones se pueden prevenir con medidas antisépticas , como esterilizar la piel antes de perforarla con la aguja de una jeringa, y con el cuidado adecuado de los catéteres permanentes. Los instrumentos quirúrgicos y dentales también se esterilizan para prevenir la contaminación por bacterias. Los desinfectantes como la lejía se utilizan para matar bacterias u otros patógenos en las superficies para prevenir la contaminación y reducir aún más el riesgo de infección. [225]
Las bacterias, a menudo bacterias de ácido láctico , como las especies de Lactobacillus y Lactococcus , en combinación con levaduras y mohos , se han utilizado durante miles de años en la preparación de alimentos fermentados , como queso , encurtidos , salsa de soja , chucrut , vinagre , vino y yogur . [226] [227]
La capacidad de las bacterias para degradar una variedad de compuestos orgánicos es notable y se ha utilizado en el procesamiento de desechos y la biorremediación . Las bacterias capaces de digerir los hidrocarburos del petróleo se utilizan a menudo para limpiar derrames de petróleo . [228] Se agregó fertilizante a algunas de las playas de Prince William Sound en un intento de promover el crecimiento de estas bacterias naturales después del derrame de petróleo del Exxon Valdez en 1989. Estos esfuerzos fueron efectivos en playas que no estaban demasiado cubiertas de petróleo. Las bacterias también se utilizan para la biorremediación de desechos tóxicos industriales . [229] En la industria química , las bacterias son más importantes en la producción de productos químicos enantioméricamente puros para su uso como productos farmacéuticos o agroquímicos . [230]
Las bacterias también se pueden utilizar en lugar de pesticidas en el control biológico de plagas . Esto implica comúnmente Bacillus thuringiensis (también llamado BT), una bacteria Gram-positiva que habita en el suelo. Las subespecies de esta bacteria se utilizan como insecticidas específicos para lepidópteros bajo nombres comerciales como Dipel y Thuricide. [231] Debido a su especificidad, estos pesticidas se consideran respetuosos con el medio ambiente , con poco o ningún efecto sobre los humanos, la vida silvestre , los polinizadores y la mayoría de los demás insectos beneficiosos . [232] [233]
Debido a su capacidad de crecer rápidamente y la relativa facilidad con la que pueden ser manipuladas, las bacterias son los caballos de batalla para los campos de la biología molecular , la genética y la bioquímica . Al realizar mutaciones en el ADN bacteriano y examinar los fenotipos resultantes, los científicos pueden determinar la función de los genes, las enzimas y las vías metabólicas en las bacterias, y luego aplicar este conocimiento a organismos más complejos. [234] Este objetivo de comprender la bioquímica de una célula alcanza su expresión más compleja en la síntesis de enormes cantidades de datos cinéticos de enzimas y de expresión genética en modelos matemáticos de organismos completos. Esto se puede lograr en algunas bacterias bien estudiadas, y ahora se están produciendo y probando modelos del metabolismo de Escherichia coli . [235] [236] Esta comprensión del metabolismo y la genética bacteriana permite el uso de la biotecnología para bioingeniería de bacterias para la producción de proteínas terapéuticas, como insulina , factores de crecimiento o anticuerpos . [237] [238]
Debido a su importancia para la investigación en general, las muestras de cepas bacterianas se aíslan y se conservan en Centros de Recursos Biológicos . Esto garantiza la disponibilidad de la cepa para los científicos de todo el mundo. [239]

Las bacterias fueron observadas por primera vez por el microscopista holandés Antonie van Leeuwenhoek en 1676, utilizando un microscopio de lente única de su propio diseño. Luego publicó sus observaciones en una serie de cartas a la Royal Society de Londres . [240] Las bacterias fueron el descubrimiento microscópico más notable de Leeuwenhoek. Su tamaño estaba justo en el límite de lo que sus lentes simples podían resolver y, en uno de los paréntesis más sorprendentes en la historia de la ciencia, nadie más las volvería a ver durante más de un siglo. [241] Sus observaciones también incluyeron protozoos a los que llamó animálculos , y sus hallazgos fueron analizados nuevamente a la luz de los hallazgos más recientes de la teoría celular . [242]
Christian Gottfried Ehrenberg introdujo la palabra "bacteria" en 1828. [243] De hecho, su Bacterium era un género que contenía bacterias con forma de bastón que no formaban esporas, [244] a diferencia de Bacillus , un género de bacterias con forma de bastón que formaban esporas definido por Ehrenberg en 1835. [245]
En 1859, Louis Pasteur demostró que el crecimiento de microorganismos causa el proceso de fermentación y que este crecimiento no se debe a la generación espontánea ( las levaduras y los mohos , comúnmente asociados con la fermentación, no son bacterias, sino hongos ). Junto con su contemporáneo Robert Koch , Pasteur fue uno de los primeros defensores de la teoría de los gérmenes de la enfermedad . [246] Antes de ellos, Ignaz Semmelweis y Joseph Lister se habían dado cuenta de la importancia de las manos desinfectadas en el trabajo médico. Semmelweis, quien en la década de 1840 formuló sus reglas para el lavado de manos en el hospital, antes del advenimiento de la teoría de los gérmenes, atribuyó la enfermedad a la "materia orgánica animal en descomposición". Sus ideas fueron rechazadas y su libro sobre el tema condenado por la comunidad médica. Sin embargo, después de Lister, los médicos comenzaron a desinfectarse las manos en la década de 1870. [247]
Robert Koch, pionero de la microbiología médica, trabajó en el cólera , el ántrax y la tuberculosis . En su investigación sobre la tuberculosis, Koch finalmente demostró la teoría de los gérmenes, por la que recibió un Premio Nobel en 1905. [248] En los postulados de Koch , estableció criterios para comprobar si un organismo es la causa de una enfermedad , y estos postulados todavía se utilizan en la actualidad. [249]
Se dice que Ferdinand Cohn es el fundador de la bacteriología y estudió las bacterias desde 1870. Cohn fue el primero en clasificar las bacterias según su morfología. [250] [251]
Aunque en el siglo XIX se sabía que las bacterias son la causa de muchas enfermedades, no había tratamientos antibacterianos eficaces disponibles. [252] En 1910, Paul Ehrlich desarrolló el primer antibiótico, al cambiar los colorantes que teñían selectivamente a Treponema pallidum (la espiroqueta que causa la sífilis ) por compuestos que mataban selectivamente al patógeno. [253] Ehrlich, que había recibido el Premio Nobel en 1908 por su trabajo en inmunología , fue pionero en el uso de colorantes para detectar e identificar bacterias, y su trabajo fue la base de la tinción de Gram y la tinción de Ziehl-Neelsen . [254]
Un gran paso adelante en el estudio de las bacterias se produjo en 1977 cuando Carl Woese reconoció que las arqueas tienen una línea de descendencia evolutiva separada de las bacterias. [255] Esta nueva taxonomía filogenética dependía de la secuenciación del ARN ribosómico 16S y dividía a los procariotas en dos dominios evolutivos, como parte del sistema de tres dominios . [4]